+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7aeb | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
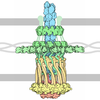
| タイトル | Cryo-EM structure of an extracellular contractile injection system in marine bacterium Algoriphagus machipongonensis, the baseplate complex in extended state applied 6-fold symmetry. | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード | STRUCTURAL PROTEIN / extracellular contractile injection system | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||||||||
| 生物種 |  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.7 Å | ||||||||||||
 データ登録者 データ登録者 | Xu, J. / Ericson, C. / Feldmueller, M. / Lien, Y.W. / Pilhofer, M. | ||||||||||||
| 資金援助 |  スイス, 3件 スイス, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Microbiol / 年: 2022 ジャーナル: Nat Microbiol / 年: 2022タイトル: Identification and structure of an extracellular contractile injection system from the marine bacterium Algoriphagus machipongonensis. 著者: Jingwei Xu / Charles F Ericson / Yun-Wei Lien / Florentine U N Rutaganira / Fabian Eisenstein / Miki Feldmüller / Nicole King / Martin Pilhofer /    要旨: Contractile injection systems (CISs) are phage tail-like nanomachines, mediating bacterial cell-cell interactions as either type VI secretion systems (T6SSs) or extracellular CISs (eCISs). ...Contractile injection systems (CISs) are phage tail-like nanomachines, mediating bacterial cell-cell interactions as either type VI secretion systems (T6SSs) or extracellular CISs (eCISs). Bioinformatic studies uncovered a phylogenetic group of hundreds of putative CIS gene clusters that are highly diverse and widespread; however, only four systems have been characterized. Here we studied a putative CIS gene cluster in the marine bacterium Algoriphagus machipongonensis. Using an integrative approach, we show that the system is compatible with an eCIS mode of action. Our cryo-electron microscopy structure revealed several features that differ from those seen in other CISs: a 'cap adaptor' located at the distal end, a 'plug' exposed to the tube lumen, and a 'cage' formed by massive extensions of the baseplate. These elements are conserved in other CISs, and our genetic tools identified that they are required for assembly, cargo loading and function. Furthermore, our atomic model highlights specific evolutionary hotspots and will serve as a framework for understanding and re-engineering CISs. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7aeb.cif.gz 7aeb.cif.gz | 2.8 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7aeb.ent.gz pdb7aeb.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7aeb.json.gz 7aeb.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7aeb_validation.pdf.gz 7aeb_validation.pdf.gz | 1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7aeb_full_validation.pdf.gz 7aeb_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  7aeb_validation.xml.gz 7aeb_validation.xml.gz | 350.8 KB | 表示 | |
| CIF形式データ |  7aeb_validation.cif.gz 7aeb_validation.cif.gz | 576 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ae/7aeb https://data.pdbj.org/pub/pdb/validation_reports/ae/7aeb ftp://data.pdbj.org/pub/pdb/validation_reports/ae/7aeb ftp://data.pdbj.org/pub/pdb/validation_reports/ae/7aeb | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 7種, 42分子 ABCDEFGHIJKLMNOPQRSTUVWXYZabcd...
| #1: タンパク質 | 分子量: 107770.953 Da / 分子数: 6 / 由来タイプ: 天然 詳細: the residues (552-end) could not be built up due to the poor map density. 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTB3 #2: タンパク質 | 分子量: 119379.320 Da / 分子数: 6 / 由来タイプ: 天然 詳細: The C terminal part (residues 916-1012aa) is built up by poly-alanine chain due to the poor map density. 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTB4 #3: タンパク質 | 分子量: 26571.104 Da / 分子数: 6 / 由来タイプ: 天然 詳細: The residue S169 is not found in relative map, which might be cleaved in the structure. 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTB8 #4: タンパク質 | 分子量: 15762.021 Da / 分子数: 6 / 由来タイプ: 天然 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTB5 #5: タンパク質 | 分子量: 17063.238 Da / 分子数: 6 / 由来タイプ: 天然 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTC0 #6: タンパク質 | 分子量: 76319.039 Da / 分子数: 6 / 由来タイプ: 天然 詳細: the residues 288-320aa could not be built up in the model, with residues 430-446aa assigned with poly-alanine chain. 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTC2 #7: タンパク質 | 分子量: 16375.458 Da / 分子数: 6 / 由来タイプ: 天然 由来: (天然)  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア)参照: UniProt: A3HTC1 |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: The baseplate complex of an extracellular contractile injection system in marine bacterium Algoriphagus machipongonensis, applied 6-fold symmetry. タイプ: COMPLEX / Entity ID: all / 由来: NATURAL |
|---|---|
| 由来(天然) | 生物種:  Algoriphagus machipongonensis (バクテリア) Algoriphagus machipongonensis (バクテリア) |
| 緩衝液 | pH: 8 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 60 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) |
- 解析
解析
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
|---|---|
| 3次元再構成 | 解像度: 2.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 82969 / 対称性のタイプ: POINT |
| 原子モデル構築 | プロトコル: AB INITIO MODEL / 空間: REAL |
 ムービー
ムービー コントローラー
コントローラー
































 PDBj
PDBj