+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5oik | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
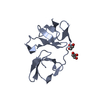
| タイトル | Structure of an RNA polymerase II-DSIF transcription elongation complex | ||||||||||||
 要素 要素 |
| ||||||||||||
 キーワード キーワード | TRANSCRIPTION / RNA polymerase II / transcription elongation | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Formation of RNA Pol II elongation complex / Formation of the Early Elongation Complex / Transcriptional regulation by small RNAs / FGFR2 alternative splicing / RNA polymerase II transcribes snRNA genes / mRNA Capping / mRNA Splicing - Minor Pathway / RNA Polymerase I Transcription Initiation / RNA Polymerase I Promoter Escape / RNA Polymerase II Promoter Escape ...Formation of RNA Pol II elongation complex / Formation of the Early Elongation Complex / Transcriptional regulation by small RNAs / FGFR2 alternative splicing / RNA polymerase II transcribes snRNA genes / mRNA Capping / mRNA Splicing - Minor Pathway / RNA Polymerase I Transcription Initiation / RNA Polymerase I Promoter Escape / RNA Polymerase II Promoter Escape / RNA Polymerase II Transcription Pre-Initiation And Promoter Opening / RNA Polymerase I Transcription Termination / RNA Polymerase II Transcription Initiation / RNA Polymerase II Transcription Initiation And Promoter Clearance / RNA Polymerase III Transcription Initiation From Type 1 Promoter / RNA Polymerase III Transcription Initiation From Type 2 Promoter / RNA Polymerase III Transcription Initiation From Type 3 Promoter / RNA Pol II CTD phosphorylation and interaction with CE / Estrogen-dependent gene expression / RNA Polymerase II Pre-transcription Events / TP53 Regulates Transcription of DNA Repair Genes / RNA Polymerase II Transcription Elongation / Processing of Capped Intron-Containing Pre-mRNA / B-WICH complex positively regulates rRNA expression / mRNA Splicing - Major Pathway / Formation of TC-NER Pre-Incision Complex / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / negative regulation of DNA-templated transcription, elongation / DNA/RNA hybrid binding / DSIF complex / regulation of transcription elongation by RNA polymerase II / positive regulation of DNA-templated transcription, elongation / Abortive elongation of HIV-1 transcript in the absence of Tat / transcription elongation-coupled chromatin remodeling / RNA Pol II CTD phosphorylation and interaction with CE during HIV infection / RNA Pol II CTD phosphorylation and interaction with CE / Formation of the Early Elongation Complex / Formation of the HIV-1 Early Elongation Complex / mRNA Capping / maintenance of transcriptional fidelity during transcription elongation by RNA polymerase II / RNA polymerase II complex binding / negative regulation of transcription elongation by RNA polymerase II / transcription by RNA polymerase I / Pausing and recovery of Tat-mediated HIV elongation / Tat-mediated HIV elongation arrest and recovery / positive regulation of nuclear-transcribed mRNA poly(A) tail shortening / transcription by RNA polymerase III / HIV elongation arrest and recovery / Pausing and recovery of HIV elongation / RNA polymerase II transcribes snRNA genes / positive regulation of macroautophagy / nuclear-transcribed mRNA catabolic process / RNA polymerase II activity / Tat-mediated elongation of the HIV-1 transcript / transcription elongation by RNA polymerase I / transcription-coupled nucleotide-excision repair / tRNA transcription by RNA polymerase III / Formation of HIV-1 elongation complex containing HIV-1 Tat / RNA polymerase I complex / RNA polymerase III complex / positive regulation of translational initiation / Formation of HIV elongation complex in the absence of HIV Tat / RNA polymerase II, core complex / RNA Polymerase II Transcription Elongation / core promoter sequence-specific DNA binding / Formation of RNA Pol II elongation complex / RNA Polymerase II Pre-transcription Events / translation initiation factor binding / protein-DNA complex / TP53 Regulates Transcription of DNA Repair Genes / transcription initiation at RNA polymerase II promoter / transcription elongation by RNA polymerase II / P-body / euchromatin / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / single-stranded DNA binding / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エキソリボヌクレアーゼ / transcription by RNA polymerase II / nucleic acid binding / chromosome, telomeric region / single-stranded RNA binding / protein dimerization activity / hydrolase activity / protein heterodimerization activity / RNA-directed RNA polymerase / RNA-dependent RNA polymerase activity / mRNA binding / nucleotide binding / chromatin binding / regulation of DNA-templated transcription / nucleolus / negative regulation of transcription by RNA polymerase II / enzyme binding / magnesium ion binding / positive regulation of transcription by RNA polymerase II / DNA binding / RNA binding 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) synthetic construct (人工物) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.7 Å | ||||||||||||
 データ登録者 データ登録者 | Bernecky, C. / Plitzko, J.M. / Cramer, P. | ||||||||||||
| 資金援助 |  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2017 ジャーナル: Nat Struct Mol Biol / 年: 2017タイトル: Structure of a transcribing RNA polymerase II-DSIF complex reveals a multidentate DNA-RNA clamp. 著者: Carrie Bernecky / Jürgen M Plitzko / Patrick Cramer /  要旨: During transcription, RNA polymerase II (Pol II) associates with the conserved elongation factor DSIF. DSIF renders the elongation complex stable and functions during Pol II pausing and RNA ...During transcription, RNA polymerase II (Pol II) associates with the conserved elongation factor DSIF. DSIF renders the elongation complex stable and functions during Pol II pausing and RNA processing. We combined cryo-EM and X-ray crystallography to determine the structure of the mammalian Pol II-DSIF elongation complex at a nominal resolution of 3.4 Å. Human DSIF has a modular structure with two domains forming a DNA clamp, two domains forming an RNA clamp, and one domain buttressing the RNA clamp. The clamps maintain the transcription bubble, position upstream DNA, and retain the RNA transcript in the exit tunnel. The mobile C-terminal region of DSIF is located near exiting RNA, where it can recruit factors for RNA processing. The structure provides insight into the roles of DSIF during mRNA synthesis. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5oik.cif.gz 5oik.cif.gz | 899.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5oik.ent.gz pdb5oik.ent.gz | 711.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5oik.json.gz 5oik.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  5oik_validation.pdf.gz 5oik_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  5oik_full_validation.pdf.gz 5oik_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  5oik_validation.xml.gz 5oik_validation.xml.gz | 126.2 KB | 表示 | |
| CIF形式データ |  5oik_validation.cif.gz 5oik_validation.cif.gz | 197.8 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/oi/5oik https://data.pdbj.org/pub/pdb/validation_reports/oi/5oik ftp://data.pdbj.org/pub/pdb/validation_reports/oi/5oik ftp://data.pdbj.org/pub/pdb/validation_reports/oi/5oik | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-DNA-directed RNA polymerase II subunit ... , 5種, 5分子 ACGIK
| #1: タンパク質 | 分子量: 217436.062 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #3: タンパク質 | 分子量: 31466.098 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #7: タンパク質 | 分子量: 19314.283 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #9: タンパク質 | 分子量: 14507.205 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #11: タンパク質 | 分子量: 13310.284 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-タンパク質 , 3種, 3分子 BDH
| #2: タンパク質 | 分子量: 134041.422 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #4: タンパク質 | 分子量: 16347.255 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #8: タンパク質 | 分子量: 17162.273 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-DNA-directed RNA polymerases I, II, and III subunit ... , 4種, 4分子 EFJL
| #5: タンパク質 | 分子量: 24514.219 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #6: タンパク質 | 分子量: 14491.026 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #10: タンパク質 | 分子量: 7655.123 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #12: タンパク質 | 分子量: 7018.244 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-DNA鎖 , 2種, 2分子 NT
| #13: DNA鎖 | 分子量: 13303.563 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|---|
| #15: DNA鎖 | 分子量: 13178.483 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-RNA鎖 , 1種, 1分子 P
| #14: RNA鎖 | 分子量: 16081.696 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|
-Transcription elongation factor ... , 2種, 2分子 YZ
| #16: タンパク質 | 分子量: 13210.201 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SUPT4H1, SPT4H, SUPT4H / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SUPT4H1, SPT4H, SUPT4H / 発現宿主:  |
|---|---|
| #17: タンパク質 | 分子量: 121145.477 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SUPT5H, SPT5, SPT5H / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SUPT5H, SPT5, SPT5H / 発現宿主:  |
-非ポリマー , 2種, 9分子 


| #18: 化合物 | ChemComp-ZN / #19: 化合物 | ChemComp-MG / | |
|---|
-詳細
| 構成要素の詳細 | In order to illustrate the path of the nontemplate DNA, phosphate atoms (chain N residues 15-23) ...In order to illustrate the path of the nontemplate DNA, phosphate atoms (chain N residues 15-23) were placed in the center of the observed DNA density. |
|---|---|
| 配列の詳細 | Chain A , corresponds to NCBI entry NP_001193242.1 |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 |
| ||||||||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||||||||
| 緩衝液 | pH: 7.25 / 詳細: pH was adjusted at 25 degrees Celsius | ||||||||||||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||||||||||||
| 試料 | 濃度: 0.25 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 200 divisions/in. / グリッドのタイプ: Quantifoil R2/1 | ||||||||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K 詳細: Sample (four microliters) was applied to glow-discharged Quantifoil R 2/1 holey carbon grids, which were then blotted for 8.5s and plunge-frozen in liquid ethane. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 37000 X / 倍率(補正後): 37037 X / 最大 デフォーカス(公称値): 3600 nm / 最小 デフォーカス(公称値): 600 nm / Calibrated defocus min: 600 nm / 最大 デフォーカス(補正後): 3600 nm / Cs: 2.7 mm / C2レンズ絞り径: 70 µm |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 9.9 sec. / 電子線照射量: 33 e/Å2 / 検出モード: SUPER-RESOLUTION フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 撮影したグリッド数: 1 / 実像数: 2549 詳細: Movies were aligned and binned to the physical pixel size of 1.35 angstroms. |
| 電子光学装置 | エネルギーフィルター名称: GIF Quantum / エネルギーフィルター 上限: 20 eV / エネルギーフィルター 下限: 0 eV |
| 画像スキャン | 動画フレーム数/画像: 33 / 利用したフレーム数/画像: 1-33 |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.10_2155: / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 687928 | ||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 101140 / アルゴリズム: FOURIER SPACE / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | 空間: REAL | ||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj





































































