[日本語] English
 万見
万見- EMDB-32299: Cryo-EM structure of the gastric proton pump complexed with revaprazan -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-32299 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the gastric proton pump complexed with revaprazan | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報H+/K+-exchanging ATPase / potassium:proton exchanging ATPase complex / P-type potassium:proton transporter activity / Ion transport by P-type ATPases / P-type sodium:potassium-exchanging transporter activity / sodium:potassium-exchanging ATPase complex / sodium ion export across plasma membrane / intracellular potassium ion homeostasis / intracellular sodium ion homeostasis / potassium ion import across plasma membrane ...H+/K+-exchanging ATPase / potassium:proton exchanging ATPase complex / P-type potassium:proton transporter activity / Ion transport by P-type ATPases / P-type sodium:potassium-exchanging transporter activity / sodium:potassium-exchanging ATPase complex / sodium ion export across plasma membrane / intracellular potassium ion homeostasis / intracellular sodium ion homeostasis / potassium ion import across plasma membrane / potassium ion binding / ATPase activator activity / potassium ion transmembrane transport / proton transmembrane transport / cell adhesion / apical plasma membrane / magnesium ion binding / ATP hydrolysis activity / ATP binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
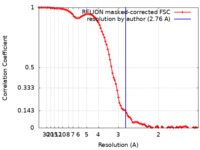
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.76 Å | |||||||||
 データ登録者 データ登録者 | Abe K / Tanaka S / Morita M / Yamagishi T | |||||||||
| 資金援助 |  日本, 1件 日本, 1件
| |||||||||
 引用 引用 |  ジャーナル: J Med Chem / 年: 2022 ジャーナル: J Med Chem / 年: 2022タイトル: Structural Basis for Binding of Potassium-Competitive Acid Blockers to the Gastric Proton Pump. 著者: Saki Tanaka / Mikio Morita / Tatsuya Yamagishi / Hridya Valia Madapally / Kenichi Hayashida / Himanshu Khandelia / Christoph Gerle / Hideki Shigematsu / Atsunori Oshima / Kazuhiro Abe /   要旨: As specific inhibitors of the gastric proton pump, responsible for gastric acidification, K-competitive acid blockers (P-CABs) have recently been utilized in the clinical treatment of gastric acid- ...As specific inhibitors of the gastric proton pump, responsible for gastric acidification, K-competitive acid blockers (P-CABs) have recently been utilized in the clinical treatment of gastric acid-related diseases in Asia. However, as these compounds have been developed based on phenotypic screening, their detailed binding poses are unknown. We show crystal and cryo-EM structures of the gastric proton pump in complex with four different P-CABs, tegoprazan, soraprazan, PF-03716556 and revaprazan, at resolutions reaching 2.8 Å. The structures describe molecular details of their interactions and are supported by functional analyses of mutations and molecular dynamics simulations. We reveal that revaprazan has a novel binding mode in which its tetrahydroisoquinoline moiety binds deep in the cation transport conduit. The mechanism of action of these P-CABs can now be evaluated at the molecular level, which will facilitate the rational development and improvement of currently available P-CABs to provide better treatment of acid-related gastrointestinal diseases. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32299.map.gz emd_32299.map.gz | 9.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32299-v30.xml emd-32299-v30.xml emd-32299.xml emd-32299.xml | 18 KB 18 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32299_fsc.xml emd_32299_fsc.xml | 9.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32299.png emd_32299.png | 81.4 KB | ||
| マスクデータ |  emd_32299_msk_1.map emd_32299_msk_1.map | 76.8 MB |  マスクマップ マスクマップ | |
| その他 |  emd_32299_half_map_1.map.gz emd_32299_half_map_1.map.gz emd_32299_half_map_2.map.gz emd_32299_half_map_2.map.gz | 59.8 MB 60 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32299 http://ftp.pdbj.org/pub/emdb/structures/EMD-32299 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32299 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32299 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_32299_validation.pdf.gz emd_32299_validation.pdf.gz | 656.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_32299_full_validation.pdf.gz emd_32299_full_validation.pdf.gz | 655.9 KB | 表示 | |
| XML形式データ |  emd_32299_validation.xml.gz emd_32299_validation.xml.gz | 16.8 KB | 表示 | |
| CIF形式データ |  emd_32299_validation.cif.gz emd_32299_validation.cif.gz | 22.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32299 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32299 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32299 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-32299 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7w4aMC  7w47C  7w48C  7w49C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-11057 (タイトル: Cryo-EM structure of the gastric proton pump complexed with revaprazan EMPIAR-11057 (タイトル: Cryo-EM structure of the gastric proton pump complexed with revaprazanData size: 2.1 TB Data #1: K3 movies for the gastric proton pump complexed with revaprazan - Movies_5 [micrographs - multiframe] Data #2: K3 movies for the gastric proton pump complexed with revaprazan - Movies_7 [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32299.map.gz / 形式: CCP4 / 大きさ: 76.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32299.map.gz / 形式: CCP4 / 大きさ: 76.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.752 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_32299_msk_1.map emd_32299_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_32299_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_32299_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : gastric proton pump
| 全体 | 名称: gastric proton pump |
|---|---|
| 要素 |
|
-超分子 #1: gastric proton pump
| 超分子 | 名称: gastric proton pump / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 実験値: 135 KDa |
-分子 #1: Potassium-transporting ATPase alpha chain 1
| 分子 | 名称: Potassium-transporting ATPase alpha chain 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: H+/K+-exchanging ATPase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 114.456734 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MGKAENYELY QVELGPGPSG DMAAKMSKKK AGRGGGKRKE KLENMKKEME INDHQLSVAE LEQKYQTSAT KGLSASLAAE LLLRDGPNA LRPPRGTPEY VKFARQLAGG LQCLMWVAAA ICLIAFAIQA SEGDLTTDDN LYLALALIAV VVVTGCFGYY Q EFKSTNII ...文字列: MGKAENYELY QVELGPGPSG DMAAKMSKKK AGRGGGKRKE KLENMKKEME INDHQLSVAE LEQKYQTSAT KGLSASLAAE LLLRDGPNA LRPPRGTPEY VKFARQLAGG LQCLMWVAAA ICLIAFAIQA SEGDLTTDDN LYLALALIAV VVVTGCFGYY Q EFKSTNII ASFKNLVPQQ ATVIRDGDKF QINADQLVVG DLVEMKGGDR VPADIRILQA QGCKVDNSSL TGESEPQTRS PE CTHESPL ETRNIAFFST MCLEGTAQGL VVNTGDRTII GRIASLASGV ENEKTPIAIE IEHFVDIIAG LAILFGATFF IVA MCIGYT FLRAMVFFMA IVVAYVPEGL LATVTVCLSL TAKRLASKNC VVKNLEAVET LGSTSVICS(BFD) KTGTLTQNRM TVSHLWFDN HIHSADTTED QSGQTFDQSS ETWRALCRVL TLCNRAAFKS GQDAVPVPKR IVIGDASETA LLKFSELTLG N AMGYRERF PKVCEIPFNS TNKFQLSIHT LEDPRDPRHV LVMKGAPERV LERCSSILIK GQELPLDEQW REAFQTAYLS LG GLGERVL GFCQLYLSEK DYPPGYAFDV EAMNFPTSGL CFAGLVSMID PPRATVPDAV LKCRTAGIRV IMVTGDHPIT AKA IAASVG IISEGSETVE DIAARLRVPV DQVNRKDARA CVINGMQLKD MDPSELVEAL RTHPEMVFAR TSPQQKLVIV ESCQ RLGAI VAVTGDGVND SPALKKADIG VAMGIAGSDA AKNAADMILL DDNFASIVTG VEQGRLIFDN LKKSIAYTLT KNIPE LTPY LIYITVSVPL PLGCITILFI ELCTDIFPSV SLAYEKAESD IMHLRPRNPK RDRLVNEPLA AYSYFQIGAI QSFAGF TDY FTAMAQEGWF PLLCVGLRPQ WENHHLQDLQ DSYGQEWTFG QRLYQQYTCY TVFFISIEMC QIADVLIRKT RRLSAFQ QG FFRNRILVIA IVFQVCIGCF LCYCPGMPNI FNFMPIRFQW WLVPMPFSLL IFVYDEIRKL GVRCCPGSWW DQELYY |
-分子 #2: Potassium-transporting ATPase subunit beta
| 分子 | 名称: Potassium-transporting ATPase subunit beta / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 33.113844 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MAALQEKKSC SQRMEEFQRY CWNPDTGQML GRTLSRWVWI SLYYVAFYVV MSGIFALCIY VLMRTIDPYT PDYQDQLKSP GVTLRPDVY GEKGLDISYN VSDSTTWAGL AHTLHRFLAG YSPAAQEGSI NCTSEKYFFQ ESFLAPNHTK FSCKFTADML Q NCSGRPDP ...文字列: MAALQEKKSC SQRMEEFQRY CWNPDTGQML GRTLSRWVWI SLYYVAFYVV MSGIFALCIY VLMRTIDPYT PDYQDQLKSP GVTLRPDVY GEKGLDISYN VSDSTTWAGL AHTLHRFLAG YSPAAQEGSI NCTSEKYFFQ ESFLAPNHTK FSCKFTADML Q NCSGRPDP TFGFAEGKPC FIIKMNRIVK FLPGNSTAPR VDCAFLDQPR DGPPLQVEYF PANGTYSLHY FPYYGKKAQP HY SNPLVAA KLLNVPRNRD VVIVCKILAE HVSFDNPHDP YEGKVEFKLK IQK |
-分子 #3: N-(4-fluorophenyl)-4,5-dimethyl-6-[(1R)-1-methyl-3,4-dihydro-1H-i...
| 分子 | 名称: N-(4-fluorophenyl)-4,5-dimethyl-6-[(1R)-1-methyl-3,4-dihydro-1H-isoquinolin-2-yl]pyrimidin-2-amine タイプ: ligand / ID: 3 / コピー数: 1 / 式: 8CK |
|---|---|
| 分子量 | 理論値: 362.443 Da |
| Chemical component information | 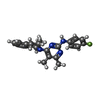 ChemComp-8CK: |
-分子 #4: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 4 / コピー数: 1 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #6: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 6 / コピー数: 3 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #7: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 7 / コピー数: 1 / 式: PCW |
|---|---|
| 分子量 | 理論値: 787.121 Da |
| Chemical component information |  ChemComp-PCW: |
-分子 #8: water
| 分子 | 名称: water / タイプ: ligand / ID: 8 / コピー数: 12 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 6.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL CRYO ARM 300 |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 48.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
 ムービー
ムービー コントローラー
コントローラー















 Z
Z Y
Y X
X