+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23640 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the HCMV pentamer bound by antibodies 1-103, 1-32 and 2-25 | |||||||||
 マップデータ マップデータ | Focused refinement calculated in cryoSPARC and sharpened using DeepEMhancer. | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報host cell Golgi apparatus / entry receptor-mediated virion attachment to host cell / symbiont entry into host cell / fusion of virus membrane with host plasma membrane / viral envelope / host cell plasma membrane / virion membrane / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Human betaherpesvirus 5 (ヘルペスウイルス) / Human betaherpesvirus 5 (ヘルペスウイルス) /  Homo sapiens (ヒト) / Homo sapiens (ヒト) /   Human cytomegalovirus (ヘルペスウイルス) Human cytomegalovirus (ヘルペスウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.81 Å | |||||||||
 データ登録者 データ登録者 | Wrapp D / McLellan JS | |||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2022 ジャーナル: Sci Adv / 年: 2022タイトル: Structural basis for HCMV Pentamer recognition by neuropilin 2 and neutralizing antibodies. 著者: Daniel Wrapp / Xiaohua Ye / Zhiqiang Ku / Hang Su / Harrison G Jones / Nianshuang Wang / Akaash K Mishra / Daniel C Freed / Fengsheng Li / Aimin Tang / Leike Li / Dabbu Kumar Jaijyan / Hua ...著者: Daniel Wrapp / Xiaohua Ye / Zhiqiang Ku / Hang Su / Harrison G Jones / Nianshuang Wang / Akaash K Mishra / Daniel C Freed / Fengsheng Li / Aimin Tang / Leike Li / Dabbu Kumar Jaijyan / Hua Zhu / Dai Wang / Tong-Ming Fu / Ningyan Zhang / Zhiqiang An / Jason S McLellan /  要旨: Human cytomegalovirus (HCMV) encodes multiple surface glycoprotein complexes to infect a variety of cell types. The HCMV Pentamer, composed of gH, gL, UL128, UL130, and UL131A, enhances entry into ...Human cytomegalovirus (HCMV) encodes multiple surface glycoprotein complexes to infect a variety of cell types. The HCMV Pentamer, composed of gH, gL, UL128, UL130, and UL131A, enhances entry into epithelial, endothelial, and myeloid cells by interacting with the cell surface receptor neuropilin 2 (NRP2). Despite the critical nature of this interaction, the molecular determinants that govern NRP2 recognition remain unclear. Here, we describe the cryo-EM structure of NRP2 bound to Pentamer. The high-affinity interaction between these proteins is calcium dependent and differs from the canonical carboxyl-terminal arginine (CendR) binding that NRP2 typically uses. We also determine the structures of four neutralizing human antibodies bound to the HCMV Pentamer to define susceptible epitopes. Two of these antibodies compete with NRP2 binding, but the two most potent antibodies recognize a previously unidentified epitope that does not overlap the NRP2-binding site. Collectively, these findings provide a structural basis for HCMV tropism and antibody-mediated neutralization. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23640.map.gz emd_23640.map.gz | 212.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23640-v30.xml emd-23640-v30.xml emd-23640.xml emd-23640.xml | 33.4 KB 33.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23640_fsc.xml emd_23640_fsc.xml | 15.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23640.png emd_23640.png | 120.1 KB | ||
| その他 |  emd_23640_additional_1.map.gz emd_23640_additional_1.map.gz emd_23640_half_map_1.map.gz emd_23640_half_map_1.map.gz emd_23640_half_map_2.map.gz emd_23640_half_map_2.map.gz | 237.9 MB 285.2 MB 285.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23640 http://ftp.pdbj.org/pub/emdb/structures/EMD-23640 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23640 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23640 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_23640_validation.pdf.gz emd_23640_validation.pdf.gz | 715.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_23640_full_validation.pdf.gz emd_23640_full_validation.pdf.gz | 715.5 KB | 表示 | |
| XML形式データ |  emd_23640_validation.xml.gz emd_23640_validation.xml.gz | 23.2 KB | 表示 | |
| CIF形式データ |  emd_23640_validation.cif.gz emd_23640_validation.cif.gz | 30.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23640 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23640 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23640 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23640 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23640.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23640.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Focused refinement calculated in cryoSPARC and sharpened using DeepEMhancer. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.075 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
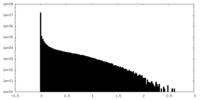
-追加マップ: Full map that was later subjected to focused...
| ファイル | emd_23640_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full map that was later subjected to focused refinement to calculate the primary map. Calculated in cryoSPARC and sharpened using DeepEMhancer. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
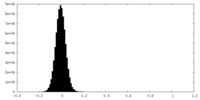
-ハーフマップ: Half map A.
| ファイル | emd_23640_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
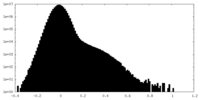
-ハーフマップ: Half map B.
| ファイル | emd_23640_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Quaternary complex of the HCMV pentamer bound by Fabs 1-103, 1-32...
+超分子 #1: Quaternary complex of the HCMV pentamer bound by Fabs 1-103, 1-32...
+超分子 #2: HCMV pentamer
+超分子 #3: 2-25 Fab
+超分子 #4: 1-32 Fab
+超分子 #5: 1-103 Fab
+分子 #1: Envelope glycoprotein L
+分子 #2: Envelope protein UL128
+分子 #3: Envelope glycoprotein UL130
+分子 #4: UL131A
+分子 #5: 2-25 Fab Heavy Chain
+分子 #6: 2-25 Fab Light Chain
+分子 #7: 1-32 Fab Heavy Chain
+分子 #8: 1-32 Fab Light Chain
+分子 #9: 1-103 Fab Heavy Chain
+分子 #10: 1-103 Fab Light Chain
+分子 #11: 2-acetamido-2-deoxy-beta-D-glucopyranose
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| |||||||||||||||
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: PLASMA CLEANING | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV 詳細: Blotted for six seconds with a force of "1" before plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 36.0 e/Å2 詳細: Collected from a single grid at a mixture of 0 degrees tilt and -30 degrees tilt |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)