+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21954 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM Structure of Influenza Hemagglutinin (HA) Trimer Vitrified Using Back-it-up | ||||||||||||
 マップデータ マップデータ | Sharpened map | ||||||||||||
 試料 試料 |
| ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報viral budding from plasma membrane / clathrin-dependent endocytosis of virus by host cell / host cell surface receptor binding / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / host cell plasma membrane / virion membrane / membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  H3N2 subtype (ウイルス) / H3N2 subtype (ウイルス) /  Influenza A virus (strain A/Hong Kong/1/1968 H3N2) (A型インフルエンザウイルス) Influenza A virus (strain A/Hong Kong/1/1968 H3N2) (A型インフルエンザウイルス) | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | ||||||||||||
 データ登録者 データ登録者 | Tan YZ / Rubinstein JL | ||||||||||||
| 資金援助 |  カナダ, 3件 カナダ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2020 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2020タイトル: Through-grid wicking enables high-speed cryoEM specimen preparation. 著者: Yong Zi Tan / John L Rubinstein /  要旨: Blotting times for conventional cryoEM specimen preparation complicate time-resolved studies and lead to some specimens adopting preferred orientations or denaturing at the air-water interface. Here, ...Blotting times for conventional cryoEM specimen preparation complicate time-resolved studies and lead to some specimens adopting preferred orientations or denaturing at the air-water interface. Here, it is shown that solution sprayed onto one side of a holey cryoEM grid can be wicked through the grid by a glass-fiber filter held against the opposite side, often called the `back', of the grid, producing a film suitable for vitrification. This process can be completed in tens of milliseconds. Ultrasonic specimen application and through-grid wicking were combined in a high-speed specimen-preparation device that was named `Back-it-up' or BIU. The high liquid-absorption capacity of the glass fiber compared with self-wicking grids makes the method relatively insensitive to the amount of sample applied. Consequently, through-grid wicking produces large areas of ice that are suitable for cryoEM for both soluble and detergent-solubilized protein complexes. The speed of the device increases the number of views for a specimen that suffers from preferred orientations. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21954.map.gz emd_21954.map.gz | 59.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21954-v30.xml emd-21954-v30.xml emd-21954.xml emd-21954.xml | 28.9 KB 28.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_21954_fsc.xml emd_21954_fsc.xml | 9.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_21954.png emd_21954.png | 153.9 KB | ||
| マスクデータ |  emd_21954_msk_1.map emd_21954_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| その他 |  emd_21954_additional_1.map.gz emd_21954_additional_1.map.gz emd_21954_additional_2.map.gz emd_21954_additional_2.map.gz emd_21954_additional_3.map.gz emd_21954_additional_3.map.gz emd_21954_additional_4.map.gz emd_21954_additional_4.map.gz emd_21954_additional_5.map.gz emd_21954_additional_5.map.gz emd_21954_half_map_1.map.gz emd_21954_half_map_1.map.gz emd_21954_half_map_2.map.gz emd_21954_half_map_2.map.gz | 12.6 MB 10.8 MB 119.8 KB 2 MB 32.2 MB 59.4 MB 59.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21954 http://ftp.pdbj.org/pub/emdb/structures/EMD-21954 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21954 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21954 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_21954_validation.pdf.gz emd_21954_validation.pdf.gz | 742.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_21954_full_validation.pdf.gz emd_21954_full_validation.pdf.gz | 741.8 KB | 表示 | |
| XML形式データ |  emd_21954_validation.xml.gz emd_21954_validation.xml.gz | 16.5 KB | 表示 | |
| CIF形式データ |  emd_21954_validation.cif.gz emd_21954_validation.cif.gz | 21.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21954 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21954 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21954 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21954 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6wxbMC  6wx6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10532 (タイトル: Single-Particle CryoEM of Influenza Hemagglutinin (HA) Trimer Vitrified Using Back-it-up EMPIAR-10532 (タイトル: Single-Particle CryoEM of Influenza Hemagglutinin (HA) Trimer Vitrified Using Back-it-upData size: 1.2 TB Data #1: Unaligned Falcon IV movies [micrographs - multiframe] Data #2: Aligned micrographs [micrographs - single frame] Data #3: Final Refined Particles with Euler Angles and Shifts [picked particles - single frame - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21954.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21954.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.03 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_21954_msk_1.map emd_21954_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: 3DFSC - Raw
| ファイル | emd_21954_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3DFSC - Raw | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: 3DFSC - Thresholded
| ファイル | emd_21954_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3DFSC - Thresholded | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: 3DFSC - Thresholded and Binarized
| ファイル | emd_21954_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3DFSC - Thresholded and Binarized | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Local resolution map
| ファイル | emd_21954_additional_4.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Local resolution map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Raw map
| ファイル | emd_21954_additional_5.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Raw map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_21954_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_21954_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Influenza Hemagglutinin Trimer (H3N2) (A/Hong Kong/1/1968)
| 全体 | 名称: Influenza Hemagglutinin Trimer (H3N2) (A/Hong Kong/1/1968) |
|---|---|
| 要素 |
|
-超分子 #1: Influenza Hemagglutinin Trimer (H3N2) (A/Hong Kong/1/1968)
| 超分子 | 名称: Influenza Hemagglutinin Trimer (H3N2) (A/Hong Kong/1/1968) タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  H3N2 subtype (ウイルス) H3N2 subtype (ウイルス) |
| 分子量 | 理論値: 190 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換株: HEK293F Homo sapiens (ヒト) / 組換株: HEK293F |
-分子 #1: Hemagglutinin
| 分子 | 名称: Hemagglutinin / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Influenza A virus (strain A/Hong Kong/1/1968 H3N2) (A型インフルエンザウイルス) Influenza A virus (strain A/Hong Kong/1/1968 H3N2) (A型インフルエンザウイルス)株: A/Hong Kong/1/1968 H3N2 |
| 分子量 | 理論値: 62.855215 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QDLPGNDNST ATLCLGHHAV PNGTLVKTIT DDQIEVTNAT ELVQSSSTGK ICNNPHRILD GIDCTLIDAL LGDPHCDVFQ NETWDLFVE RSKAFSNCYP YDVPDYASLR SLVASSGTLE FITEGFTWTG VTQNGGSNAC KRGPGSGFFS RLNWLTKSGS T YPVLNVTM ...文字列: QDLPGNDNST ATLCLGHHAV PNGTLVKTIT DDQIEVTNAT ELVQSSSTGK ICNNPHRILD GIDCTLIDAL LGDPHCDVFQ NETWDLFVE RSKAFSNCYP YDVPDYASLR SLVASSGTLE FITEGFTWTG VTQNGGSNAC KRGPGSGFFS RLNWLTKSGS T YPVLNVTM PNNDNFDKLY IWGVHHPSTN QEQTSLYVQA SGRVTVSTRR SQQTIIPNIG SRPWVRGLSS RISIYWTIVK PG DVLVINS NGNLIAPRGY FKMRTGKSSI MRSDAPIDTC ISECITPNGS IPNDKPFQNV NKITYGACPK YVKQNTLKLA TGM RNVPEK QTRGLFGAIA GFIENGWEGM IDGWYGFRHQ NSEGTGQAAD LKSTQAAIDQ INGKLNRVIE KTNEKFHQIE KEFS EVEGR IQDLEKYVED TKIDLWSYNA ELLVALENQH TIDLTDSEMN KLFEKTRRQL RENAEDMGNG CFKIYHKCDN ACIES IRNG TYDHDVYRDE ALNNRFQIKG VELKSGYDGG GGTGGGGTGR MKQIEDKIEE ILSKIYHIEN EIARIKKLIG ERHHHH HH |
-分子 #2: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 2 / コピー数: 12 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #3: beta-D-mannopyranose
| 分子 | 名称: beta-D-mannopyranose / タイプ: ligand / ID: 3 / コピー数: 3 / 式: BMA |
|---|---|
| 分子量 | 理論値: 180.156 Da |
| Chemical component information | 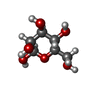 ChemComp-BMA: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | モデル: Homemade / 材質: COPPER/RHODIUM / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR 詳細: Grid was glow discharged on both sides for 120s each. |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 50 % / チャンバー内温度: 298 K / 装置: HOMEMADE PLUNGER 詳細: Back-it-up (ultrasonic specimen application and through-grid wicking in a high-speed specimen preparation device) was used. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / デジタル化 - サンプリング間隔: 14.0 µm / 撮影したグリッド数: 1 / 実像数: 1556 / 平均露光時間: 9.0 sec. / 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





















 Z
Z Y
Y X
X



































































