+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12795 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human RNA Polymerase I in elongation state | |||||||||
 マップデータ マップデータ | Elongating human RNA Polymerase I, Map A, unsharpened | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNA polymerase I / human / rRNA transcription / DNA-dependent RNA polymerase / elongation state / TRANSCRIPTION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA polymerase I transcription regulator complex / negative regulation of protein localization to nucleolus / nucleologenesis / neural crest formation / RNA Polymerase III Chain Elongation / RNA Polymerase III Transcription Termination / DNA/RNA hybrid binding / regulation of transcription by RNA polymerase I / RPAP3/R2TP/prefoldin-like complex / RNA polymerase I general transcription initiation factor binding ...RNA polymerase I transcription regulator complex / negative regulation of protein localization to nucleolus / nucleologenesis / neural crest formation / RNA Polymerase III Chain Elongation / RNA Polymerase III Transcription Termination / DNA/RNA hybrid binding / regulation of transcription by RNA polymerase I / RPAP3/R2TP/prefoldin-like complex / RNA polymerase I general transcription initiation factor binding / Cytosolic sensors of pathogen-associated DNA / RNA Polymerase III Transcription Initiation From Type 1 Promoter / RNA Polymerase III Transcription Initiation From Type 2 Promoter / RNA Polymerase III Transcription Initiation From Type 3 Promoter / RNA Polymerase III Abortive And Retractive Initiation / RNA polymerase I preinitiation complex assembly / Abortive elongation of HIV-1 transcript in the absence of Tat / nucleobase-containing compound metabolic process / RNA Polymerase I Transcription Termination / FGFR2 alternative splicing / MicroRNA (miRNA) biogenesis / Signaling by FGFR2 IIIa TM / Viral Messenger RNA Synthesis / RNA Pol II CTD phosphorylation and interaction with CE during HIV infection / RNA Pol II CTD phosphorylation and interaction with CE / Formation of the Early Elongation Complex / Formation of the HIV-1 Early Elongation Complex / mRNA Capping / PIWI-interacting RNA (piRNA) biogenesis / HIV Transcription Initiation / RNA Polymerase II HIV Promoter Escape / Transcription of the HIV genome / RNA Polymerase II Promoter Escape / RNA Polymerase II Transcription Pre-Initiation And Promoter Opening / RNA Polymerase II Transcription Initiation / RNA Polymerase II Transcription Initiation And Promoter Clearance / RNA polymerase III activity / termination of RNA polymerase I transcription / nucleolar large rRNA transcription by RNA polymerase I / mRNA Splicing - Minor Pathway / RNA Polymerase I Transcription Initiation / Pausing and recovery of Tat-mediated HIV elongation / Tat-mediated HIV elongation arrest and recovery / transcription by RNA polymerase I / transcription initiation at RNA polymerase I promoter / rRNA transcription / HIV elongation arrest and recovery / Pausing and recovery of HIV elongation / Processing of Capped Intron-Containing Pre-mRNA / transcription by RNA polymerase III / RNA polymerase II transcribes snRNA genes / Tat-mediated elongation of the HIV-1 transcript / transcription elongation by RNA polymerase I / Formation of HIV-1 elongation complex containing HIV-1 Tat / tRNA transcription by RNA polymerase III / RNA polymerase I complex / RNA polymerase I activity / RNA polymerase III complex / Formation of HIV elongation complex in the absence of HIV Tat / RNA polymerase II, core complex / RNA Polymerase II Transcription Elongation / Formation of RNA Pol II elongation complex / cell surface receptor protein tyrosine kinase signaling pathway / RNA Polymerase II Pre-transcription Events / Inhibition of DNA recombination at telomere / embryo implantation / mRNA Splicing - Major Pathway / protein-DNA complex / cellular response to leukemia inhibitory factor / DNA-templated transcription initiation / TP53 Regulates Transcription of DNA Repair Genes / RNA Polymerase I Promoter Escape / Transcriptional regulation by small RNAs / NoRC negatively regulates rRNA expression / B-WICH complex positively regulates rRNA expression / Transcription-Coupled Nucleotide Excision Repair (TC-NER) / Formation of TC-NER Pre-Incision Complex / ribonucleoside binding / fibrillar center / Activation of anterior HOX genes in hindbrain development during early embryogenesis / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / single-stranded DNA binding / chromosome / Estrogen-dependent gene expression / transcription by RNA polymerase II / nucleic acid binding / protein dimerization activity / protein stabilization / chromatin binding / nucleolus / magnesium ion binding / mitochondrion / DNA binding / RNA binding / zinc ion binding / nucleoplasm / nucleus 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.7 Å | |||||||||
 データ登録者 データ登録者 | Misiaszek AD / Girbig M | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2021 ジャーナル: Nat Struct Mol Biol / 年: 2021タイトル: Cryo-EM structures of human RNA polymerase I. 著者: Agata D Misiaszek / Mathias Girbig / Helga Grötsch / Florence Baudin / Brice Murciano / Aleix Lafita / Christoph W Müller /   要旨: RNA polymerase I (Pol I) specifically synthesizes ribosomal RNA. Pol I upregulation is linked to cancer, while mutations in the Pol I machinery lead to developmental disorders. Here we report the ...RNA polymerase I (Pol I) specifically synthesizes ribosomal RNA. Pol I upregulation is linked to cancer, while mutations in the Pol I machinery lead to developmental disorders. Here we report the cryo-EM structure of elongating human Pol I at 2.7 Å resolution. In the exit tunnel, we observe a double-stranded RNA helix that may support Pol I processivity. Our structure confirms that human Pol I consists of 13 subunits with only one subunit forming the Pol I stalk. Additionally, the structure of human Pol I in complex with the initiation factor RRN3 at 3.1 Å resolution reveals stalk flipping upon RRN3 binding. We also observe an inactivated state of human Pol I bound to an open DNA scaffold at 3.3 Å resolution. Lastly, the high-resolution structure of human Pol I allows mapping of disease-related mutations that can aid understanding of disease etiology. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12795.map.gz emd_12795.map.gz | 65.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12795-v30.xml emd-12795-v30.xml emd-12795.xml emd-12795.xml | 61.1 KB 61.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_12795_fsc.xml emd_12795_fsc.xml | 10 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_12795.png emd_12795.png | 62.1 KB | ||
| マスクデータ |  emd_12795_msk_1.map emd_12795_msk_1.map emd_12795_msk_2.map emd_12795_msk_2.map emd_12795_msk_3.map emd_12795_msk_3.map | 83.7 MB 83.7 MB 83.7 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-12795.cif.gz emd-12795.cif.gz | 11.5 KB | ||
| その他 |  emd_12795_additional_1.map.gz emd_12795_additional_1.map.gz emd_12795_additional_2.map.gz emd_12795_additional_2.map.gz emd_12795_additional_3.map.gz emd_12795_additional_3.map.gz emd_12795_additional_4.map.gz emd_12795_additional_4.map.gz emd_12795_additional_5.map.gz emd_12795_additional_5.map.gz emd_12795_additional_6.map.gz emd_12795_additional_6.map.gz emd_12795_additional_7.map.gz emd_12795_additional_7.map.gz emd_12795_additional_8.map.gz emd_12795_additional_8.map.gz emd_12795_additional_9.map.gz emd_12795_additional_9.map.gz emd_12795_half_map_1.map.gz emd_12795_half_map_1.map.gz emd_12795_half_map_2.map.gz emd_12795_half_map_2.map.gz | 75.3 MB 64.9 MB 73.5 MB 66.8 MB 62.3 MB 73.9 MB 76.1 MB 67.2 MB 74.8 MB 65.4 MB 65.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12795 http://ftp.pdbj.org/pub/emdb/structures/EMD-12795 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12795 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12795 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12795_validation.pdf.gz emd_12795_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12795_full_validation.pdf.gz emd_12795_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_12795_validation.xml.gz emd_12795_validation.xml.gz | 17 KB | 表示 | |
| CIF形式データ |  emd_12795_validation.cif.gz emd_12795_validation.cif.gz | 22.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12795 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12795 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12795 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12795 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7ob9MC  7obaC  7obbC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10965 (タイトル: Cryo-EM structure of human RNA polymerase I in elongation state EMPIAR-10965 (タイトル: Cryo-EM structure of human RNA polymerase I in elongation stateData size: 1.8 TB Data #1: Unaligned multi-frame micrographs of human RNA polymerase I in elongating state [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12795.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12795.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Elongating human RNA Polymerase I, Map A, unsharpened | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.822 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
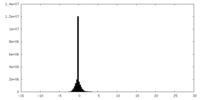
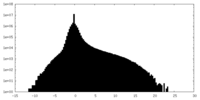
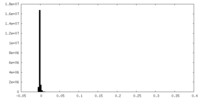
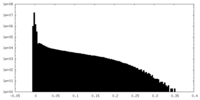
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
+マスク #1
+マスク #2
+マスク #3
+追加マップ: Elongating human RNA Polymerase I, Map B1, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map A, locally...
+追加マップ: Elongating human RNA Polymerase I, Map B, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map B2, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map B1, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map B, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map B2, RELION...
+追加マップ: Elongating human RNA Polymerase I, Map C, Phenix...
+追加マップ: Elongating human RNA Polymerase I, Map C, Phenix...
+ハーフマップ: Elongating human RNA Polymerase I, Map A, half map 2
+ハーフマップ: Elongating human RNA Polymerase I, Map A, half map 2
- 試料の構成要素
試料の構成要素
+全体 : RNA polymerase I
+超分子 #1: RNA polymerase I
+超分子 #2: RNA polymerase I
+超分子 #3: RNA and DNA
+分子 #1: DNA-directed RNA polymerase I subunit RPA1
+分子 #2: DNA-directed RNA polymerase I subunit RPA2
+分子 #3: DNA-directed RNA polymerases I and III subunit RPAC1
+分子 #4: DNA-directed RNA polymerases I, II, and III subunit RPABC1
+分子 #5: DNA-directed RNA polymerases I, II, and III subunit RPABC2
+分子 #6: DNA-directed RNA polymerase I subunit RPA43
+分子 #7: DNA-directed RNA polymerases I, II, and III subunit RPABC3
+分子 #8: DNA-directed RNA polymerase I subunit RPA12
+分子 #9: DNA-directed RNA polymerases I, II, and III subunit RPABC5
+分子 #10: DNA-directed RNA polymerases I and III subunit RPAC2
+分子 #11: DNA-directed RNA polymerases I, II, and III subunit RPABC4
+分子 #12: DNA-directed RNA polymerase I subunit RPA34
+分子 #13: DNA-directed RNA polymerase I subunit RPA49
+分子 #14: RNA
+分子 #15: DNA non-template strand
+分子 #16: DNA template strand
+分子 #17: ZINC ION
+分子 #18: MAGNESIUM ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.7 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: OTHER 詳細: NanoClean plasma cleaner (Fischione Instruments, Model 1070) | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 288 K / 装置: FEI VITROBOT MARK IV / 詳細: blot force 3, blot time 0 s, wait time 0 s. | |||||||||||||||
| 詳細 | Human RNA Polymerase I with 1.5 molar excess of the synthetic nucleic acid template |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 10053 / 平均電子線量: 50.9 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル |
| ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 詳細 | Initial rigid body fitting with UCSF Chimera followed by manual model fitting in Coot. | ||||||||||||||||
| 得られたモデル |  PDB-7ob9: |
 ムービー
ムービー コントローラー
コントローラー

































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)