+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10845 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of yeast mitochondrial RNA polymerase transcription pre-initiation complex | |||||||||
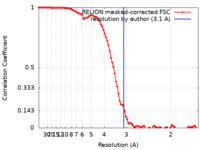
 マップデータ マップデータ | post process map 3.1A | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | gene transcription / polymerase / RDRP / MTF1 / RPO41 / POLRMT / mtRNAP / DNA / transcription initiation / RNA polymerase / mitochondria / TRANSCRIPTION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Mitochondrial transcription initiation / mitochondrial DNA-directed RNA polymerase complex / mitochondrial promoter sequence-specific DNA binding / mitochondrial transcription factor activity / transcription initiation at mitochondrial promoter / mitochondrial transcription / mitochondrial genome maintenance / DNA primase activity / DNA replication, synthesis of primer / positive regulation of DNA-templated transcription, elongation ...Mitochondrial transcription initiation / mitochondrial DNA-directed RNA polymerase complex / mitochondrial promoter sequence-specific DNA binding / mitochondrial transcription factor activity / transcription initiation at mitochondrial promoter / mitochondrial transcription / mitochondrial genome maintenance / DNA primase activity / DNA replication, synthesis of primer / positive regulation of DNA-templated transcription, elongation / mitochondrial nucleoid / 転移酵素; 一炭素原子の基を移すもの; メチル基を移すもの / methyltransferase activity / mitochondrial intermembrane space / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / methylation / mitochondrial matrix / mitochondrion / DNA binding / RNA binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Das K | |||||||||
| 資金援助 |  ベルギー, 1件 ベルギー, 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2021 ジャーナル: Mol Cell / 年: 2021タイトル: Cryo-EM Structures Reveal Transcription Initiation Steps by Yeast Mitochondrial RNA Polymerase. 著者: Brent De Wijngaert / Shemaila Sultana / Anupam Singh / Chhaya Dharia / Hans Vanbuel / Jiayu Shen / Daniel Vasilchuk / Sergio E Martinez / Eaazhisai Kandiah / Smita S Patel / Kalyan Das /    要旨: Mitochondrial RNA polymerase (mtRNAP) is crucial in cellular energy production, yet understanding of mitochondrial DNA transcription initiation lags that of bacterial and nuclear DNA transcription. ...Mitochondrial RNA polymerase (mtRNAP) is crucial in cellular energy production, yet understanding of mitochondrial DNA transcription initiation lags that of bacterial and nuclear DNA transcription. We report structures of two transcription initiation intermediate states of yeast mtRNAP that explain promoter melting, template alignment, DNA scrunching, abortive synthesis, and transition into elongation. In the partially melted initiation complex (PmIC), transcription factor MTF1 makes base-specific interactions with flipped non-template (NT) nucleotides "AAGT" at -4 to -1 positions of the DNA promoter. In the initiation complex (IC), the template in the expanded 7-mer bubble positions the RNA and NTP analog UTPαS, while NT scrunches into an NT loop. The scrunched NT loop is stabilized by the centrally positioned MTF1 C-tail. The IC and PmIC states coexist in solution, revealing a dynamic equilibrium between two functional states. Frequent scrunching/unscruching transitions and the imminent steric clashes of the inflating NT loop and growing RNA:DNA with the C-tail explain abortive synthesis and transition into elongation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10845.map.gz emd_10845.map.gz | 14.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10845-v30.xml emd-10845-v30.xml emd-10845.xml emd-10845.xml | 27.1 KB 27.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_10845_fsc.xml emd_10845_fsc.xml | 9.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_10845.png emd_10845.png | 172.2 KB | ||
| マスクデータ |  emd_10845_msk_1.map emd_10845_msk_1.map | 15.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-10845.cif.gz emd-10845.cif.gz | 7.8 KB | ||
| その他 |  emd_10845_half_map_1.map.gz emd_10845_half_map_1.map.gz emd_10845_half_map_2.map.gz emd_10845_half_map_2.map.gz | 49.6 MB 49.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10845 http://ftp.pdbj.org/pub/emdb/structures/EMD-10845 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10845 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10845 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_10845_validation.pdf.gz emd_10845_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_10845_full_validation.pdf.gz emd_10845_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_10845_validation.xml.gz emd_10845_validation.xml.gz | 15.8 KB | 表示 | |
| CIF形式データ |  emd_10845_validation.cif.gz emd_10845_validation.cif.gz | 20.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10845 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10845 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10845 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10845 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10845.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10845.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | post process map 3.1A | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.827 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_10845_msk_1.map emd_10845_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
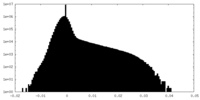
| 密度ヒストグラム |
-ハーフマップ: Half-1
| ファイル | emd_10845_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half-2
| ファイル | emd_10845_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : mitochondria DNA-dependent RNA polymerase pre-initiation complex
| 全体 | 名称: mitochondria DNA-dependent RNA polymerase pre-initiation complex |
|---|---|
| 要素 |
|
-超分子 #1: mitochondria DNA-dependent RNA polymerase pre-initiation complex
| 超分子 | 名称: mitochondria DNA-dependent RNA polymerase pre-initiation complex タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 分子量 | 理論値: 202 KDa |
-超分子 #2: mitochondria DNA-dependent RNA polymerase pre-initiation complex
| 超分子 | 名称: mitochondria DNA-dependent RNA polymerase pre-initiation complex タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: DNA
| 超分子 | 名称: DNA / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3-#4 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Mitochondrial transcription factor 1
| 分子 | 名称: Mitochondrial transcription factor 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO EC番号: 転移酵素; 一炭素原子の基を移すもの; メチル基を移すもの |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 41.151203 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGGSHHHHHH GMASSVPIPG IKDISKLKFF YGFKYLWNPT VYNKIFDKLD LTKTYKHPEE LKVLDLYPGV GIQSAIFYNK YCPRQYSLL EKRSSLYKFL NAKFEGSPLQ ILKRDPYDWS TYSNLIDEER IFVPEVQSSD HINDKFLTVA NVTGEGSEGL I MQWLSCIG ...文字列: MGGSHHHHHH GMASSVPIPG IKDISKLKFF YGFKYLWNPT VYNKIFDKLD LTKTYKHPEE LKVLDLYPGV GIQSAIFYNK YCPRQYSLL EKRSSLYKFL NAKFEGSPLQ ILKRDPYDWS TYSNLIDEER IFVPEVQSSD HINDKFLTVA NVTGEGSEGL I MQWLSCIG NKNWLYRFGK VKMLLWMPST TARKLLARPG MHSRSKCSVV REAFTDTKLI AISDANELKG FDSQCIEEWD PI LFSAAEI WPTKGKPIAL VEMDPIDFDF DVDNWDYVTR HLMILKRTPL NTVMDSLGHG GQQYFNSRIT DKDLLKKCPI DLT NDEFIY LTKLFMEWPF KPDILMDFVD MYQTEHSG UniProtKB: Mitochondrial transcription factor 1 |
-分子 #2: DNA-directed RNA polymerase, mitochondrial
| 分子 | 名称: DNA-directed RNA polymerase, mitochondrial / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 143.282656 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: GAMGSGIQRP SAVTSMTRTR DVMQLWSLLE ACLQSNLMKR AFSILESLYL VPEHKQRFIE DYNMYLNSFS KNDPNFPILK MNEKLTNDL ETSFKDVNYN DKTLAIMIHH ALNFHSTTSS MLLKPIISAY LKMSVNGIRE IFSCLDILTI SDLNILMNDL K VITPSQLP ...文字列: GAMGSGIQRP SAVTSMTRTR DVMQLWSLLE ACLQSNLMKR AFSILESLYL VPEHKQRFIE DYNMYLNSFS KNDPNFPILK MNEKLTNDL ETSFKDVNYN DKTLAIMIHH ALNFHSTTSS MLLKPIISAY LKMSVNGIRE IFSCLDILTI SDLNILMNDL K VITPSQLP NSVRPILESL TLSPTPVNNI ENEEGLNKVE AENDSKLHKA SNASSDSIKK PSLDPLREVS FHGSTEVLSK DA EKLIAVD TIGMRVIRHT LLGLSLTPEQ KEQISKFKFD ANDNVLKMKP TKNDDNNNSI NFFEIYNSLP TLEEKKAFES ALN IFNQDR QKVLENRATE AARERWKHDF EEAKARGDIS IEKNLNVKLW KWYNEMLPLV KEEINHCRSL LSEKLSDKKG LNKV DTNRL GYGPYLTLID PGKMCVITIL ELLKLNSTGG VIEGMRTARA VISVGKAIEM EFRSEQVLKS ESQAFRDVNK KSPEF KKLV QNAKSVFRSS QIEQSKILWP QSIRARIGSV LISMLIQVAK VSVQGVDPVT KAKVHGEAPA FAHGYQYHNG SKLGVL KIH KTLIRQLNGE RLIASVQPQL LPMLVEPKPW VNWRSGGYHY TQSTLLRTKD SPEQVAYLKA ASDNGDIDRV YDGLNVL GR TPWTVNRKVF DVVSQVWNKG EGFLDIPGAQ DEMVLPPAPP KNSDPSILRA WKLQVKTIAN KFSSDRSNRC DTNYKLEI A RAFLGEKLYF PHNLDFRGRA YPLSPHFNHL GNDMSRGLLI FWHGKKLGPS GLKWLKIHLS NLFGFDKLPL KDRVAFTES HLQDIKDSAE NPLTGDRWWT TADKPWQALA TCFELNEVMK MDNPEEFISH QPVHQDGTCN GLQHYAALGG DVEGATQVNL VPSDKPQDV YAHVARLVQK RLEIAAEKGD ENAKILKDKI TRKVVKQTVM TNVYGVTYVG ATFQIAKQLS PIFDDRKESL D FSKYLTKH VFSAIRELFH SAHLIQDWLG ESAKRISKSI RLDVDEKSFK NGNKPDFMSS VIWTTPLGLP IVQPYREESK KQ VETNLQT VFISDPFAVN PVNARRQKAG LPPNFIHSLD ASHMLLSAAE CGKQGLDFAS VHDSYWTHAS DIDTMNVVLR EQF IKLHEV DLVLRLKEEF DQRYKNYVKI GKLKRSTDLA QKIIRIRKDL SRKLGRSTTL ADEIYFEKKR QELLNSPLIE DRNV GEKMV TTVSLFEDIT DLDALELENG GDENSGMSVL LPLRLPEIPP KGDFDVTVLR NSQYFFS UniProtKB: DNA-directed RNA polymerase, mitochondrial |
-分子 #3: DNA (33-MER) NON-TEMPLATE
| 分子 | 名称: DNA (33-MER) NON-TEMPLATE / タイプ: dna / ID: 3 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 10.248671 KDa |
| 配列 | 文字列: (DC)(DG)(DA)(DA)(DT)(DA)(DA)(DG)(DT)(DA) (DT)(DT)(DG)(DA)(DT)(DA)(DT)(DA)(DA)(DG) (DT)(DA)(DA)(DT)(DA)(DG)(DA)(DT)(DA) (DA)(DT)(DG)(DC) |
-分子 #4: DNA (33-MER) template
| 分子 | 名称: DNA (33-MER) template / タイプ: dna / ID: 4 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 10.047511 KDa |
| 配列 | 文字列: (DG)(DC)(DA)(DT)(DT)(DA)(DT)(DC)(DT)(DA) (DC)(DC)(DG)(DA)(DC)(DA)(DA)(DT)(DA)(DT) (DC)(DA)(DA)(DT)(DA)(DC)(DT)(DT)(DA) (DT)(DT)(DC)(DG) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.0 mg/mL |
|---|---|
| 緩衝液 | pH: 7 詳細: 50mM Bis-tris propane, 100mM NaCl, 5mM MgCl2, 1mM EDTA, 2mM DTT |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 8 K / 装置: LEICA EM GP / 詳細: 5 uL sample; back blotting for 12 -14 second. |
| 詳細 | The sample was monodisperse with hydrodynamic radius 5.82nm. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 1 / 平均露光時間: 6.0 sec. / 平均電子線量: 65.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 最大 デフォーカス(補正後): 26.0 µm / 最小 デフォーカス(補正後): 5.5 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 22.0 µm / 最小 デフォーカス(公称値): 7.0 µm / 倍率(公称値): 165000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル |
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 詳細 | Realspace refinement | ||||||||
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: Coorelation coefficu=ient | ||||||||
| 得られたモデル |  PDB-6ymv: |
 ムービー
ムービー コントローラー
コントローラー






























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)