+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10413 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SAGA Tra1 module | |||||||||
 マップデータ マップデータ | local resolution filtered map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Coactivator / Transcription / Histone acetyltransferase / Histone deubiquitinase / GENE REGULATION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報TTT Hsp90 cochaperone complex / SLIK (SAGA-like) complex / SAGA complex / RNA Polymerase II Promoter Escape / RNA Polymerase II Transcription Pre-Initiation And Promoter Opening / RNA Polymerase II Transcription Initiation / RNA Polymerase II Transcription Initiation And Promoter Clearance / IRE1-mediated unfolded protein response / transcription factor TFIID complex / RNA Polymerase II Pre-transcription Events ...TTT Hsp90 cochaperone complex / SLIK (SAGA-like) complex / SAGA complex / RNA Polymerase II Promoter Escape / RNA Polymerase II Transcription Pre-Initiation And Promoter Opening / RNA Polymerase II Transcription Initiation / RNA Polymerase II Transcription Initiation And Promoter Clearance / IRE1-mediated unfolded protein response / transcription factor TFIID complex / RNA Polymerase II Pre-transcription Events / DNA repair-dependent chromatin remodeling / NuA4 histone acetyltransferase complex / Ub-specific processing proteases / RNA polymerase II preinitiation complex assembly / TBP-class protein binding / transcription coregulator activity / peroxisome / chromatin organization / molecular adaptor activity / RNA polymerase II-specific DNA-binding transcription factor binding / transcription by RNA polymerase II / protein heterodimerization activity / DNA repair / DNA-templated transcription / chromatin binding / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / DNA binding / identical protein binding / nucleus 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
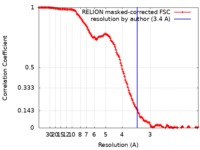
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Wang H / Cheung A | |||||||||
| 資金援助 |  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2020 ジャーナル: Nature / 年: 2020タイトル: Structure of the transcription coactivator SAGA. 著者: Haibo Wang / Christian Dienemann / Alexandra Stützer / Henning Urlaub / Alan C M Cheung / Patrick Cramer /   要旨: Gene transcription by RNA polymerase II is regulated by activator proteins that recruit the coactivator complexes SAGA (Spt-Ada-Gcn5-acetyltransferase) and transcription factor IID (TFIID). SAGA is ...Gene transcription by RNA polymerase II is regulated by activator proteins that recruit the coactivator complexes SAGA (Spt-Ada-Gcn5-acetyltransferase) and transcription factor IID (TFIID). SAGA is required for all regulated transcription and is conserved among eukaryotes. SAGA contains four modules: the activator-binding Tra1 module, the core module, the histone acetyltransferase (HAT) module and the histone deubiquitination (DUB) module. Previous studies provided partial structures, but the structure of the central core module is unknown. Here we present the cryo-electron microscopy structure of SAGA from the yeast Saccharomyces cerevisiae and resolve the core module at 3.3 Å resolution. The core module consists of subunits Taf5, Sgf73 and Spt20, and a histone octamer-like fold. The octamer-like fold comprises the heterodimers Taf6-Taf9, Taf10-Spt7 and Taf12-Ada1, and two histone-fold domains in Spt3. Spt3 and the adjacent subunit Spt8 interact with the TATA box-binding protein (TBP). The octamer-like fold and its TBP-interacting region are similar in TFIID, whereas Taf5 and the Taf6 HEAT domain adopt distinct conformations. Taf12 and Spt20 form flexible connections to the Tra1 module, whereas Sgf73 tethers the DUB module. Binding of a nucleosome to SAGA displaces the HAT and DUB modules from the core-module surface, allowing the DUB module to bind one face of an ubiquitinated nucleosome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10413.map.gz emd_10413.map.gz | 142.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10413-v30.xml emd-10413-v30.xml emd-10413.xml emd-10413.xml | 23.2 KB 23.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_10413_fsc.xml emd_10413_fsc.xml | 14.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_10413.png emd_10413.png | 302 KB | ||
| Filedesc metadata |  emd-10413.cif.gz emd-10413.cif.gz | 8.7 KB | ||
| その他 |  emd_10413_half_map_1.map.gz emd_10413_half_map_1.map.gz emd_10413_half_map_2.map.gz emd_10413_half_map_2.map.gz | 194.1 MB 194.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10413 http://ftp.pdbj.org/pub/emdb/structures/EMD-10413 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10413 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10413 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_10413_validation.pdf.gz emd_10413_validation.pdf.gz | 362.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_10413_full_validation.pdf.gz emd_10413_full_validation.pdf.gz | 361.6 KB | 表示 | |
| XML形式データ |  emd_10413_validation.xml.gz emd_10413_validation.xml.gz | 19.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10413 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10413 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10413 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-10413 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10413.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10413.map.gz / 形式: CCP4 / 大きさ: 244.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | local resolution filtered map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
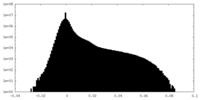
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.05 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
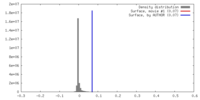
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: half map 1
| ファイル | emd_10413_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 1 | ||||||||||||
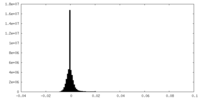
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 2
| ファイル | emd_10413_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 2 | ||||||||||||
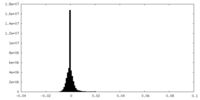
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SAGA Tra1 module
| 全体 | 名称: SAGA Tra1 module |
|---|---|
| 要素 |
|
-超分子 #1: SAGA Tra1 module
| 超分子 | 名称: SAGA Tra1 module / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 450 KDa |
-分子 #1: Transcription factor SPT20
| 分子 | 名称: Transcription factor SPT20 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 67.880312 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSANSPTGND PHVFGIPVNA TPSNMGSPGS PVNVPPPMNP AVANVNHPVM RTNSNSNANE GTRTLTREQI QQLQQRQRLL LQQRLLEQQ RKQQALQNYE AQFYQMLMTL NKRPKRLYNF VEDADSILKK YEQYLHSFEF HIYENNYKIC APANSRLQQQ Q KQPELTSD ...文字列: MSANSPTGND PHVFGIPVNA TPSNMGSPGS PVNVPPPMNP AVANVNHPVM RTNSNSNANE GTRTLTREQI QQLQQRQRLL LQQRLLEQQ RKQQALQNYE AQFYQMLMTL NKRPKRLYNF VEDADSILKK YEQYLHSFEF HIYENNYKIC APANSRLQQQ Q KQPELTSD GLILTKNNET LKEFLEYVAR GRIPDAIMEV LRDCNIQFYE GNLILQVYDH TNTVDVTPKE NKPNLNSSSS PS NNNSTQD NSKIQQPSEP NSGVANTGAN TANKKASFKR PRVYRTLLKP NDLTTYYDMM SYADNARFSD SIYQQFESEI LTL TKRNLS LSVPLNPYEH RDMLEETAFS EPHWDSEKKS FIHEHRAEST REGTKGVVGH IEERDEFPQH SSNYEQLMLI MNER TTTIT NSTFAVSLTK NAMEIASSSS NGVRGASSST SNSASNTRNN SLANGNQVAL AAAAAAAAVG STMGNDNNQF SRLKF IEQW RINKEKRKQQ ALSANINPTP FNARISMTAP LTPQQQLLQR QQQALEQQQN GGAMKNANKR SGNNATSNNN NNNNNL DKP KVKRPRKNAK KSESGTPAPK KKRMTKKKQS ASSTPSSTTM S UniProtKB: SAGA complex subunit SPT20 |
-分子 #2: Transcription initiation factor TFIID subunit 12
| 分子 | 名称: Transcription initiation factor TFIID subunit 12 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 61.144379 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSSNPENSGV NANNNTGTGN ADAITGAQQN MVLQPRQLQE MAAKFRTLLT EARNVGETTP RGKELMFQAA KIKQVYDALT LNRRRQQAA QAYNNTSNSN SSNPASIPTE NVPNSSQQQQ QQQQQTRNNS NKFSNMIKQV LTPEENQEYE KLWQNFQVRH T SIKEKETY ...文字列: MSSNPENSGV NANNNTGTGN ADAITGAQQN MVLQPRQLQE MAAKFRTLLT EARNVGETTP RGKELMFQAA KIKQVYDALT LNRRRQQAA QAYNNTSNSN SSNPASIPTE NVPNSSQQQQ QQQQQTRNNS NKFSNMIKQV LTPEENQEYE KLWQNFQVRH T SIKEKETY LKQNIDRLEQ EINKQTDEGP KQQLQEKKIE LLNDWKVLKI EYTKLFNNYQ NSKKTFYVEC ARHNPALHKF LQ ESTQQQR VQQQRVQQQQ QQQQQQQQQQ QQQQQQQQQR QGQNQRKISS SNSTEIPSVT GPDALKSQQQ QQNTITATNN PRG NVNTSQ TEQSKAKVTN VNATASMLNN ISSSKSAIFK QTEPAIPISE NISTKTPAPV AYRSNRPTIT GGSAMNASAL NTPA TTKLP PYEMDTQRVM SKRKLRELVK TVGIDEGDGE TVIDGDVEEL LLDLADDFVT NVTAFSCRLA KHRKSDNLEA RDIQL HLER NWNIRIPGYS ADEIRSTRKW NPSQNYNQKL QSITSDKVAA AKNNGNNVAS LNTKK UniProtKB: SAGA complex/transcription factor TFIID complex subunit TAF12 |
-分子 #3: Transcription-associated protein 1
| 分子 | 名称: Transcription-associated protein 1 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 433.677281 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSLTEQIEQF ASRFRDDDAT LQSRYSTLSE LYDIMELLNS PEDYHFFLQA VIPLLLNQLK EVPISYDAHS PEQKLRNSML DIFNRCLMN QTFQPYAMEV LEFLLSVLPK ENEENGILCM KVLTTLFKSF KSILQDKLDS FIRIIIQIYK NTPNLINQTF Y EAGKAEQG ...文字列: MSLTEQIEQF ASRFRDDDAT LQSRYSTLSE LYDIMELLNS PEDYHFFLQA VIPLLLNQLK EVPISYDAHS PEQKLRNSML DIFNRCLMN QTFQPYAMEV LEFLLSVLPK ENEENGILCM KVLTTLFKSF KSILQDKLDS FIRIIIQIYK NTPNLINQTF Y EAGKAEQG DLDSPKEPQA DELLDEFSKN DEEKDFPSKQ SSTEPRFENS TSSNGLRSSM FSFKILSECP ITMVTLYSSY KQ LTSTSLP EFTPLIMNLL NIQIKQQQEA REQAESRGEH FTSISTEIIN RPAYCDFILA QIKATSFLAY VFIRGYAPEF LQD YVNFVP DLIIRLLQDC PSELSSARKE LLHATRHILS TNYKKLFLPK LDYLFDERIL IGNGFTMHET LRPLAYSTVA DFIH NIRSE LQLSEIEKTI KIYTGYLLDE SLALTVQIMS AKLLLNLVER ILKLGKENPQ EAPRAKKLLM IIIDSYMNRF KTLNR QYDT IMKYYGRYET HKKEKAEKLK NSIQDNDKES EEFMRKVLEP SDDDHLMPQP KKEDINDSPD VEMTESDKVV KNDVEM FDI KNYAPILLLP TPTNDPIKDA FYLYRTLMSF LKTIIHDLKV FNPPPNEYTV ANPKLWASVS RVFSYEEVIV FKDLFHE CI IGLKFFKDHN EKLSPETTKK HFDISMPSLP VSATKDAREL MDYLAFMFMQ MDNATFNEII EQELPFVYER MLEDSGLL H VAQSFLTSEI TSPNFAGILL RFLKGKLKDL GNVDFNTSNV LIRLFKLSFM SVNLFPNINE VVLLPHLNDL ILNSLKYST TAEEPLVYFY LIRTLFRSIG GGRFENLYRS IKPILQVLLQ SLNQMILTAR LPHERELYVE LCITVPVRLS VLAPYLPFLM KPLVFALQQ YPDLVSQGLR TLELCIDNLT AEYFDPIIEP VIDDVSKALF NLLQPQPFNH AISHNVVRIL GKLGGRNRQF L KPPTDLTE KTELDIDAIA DFKINGMPED VPLSVTPGIQ SALNILQSYK SDIHYRKSAY KYLTCVLLLM TKSSAEFPTN YT ELLKTAV NSIKLERIGI EKNFDLEPTV NKRDYSNQEN LFLRLLESVF YATSIKELKD DAMDLLNNLL DHFCLLQVNT TLL NKRNYN GTFNIDLKNP NFMLDSSLIL DAIPFALSYY IPEVREVGVL AYKRIYEKSC LIYGEELALS HSFIPELAKQ FIHL CYDET YYNKRGGVLG IKVLIDNVKS SSVFLKKYQY NLANGLLFVL KDTQSEAPSA ITDSAEKLLI DLLSITFADV KEEDL GNKV LENTLTDIVC ELSNANPKVR NACQKSLHTI SNLTGIPIVK LMDHSKQFLL SPIFAKPLRA LPFTMQIGNV DAITFC LSL PNTFLTFNEE LFRLLQESIV LADAEDESLS TNIQKTTEYS TSEQLVQLRI ACIKLLAIAL KNEEFATAQQ GNIRIRI LA VFFKTMLKTS PEIINTTYEA LKGSLAENSK LPKELLQNGL KPLLMNLSDH QKLTVPGLDA LSKLLELLIA YFKVEIGR K LLDHLTAWCR VEVLDTLFGQ DLAEQMPTKI IVSIINIFHL LPPQADMFLN DLLLKVMLLE RKLRLQLDSP FRTPLARYL NRFHNPVTEY FKKNMTLRQL VLFMCNIVQR PEAKELAEDF EKELDNFYDF YISNIPKNQV RVVSFFTNMV DLFNTMVITN GDEWLKKKG NMILKLKDML NLTLKTIKEN SFYIDHLQLN QSIAKFQALY LRFTELSERD QNPLLLDFID FSFSNGIKAS Y SLKKFIFH NIIASSNKEK QNNFINDATL FVLSDKCLDA RIFVLKNVIN STLIYEVATS GSLKSYLVED KKPKWLELLH NK IWKNSNA ILAYDVLDHH DLFRFELLQL SAIFIKADPE IIAEIKKDII KFCWNFIKLE DTLIKQSAYL VTSYFISKFD FPI KVVTQV FVALLRSSHV EARYLVKQSL DVLTPVLHER MNAAGTPDTW INWVKRVMVE NSSSQNNILY QFLISHPDLF FNSR DLFIS NIIHHMNKIT FMSNSNSDSH TLAIDLASLI LYWENKTLEI TNVNNTKTDS DGDVVMSDSK SDINPVEADT TAIIV DANN NSPISLHLRE ACTAFLIRYV CASNHRAIET ELGLRAINIL SELISDKHWT NVNVKLVYFE KFLIFQDLDS ENILYY CMN ALDVLYVFFK NKTKEWIMEN LPTIQNLLEK CIKSDHHDVQ EALQKVLQVI MKAIKAQGVS VIIEEESPGK TFIQMLT SV ITQDLQETSS VTAGVTLAWV LFMNFPDNIV PLLTPLMKTF SKLCKDHLSI SQPKDAMALE EARITTKLLE KVLYILSL K VSLLGDSRRP FLSTVALLID HSMDQNFLRK IVNMSRSWIF NTEIFPTVKE KAAILTKMLA FEIRGEPSLS KLFYEIVLK LFDQEHFNNT EITVRMEQPF LVGTRVEDIG IRKRFMTILD NSLERDIKER LYYVIRDQNW EFIADYPWLN QALQLLYGSF NREKELSLK NIYCLSPPSI LQEYLPENAE MVTEVNDLEL SNFVKGHIAS MQGLCRIISS DFIDSLIEIF YQDPKAIHRA W VTLFPQVY KSIPKNEKYG FVRSIITLLS KPYHTRQISS RTNVINMLLD SISKIESLEL PPHLVKYLAI SYNAWYQSIN IL ESIQSNT SIDNTKIIEA NEDALLELYV NLQEEDMFYG LWRRRAKYTE TNIGLSYEQI GLWDKAQQLY EVAQVKARSG ALP YSQSEY ALWEDNWIQC AEKLQHWDVL TELAKHEGFT DLLLECGWRV ADWNSDRDAL EQSVKSVMDV PTPRRQMFKT FLAL QNFAE SRKGDQEVRK LCDEGIQLSL IKWVSLPIRY TPAHKWLLHG FQQYMEFLEA TQIYANLHTT TVQNLDSKAQ EIKRI LQAW RDRLPNTWDD VNMWNDLVTW RQHAFQVINN AYLPLIPALQ QSNSNSNINT HAYRGYHEIA WVINRFAHVA RKHNMP DVC ISQLARIYTL PNIEIQEAFL KLREQAKCHY QNMNELTTGL DVISNTNLVY FGTVQKAEFF TLKGMFLSKL RAYEEAN QA FATAVQIDLN LAKAWAQWGF FNDRRLSEEP NNISFASNAI SCYLQAAGLY KNSKIRELLC RILWLISIDD ASGMLTNA F DSFRGEIPVW YWITFIPQLL TSLSHKEANM VRHILIRIAK SYPQALHFQL RTTKEDFAVI QRQTMAVMGD KPDTNDRNG RRQPWEYLQE LNNILKTAYP LLALSLESLV AQINDRFKST TDEDLFRLIN VLLIDGTLNY NRLPFPRKNP KLPENTEKNL VKFSTTLLA PYIRPKFNAD FIDNKPDYET YIKRLRYWRR RLENKLDRAS KKENLEVLCP HLSNFHHQKF EDIEIPGQYL L NKDNNVHF IKIARFLPTV DFVRGTHSSY RRLMIRGHDG SVHSFAVQYP AVRHSRREER MFQLYRLFNK SLSKNVETRR RS IQFNLPI AIPLSPQVRI MNDSVSFTTL HEIHNEFCKK KGFDPDDIQD FMADKLNAAH DDALPAPDMT ILKVEIFNSI QTM FVPSNV LKDHFTSLFT QFEDFWLFRK QFASQYSSFV FMSYMMMINN RTPHKIHVDK TSGNVFTLEM LPSRFPYERV KPLL KNHDL SLPPDSPIFH NNEPVPFRLT PNIQSLIGDS ALEGIFAVNL FTISRALIEP DNELNTYLAL FIRDEIISWF SNLHR PIIE NPQLREMVQT NVDLIIRKVA QLGHLNSTPT VTTQFILDCI GSAVSPRNLA RTDVNFMPWF UniProtKB: SAGA complex/NuA4 acetyltransferase complex subunit TRA1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
詳細: Solution were made from stock solution | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: blot for 4 seconds before plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均露光時間: 9.0 sec. / 平均電子線量: 42.45 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 107.1 / 当てはまり具合の基準: Correlation coefficient |
|---|---|
| 得られたモデル |  PDB-6t9j: |
 ムービー
ムービー コントローラー
コントローラー



























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)