+検索条件
-Structure paper
| タイトル | Auxiliary subunits reshape structural asymmetry and functional plasticity in heterotetrameric GluA1/A2 AMPA receptor core. |
|---|---|
| ジャーナル・号・ページ | Nat Commun, Year 2026 |
| 掲載日 | 2026年3月28日 |
 著者 著者 | Laura Y Yen / Thomas P Newton / Maria V Yelshanskaya / Muhammed Aktolun / Shanti Pal Gangwar / Rasmus P Clausen / Maria G Kurnikova / Alexander I Sobolevsky /   |
| PubMed 要旨 | AMPA-subtype ionotropic glutamate receptors (AMPARs) mediate the fast component of excitatory neurotransmission. They govern synaptic plasticity that underlies learning and memory, while their ...AMPA-subtype ionotropic glutamate receptors (AMPARs) mediate the fast component of excitatory neurotransmission. They govern synaptic plasticity that underlies learning and memory, while their dysregulation is implicated in numerous neurological disorders. The functional diversity of AMPARs arises from variations in their subunit composition and also their association with auxiliary subunits. While multiple structures of homomeric AMPARs have been reported, structural information for the heteromeric core - particularly in the absence of auxiliary subunits, which would serve as a functional and structural baseline - has been limited. Here, we report cryo-electron microscopy structures of GluA1/A2, the most abundant AMPAR di-heteromer in the brain, in the closed, open, and desensitized states. Using molecular dynamics (MD) simulations and cross-correlating structural and functional information, we find that auxiliary subunits increase the diameter of channel pore, which corresponds to larger conductance. Likewise, we find that recovery from desensitization slows with greater disruption of two-fold rotational symmetry of the ligand-binding domain dimer in the desensitized state. Both receptor activation and desensitization vary with the type and number of associated auxiliary proteins. These structures offer a foundation for uncovering how auxiliary subunits reshape structural asymmetry and functional plasticity in heterotetrameric AMPARs. |
 リンク リンク |  Nat Commun / Nat Commun /  PubMed:41904128 PubMed:41904128 |
| 手法 | EM (単粒子) |
| 解像度 | 3.13 - 4.91 Å |
| 構造データ |  EMDB-70909: Heteromeric GluA1/A2 in the inactive state, consensus refinement of LBD-TMD  EMDB-70910: Heteromeric GluA1/A2 in the inactive state, transmembrane domain (TMD)  EMDB-70911: Heteromeric GluA1/A2 in the inactive state, ligand binding domain (LBD) EMDB-70912, PDB-9ovt:  EMDB-70913: Heteromeric GluA1/A2 in the activated state, consensus refinement of ATD-LBD-TMD  EMDB-70914: Heteromeric GluA1/A2 in the activated state, ligand binding domain (LBD)  EMDB-70915: Heteromeric GluA1/A2 in the activated state, transmembrane domain (TMD)  EMDB-70916: Heteromeric GluA1/A2-CNIH1 in the activated state, consensus refinement of LBD-TMD  EMDB-70917: Heteromeric GluA1/A2-CNIH1 in the activated state, ligand binding domain (LBD)  EMDB-70918: Heteromeric GluA1/A2-CNIH1 in the activated state, transmembrane domain (TMD) EMDB-70919, PDB-9ovu: EMDB-70920, PDB-9ovv:  EMDB-70921: Heteromeric GluA1/A2 in the desensitized state, consensus refinement of ATD-LBD-TMD  EMDB-70922: Heteromeric GluA1/A2 in the desensitized state, amino-terminal domain (ATD)  EMDB-70923: Heteromeric GluA1/A2 in the desensitized state, ligand binding domain (LBD)  EMDB-70924: Heteromeric GluA1/A2 in the desensitized state, transmembrane domain (TMD) EMDB-70925, PDB-9ovw:  EMDB-75274: Heteromeric GluA1/A2 in the activated state, amino-terminal domain (ATD) |
| 化合物 | 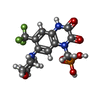 ChemComp-ZK1:  ChemComp-NA:  ChemComp-HOH:  ChemComp-GLU: 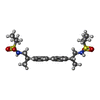 ChemComp-FWF: 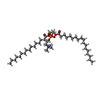 ChemComp-POV: 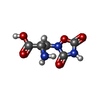 ChemComp-QUS: |
| 由来 |
|
 キーワード キーワード | MEMBRANE PROTEIN / GluA1A2 heterotetramer ZK iGluR / GluA1A2 heterotetramer active iGluR / GluA1A2-CNIH2 heterotetramer active iGluR / GluA1A2 heterotetramer quisqualate iGluR |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について












 homo sapiens (ヒト)
homo sapiens (ヒト)