-検索条件
-検索結果
検索 (著者・登録者: zhou & cc)の結果191件中、1から50件目までを表示しています

EMDB-36466: 
FCP trimer in diatom Thalassiosira pseudonana

EMDB-43529: 
L5A7 Fab bound to Indonesia2005 Hemagglutinin

EMDB-43545: 
L5A7 Fab bound to 28H6E11 anti-idiotype Fab

PDB-8vue: 
L5A7 Fab bound to Indonesia2005 Hemagglutinin

PDB-8vuz: 
L5A7 Fab bound to 28H6E11 anti-idiotype Fab

EMDB-44496: 
Cryo-EM co-structure of AcrB with the CU032 efflux pump inhibitor

EMDB-44500: 
Cryo-EM co-structure of AcrB with the EPM35 efflux pump inhibitor

EMDB-44501: 
Cryo-EM co-structure of AcrB with the CU232 efflux pump inhibitor
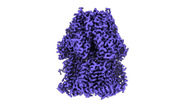
EMDB-44506: 
Cryo-EM co-structure of AcrB with CU244

EMDB-41374: 
Antibody N3-1 bound to RBDs in the up and down conformations

EMDB-41382: 
Antibody N3-1 bound to RBD in the up conformation

EMDB-41399: 
Antibody N3-1 bound to SARS-CoV-2 spike

PDB-8tm1: 
Antibody N3-1 bound to RBDs in the up and down conformations

PDB-8tma: 
Antibody N3-1 bound to RBD in the up conformation

EMDB-41144: 
Cryo-EM Structure of GPR61-G protein complex stabilized by scFv16

EMDB-41145: 
Cryo-EM Structure of GPR61-

PDB-8tb0: 
Cryo-EM Structure of GPR61-G protein complex stabilized by scFv16

PDB-8tb7: 
Cryo-EM Structure of GPR61-
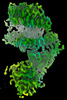
EMDB-29530: 
SARS-CoV-2 XBB.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
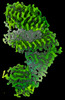
EMDB-29531: 
SARS-CoV-2 BQ.1.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
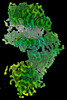
EMDB-40240: 
SARS-CoV-2 BN.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8fxb: 
SARS-CoV-2 XBB.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8fxc: 
SARS-CoV-2 BQ.1.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8s9g: 
SARS-CoV-2 BN.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

EMDB-33883: 
Structural basis of human PRPS2 filaments

EMDB-34226: 
SARS-CoV-2 BA.2 spike RBD in complex bound with VacBB-551

EMDB-34935: 
Cryo-EM structure of a SIN3/HDAC complex from budding yeast
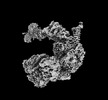
EMDB-34936: 
Cryo-EM map of the Rpd3L complex from the Rxt1-Flag dataset

EMDB-34937: 
Cryo-EM map of the Rpd3L complex in Sin3 part

EMDB-34938: 
Cryo-EM map of the Rpd3L complex in Dep1 region
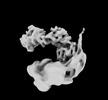
EMDB-34939: 
Cryo-EM map of the Rpd3L complex in Ume1 part
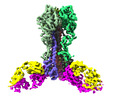
EMDB-27139: 
Cryo-EM structure of the VRC321 clinical trial, vaccine-elicited, human antibody 1B06 in complex with a stabilized NC99 HA trimer

PDB-8d21: 
Cryo-EM structure of the VRC321 clinical trial, vaccine-elicited, human antibody 1B06 in complex with a stabilized NC99 HA trimer

EMDB-27243: 
Cryo-EM map of MORF-WHs in complex with 197bp nucleosome aided by scFv

EMDB-26044: 
H10ssF: ferritin-based nanoparticle displaying H10 hemagglutinin stabilized stem epitopes

EMDB-32497: 
SARS-CoV-2 spike in complex with the ZB8 neutralizing antibody Fab (focused refinement on Fab-RBD)

EMDB-32498: 
SARS-CoV-2 spike in complex with the ZB8 neutralizing antibody Fab (3U)

EMDB-32499: 
SARS-CoV-2 spike in complex with the ZB8 neutralizing antibody Fab (2u1d)

EMDB-26028: 
Structure of Enterobacter cloacae Cap2-CdnD02 2:2 complex

EMDB-26066: 
Structure of Enterobacter cloacae Cap2-CdnD02 2:1 complex

PDB-7to3: 
Structure of Enterobacter cloacae Cap2-CdnD02 2:2 complex

PDB-7tqd: 
Structure of Enterobacter cloacae Cap2-CdnD02 2:1 complex

EMDB-32541: 
Structural basis for ligand binding modes of CTP synthase

EMDB-32542: 
Structural basis for ligand binding modes of CTP synthase

EMDB-28558: 
SARS-CoV-2 BA.1 spike ectodomain trimer in complex with the S2X324 neutralizing antibody Fab fragment (local refinement of the RBD and S2X324)

EMDB-28559: 
SARS-CoV-2 Omicron BA.1 spike ectodomain trimer in complex with the S2X324 neutralizing antibody Fab fragment

PDB-8erq: 
SARS-CoV-2 BA.1 spike ectodomain trimer in complex with the S2X324 neutralizing antibody Fab fragment (local refinement of the RBD and S2X324)

PDB-8err: 
SARS-CoV-2 Omicron BA.1 spike ectodomain trimer in complex with the S2X324 neutralizing antibody Fab fragment

EMDB-24693: 
SARS-CoV-2-6P-Mut7 S protein (C3 symmetry)

EMDB-24694: 
SARS-CoV-2-6P-Mut7 S protein (asymmetric)
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
