-検索条件
-検索結果
検索 (著者・登録者: weis & wi)の結果109件中、1から50件目までを表示しています

EMDB-28198: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with LLNL-199

EMDB-28199: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with 2130-1-0114-112

PDB-8ekd: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with 2130-1-0114-112

EMDB-16242: 
Cryo-EM structure of RANBP10-CTLH SR4 complex

EMDB-16243: 
Cryo-EM map of ARMC8-specific nanobody bound to CTLH-SR4

EMDB-27703: 
Structure of RBD directed antibody DH1047 in complex with SARS-CoV-2 spike: Local refinement of RBD-Fab interace

PDB-8dtk: 
Structure of RBD directed antibody DH1047 in complex with SARS-CoV-2 spike: Local refinement of RBD-Fab interace
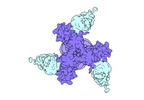
EMDB-27706: 
Vaccine elicited Antibody MU89 bound to CH848.D949.10.17_N133D_N138T.DS.SOSIP.664 HIV-1 Env trimer
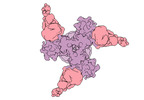
EMDB-27776: 
Vaccine elicited Antibody MU89+S27Y bound to CH848.D949.10.17_N133D_N138T.DS.SOSIP.664 HIV-1 Env trimer

PDB-8dto: 
Vaccine elicited Antibody MU89 bound to CH848.D949.10.17_N133D_N138T.DS.SOSIP.664 HIV-1 Env trimer

PDB-8dy6: 
Vaccine elicited Antibody MU89+S27Y bound to CH848.D949.10.17_N133D_N138T.DS.SOSIP.664 HIV-1 Env trimer

EMDB-29044: 
Structure of Zanidatamab bound to HER2

EMDB-14630: 
Membrane-bound CHMP2A-CHMP3 filament (430 Angstrom diameter)

EMDB-14631: 
Membrane-bound CHMP2A-CHMP3 filament (410 Angstrom diameter)

PDB-7zcg: 
CHMP2A-CHMP3 heterodimer (430 Angstrom diameter)

PDB-7zch: 
CHMP2A-CHMP3 heterodimer (410 Angstrom diameter)

EMDB-27779: 
Structure of the SARS-CoV-2 spike glycoprotein S2 subunit

PDB-8dya: 
Structure of the SARS-CoV-2 spike glycoprotein S2 subunit

EMDB-26522: 
SARS-CoV-2 6P Mut7 in complex with K398.25 Fab

EMDB-26523: 
SARS-CoV-1 in complex with K398.25 Fab

EMDB-26524: 
SARS-CoV-2 6P Mut7 in complex with K398.16 Fab
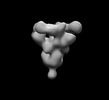
EMDB-26525: 
SARS-CoV-2 6P Mut7 in complex with K398.16 Fab (3 bound)

EMDB-26526: 
SARS-CoV-1 in complex with K398.16 Fab

EMDB-26527: 
SARS-CoV-2 6P Mut7 in complex with K288.2 Fab

EMDB-26528: 
SARS-CoV-2 6P Mut7 in complex with K398.8 Fab

EMDB-26529: 
SARS-CoV-2 6P Mut7 in complex with K398.8 Fab (2 bound)

EMDB-26530: 
SARS-CoV-2 6P Mut7 in complex with K398.18 Fab

EMDB-26531: 
SARS-CoV-2 6P Mut7 in complex with K398.18 Fabs (2 bound)

EMDB-26532: 
SARS-CoV-2 6P Mut7 in complex with K398.22 Fab
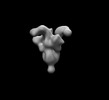
EMDB-26533: 
SARS-CoV-2 6P Mut7 in complex with K398.22 Fab (2 bound)

EMDB-26534: 
SARS-CoV-1 in complex with K398.8 Fab

EMDB-26535: 
SARS-CoV-1 in complex with K398.8 Fab (2 bound)

EMDB-26536: 
SARS-CoV-1 in complex with K398.18 Fab (2 bound)

EMDB-26537: 
SARS-CoV-1 in complex with K398.18 Fab (3 bound)

EMDB-26538: 
SARS-CoV-1 in complex with K288.2 Fab

EMDB-26539: 
SARS-CoV-1 in complex with K398.22 Fab

EMDB-11953: 
SARS-CoV-2 S 2P trimer in complex with monovalent DARPin R2 (State 1) - Composite Map

EMDB-11954: 
SARS-CoV-2 S 2P trimer in complex with monovalent DARPin R2 (State 2)

EMDB-14810: 
SARS-CoV-2 S 2P trimer in complex with monovalent DARPin R2 (State 1) - Consensus Map

EMDB-14811: 
SARS-CoV-2 S 2P trimer in complex with monovalent DARPin R2 (State 1) - Focused Refinement

EMDB-13776: 
Structure of formaldehyde cross-linked SARS-CoV-2 S glycoprotein

PDB-7q1z: 
Structure of formaldehyde cross-linked SARS-CoV-2 S glycoprotein

EMDB-23480: 
Cryo-EM structure of llama J3 VHH antibody in complex with HIV-1 Env BG505 DS-SOSIP.664

PDB-7lpn: 
Cryo-EM structure of llama J3 VHH antibody in complex with HIV-1 Env BG505 DS-SOSIP.664

EMDB-12901: 
Cryo-EM structure of pyrococcus furiosus apoferritin in nanofluidic channels

EMDB-12902: 
Electron cryo-tomogram of pyrococcus furiosus apoferritin in nanofluidic channels

EMDB-12903: 
Cryo-EM structure of tobacco mosaic virus in nanofluidic channels

EMDB-12914: 
Electron cryo-tomogram of tobacco mosaic virus in nanofluidic channels

EMDB-12915: 
Cryo-EM structure of T20S proteasome in nanofluidic channels

EMDB-12917: 
Electron cryo-tomogram of T20S proteasome in nanofluidic channels
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
