-検索条件
-検索結果
検索 (著者・登録者: shen & qt)の結果78件中、1から50件目までを表示しています

EMDB-31367: 
Structure of mumps virus nucleoprotein without C-arm

EMDB-37957: 
Cryo-EM map for Mumps Virus L Protein Bound by Phosphoprotein Tetramer

EMDB-37958: 
Cryo-EM map for Mumps Virus L Protein Bound by Phosphoprotein Tetramer (Focused map for CD-MTase-CTD)

EMDB-37959: 
Cryo-EM map for Mumps Virus L Protein Bound by Phosphoprotein Tetramer (Focused map for RdRp-PRNTase)

EMDB-37960: 
Cryo-EM map for Mumps Virus L Protein Bound by Phosphoprotein Tetramer (Focused map for tetrameric phosphoproteins)

EMDB-37961: 
Cryo-EM map for Mumps Virus L Protein (State 2) Bound by Phosphoprotein Tetramer

EMDB-37962: 
Cryo-EM map for Mumps Virus L protein (state2) Bound by Phosphoprotein Tetramer (Focused for tetrameric phosphoprotein)

EMDB-37964: 
Structure of the Mumps Virus L Protein (state2) Bound by Phosphoprotein Tetramer (composite map)

EMDB-37416: 
Cryo-EM structure of Snf7 N-terminal domain in outer coils of spiral polymers

EMDB-37417: 
CryoEM structure of Snf7 N-terminal domain in the inner coils of spiral

EMDB-35864: 
Structure of the Mumps Virus L Protein Bound by Phosphoprotein Tetramer (composite map)

EMDB-35865: 
Structure of the Mumps Virus L Protein (state2) Bound by Phosphoprotein Tetramer
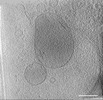
EMDB-39012: 
Representative tomogram of primary glioblastoma stem cell with circular inter-mitochondrial junctions.

EMDB-39015: 
Representative tomogram of microglia cell with nanotunnel-like structures resembling mitochondrial fission.
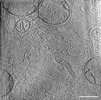
EMDB-39019: 
Representative tomogram of glioblastoma cell with nanotunnel-like structure and inter-mitochondrial junction.

EMDB-39021: 
Representative tomogram of normal human astrocyte with nanotunnel-like structure which is an extension of the mitochondrial outer membrane.

EMDB-39023: 
Representative tomogram of primary glioblastoma differentiated cell with parallel inter-mitochondrial junction.

EMDB-39024: 
Representative tomogram of primary glioblastoma stem cell with clustered mitochondria bearing various long-short axis ratios.

EMDB-37390: 
Cryo-EM structure of peptide free and Gs-coupled GIPR

EMDB-29943: 
Cryo-EM Structure of the Prostaglandin E2 Receptor 4 Coupled to G Protein

EMDB-29944: 
Cryo-EM Structure of the Prostaglandin E2 Receptor 4 Coupled to G Protein

EMDB-29945: 
Cryo-EM Structure of the Prostaglandin E2 Receptor 4 Coupled to G Protein

EMDB-29946: 
Cryo-EM Structure of the Prostaglandin E2 Receptor 3 Coupled to G Protein

EMDB-29935: 
Cryo-EM Structure of the Prostaglandin E Receptor EP4 Coupled to G Protein

EMDB-29940: 
Cryo-EM Structure of the Prostaglandin E2 Receptor 4 Coupled to G Protein

EMDB-33165: 
arch-like and diamond-like structures

EMDB-33162: 
The architecture of the head in oval-shaped WSSV capsids.

EMDB-33166: 
Barrel-like structure of the body

EMDB-33168: 
structure of vp51 in white spot syndrome virus capsid

EMDB-33163: 
3D structure of the base in oval-shaped WSSV capsids

EMDB-33164: 
Cryo-EM models of the plug

EMDB-33167: 
Cryo-EM model of the base and part of the body

EMDB-33170: 
Cryo-EM model of the neck

EMDB-35522: 
Cryo-EM structure of the TUG891 bound GPR120-Giq complex(mask on receptor)

EMDB-35523: 
Cryo-EM structure of the TUG891 bound GPR120-Giq complex(mask on Giq-scFV16 complex)

EMDB-35524: 
Cryo-EM structure of the eicosapentaenoic acid bound GPR120-Gi1 complex(mask on receptor)

EMDB-35525: 
Cryo-EM structure of the eicosapentaenoic acid bound GPR120-Gi1 complex(mask on Gil-scFV16 complex)

EMDB-35529: 
Cryo-EM structure of the TUG891 bound GPR120-Giq complex (consensus map)

EMDB-35533: 
Cryo-EM structure of the eicosapentaenoic acid bound GPR120-Gi complex(consensus map)

EMDB-35356: 
Cryo-EM structure of the 9-hydroxystearic acid bound GPR120-Gi complex

EMDB-35357: 
Cryo-EM structure of the linoleic acid bound GPR120-Gi complex

EMDB-35358: 
Cryo-EM structure of the oleic acid bound GPR120-Gi complex

EMDB-35359: 
Cryo-EM structure of the TUG891 bound GPR120-Gi complex

EMDB-35360: 
Cryo-EM structure of the eicosapentaenoic acid bound GPR120-Gi complex

EMDB-29736: 
Cryo-EM structure of the TUG891 bound GPR120-Giq complex

EMDB-33871: 
Cryo-EM structure of the INSL5-bound human relaxin family peptidereceptor 4(RXFP4)-Gi complex

EMDB-33888: 
Cryo-EM structure of the compound 4-bound human relaxin family peptide receptor 4 (RXFP4)-Gi complex

EMDB-33889: 
Cryo-EM structure of the DC591053-bound human relaxin family peptide receptor 4 (RXFP4)-Gi complex

EMDB-33248: 
Cryo-EM structure of DHEA-ADGRG2-BT-Gs complex

EMDB-33249: 
Cryo-EM structure of DHEA-ADGRG2-FL-Gs complex
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
