-検索条件
-検索結果
検索 (著者・登録者: chun & j)の結果2,039件中、1から50件目までを表示しています

EMDB-39212: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH8.0 (3.23A)

EMDB-39213: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH6.5 (2.82A)

EMDB-39214: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH5.0 (3.52A)

EMDB-39215: 
Cryo-EM structure of Dragon Grouper nervous necrosis virion at pH6.5 (3.12A)

EMDB-39217: 
Cryo-EM structure of Dragon Grouper nervous necrosis virion at pH5.0 (4.36A)

PDB-8yf6: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH8.0 (3.23A)

PDB-8yf7: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH6.5 (2.82A)

PDB-8yf8: 
Cryo-EM structure of Dragon Grouper nervous necrosis virus-like particle at pH5.0 (3.52A)

PDB-8yf9: 
Cryo-EM structure of Dragon Grouper nervous necrosis virion at pH6.5 (3.12A)
EMDB-38080: 
SIRM reconstruction of the MC-45 de novo processed ribosome 50S
EMDB-38081: 
Conventional Reconstruction of the MC-45 de novo processed ribosome 50S
EMDB-38082: 
SIRM reconstruction of the unpublished protein

EMDB-38083: 
The SIRM reconstruction of the MC-40 de novo processed HA-trimer
EMDB-38084: 
The conventional reconstruction of the MC-40 de novo processed HA-trimer

EMDB-38085: 
The SIRM reconstruction of the MC-45 de novo processed PS1

EMDB-38086: 
The conventional reconstruction of the MC-45 de novo processed PS1

EMDB-39299: 
Human resource SGLT1-MAP17 complex
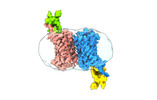
EMDB-36488: 
Structure of Duffy Antigen Receptor for Chemokines (DARC)/ACKR1 in complex with the chemokine, CCL7 (Composite map)

EMDB-37212: 
Structure of Duffy Antigen Receptor for Chemokines (DARC)/ACKR1 in complex with the chemokine, CCL7 (Receptor original map)
EMDB-37214: 
Structure of Duffy Antigen Receptor for Chemokines (DARC)/ACKR1 in complex with the chemokine, CCL7 (Ligand/CCL7 focused map)

PDB-8jps: 
Structure of Duffy Antigen Receptor for Chemokines (DARC)/ACKR1 in complex with the chemokine, CCL7 (Composite map)

EMDB-37515: 
Cryo-EM structure of inward-open state human norepinephrine transporter NET bound with antidepressant desipramine in KCl condition.

EMDB-37520: 
Cryo-EM structure of inward-open state human norepinephrine transporter NET bound with norepinephrine in nanodisc.

EMDB-39729: 
Cryo-EM structure of human norepinephrine transporter NET in the presence of the antidepressant atomoxetine in an outward-open state at resolution of 3.4 angstrom.

PDB-8wgr: 
Cryo-EM structure of inward-open state human norepinephrine transporter NET bound with antidepressant desipramine in KCl condition.

PDB-8wgx: 
Cryo-EM structure of inward-open state human norepinephrine transporter NET bound with norepinephrine in nanodisc.

PDB-8z1l: 
Cryo-EM structure of human norepinephrine transporter NET in the presence of the antidepressant atomoxetine in an outward-open state at resolution of 3.4 angstrom.

EMDB-18833: 
INTS9-INTS11-BRAT1-WDR73 complex

EMDB-18834: 
INTS9-INTS11-BRAT1 complex

EMDB-18839: 
Integrator cleavage module assembly intermediate

PDB-8r22: 
INTS9-INTS11-BRAT1-WDR73 complex

PDB-8r23: 
INTS9-INTS11-BRAT1 complex

PDB-8r2d: 
Integrator cleavage module assembly intermediate

EMDB-38609: 
The Cryo-EM structure of IL-12, receptor subunit beta-1 and receptor subunit beta-2 complex

EMDB-39311: 
The Cryo-EM structure of IL-12, receptor subunit beta-1 and receptor subunit beta-2 complex, local refinement
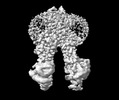
EMDB-38532: 
Cryo-EM structure of human ABCC4

PDB-8xok: 
Cryo-EM structure of human ABCC4

EMDB-38533: 
Cryo-EM structure of human ABCC4 with ANP bound in NBD1

EMDB-38534: 
Cryo-EM structure of human ABCC4 in complex with ANP-bound in NBD1 and METHOTREXATE

PDB-8xol: 
Cryo-EM structure of human ABCC4 with ANP bound in NBD1

PDB-8xom: 
Cryo-EM structure of human ABCC4 in complex with ANP-bound in NBD1 and METHOTREXATE

EMDB-37546: 
Spike Trimer of BA.2.86 in complex with one hACE2

EMDB-37548: 
Spike Trimer of BA.2.86 in complex with two hACE2s

EMDB-37549: 
Spike Trimer of BA.2.86 with three RBDs down

EMDB-37550: 
Spike Trimer of BA.2.86 with single RBD up

EMDB-38049: 
SARS-CoV-2 JN.1 Spike

EMDB-38072: 
SARS-CoV-2 BA.2.75 Spike with K356T mutation (3 RBD down)

EMDB-38073: 
SARS-CoV-2 BA.2.75 Spike with K356T mutation (1 RBD up)

EMDB-38681: 
BA.2.86 Spike Trimer in complex with heparan sulfate

EMDB-38682: 
JN.1 Spike Trimer in complex with heparan sulfate
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
