[English] 日本語
 Yorodumi
Yorodumi- PDB-5bqb: Crystal structure of Norrin, a Wnt signalling activator, Crystal ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 5bqb | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal structure of Norrin, a Wnt signalling activator, Crystal Form III | ||||||||||||
 Components Components | Norrin | ||||||||||||
 Keywords Keywords |  SIGNALING PROTEIN / SIGNALING PROTEIN /  Wnt signalling pathway / Wnt signalling pathway /  Norrie disease protein / cystine-knot like growth factor / ligand for Frizzled 4 receptor Norrie disease protein / cystine-knot like growth factor / ligand for Frizzled 4 receptor | ||||||||||||
| Function / homology |  Function and homology information Function and homology informationretina blood vessel maintenance / cone retinal bipolar cell differentiation / Norrin signaling pathway / extracellular matrix-cell signaling / re-entry into mitotic cell cycle / retinal blood vessel morphogenesis / retinal rod cell differentiation / ubiquitin-dependent endocytosis / retina layer formation / retinal pigment epithelium development ...retina blood vessel maintenance / cone retinal bipolar cell differentiation / Norrin signaling pathway / extracellular matrix-cell signaling / re-entry into mitotic cell cycle / retinal blood vessel morphogenesis / retinal rod cell differentiation / ubiquitin-dependent endocytosis / retina layer formation / retinal pigment epithelium development / establishment of blood-retinal barrier / microglial cell proliferation / glycine metabolic process / endothelial cell differentiation / dendritic spine development / protein targeting to lysosome / establishment of blood-brain barrier / vacuole organization / microglia differentiation /  frizzled binding / optic nerve development / retinal ganglion cell axon guidance / lens development in camera-type eye / exploration behavior / frizzled binding / optic nerve development / retinal ganglion cell axon guidance / lens development in camera-type eye / exploration behavior /  action potential / smoothened signaling pathway / action potential / smoothened signaling pathway /  decidualization / canonical Wnt signaling pathway / response to axon injury / blood vessel remodeling / glutathione metabolic process / decidualization / canonical Wnt signaling pathway / response to axon injury / blood vessel remodeling / glutathione metabolic process /  tricarboxylic acid cycle / tricarboxylic acid cycle /  visual perception / transforming growth factor beta receptor signaling pathway / phosphatidylinositol 3-kinase/protein kinase B signal transduction / visual perception / transforming growth factor beta receptor signaling pathway / phosphatidylinositol 3-kinase/protein kinase B signal transduction /  cytokine activity / mitotic cell cycle / cytokine activity / mitotic cell cycle /  nervous system development / cellular response to hypoxia / collagen-containing extracellular matrix / nervous system development / cellular response to hypoxia / collagen-containing extracellular matrix /  angiogenesis / neuron apoptotic process / transcription by RNA polymerase II / protein ubiquitination / angiogenesis / neuron apoptotic process / transcription by RNA polymerase II / protein ubiquitination /  inflammatory response / positive regulation of DNA-templated transcription / inflammatory response / positive regulation of DNA-templated transcription /  cell surface / protein homodimerization activity / cell surface / protein homodimerization activity /  extracellular space extracellular spaceSimilarity search - Function | ||||||||||||
| Biological species |   Homo sapiens (human) Homo sapiens (human) | ||||||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 2.3 Å molecular replacement / Resolution: 2.3 Å | ||||||||||||
 Authors Authors | Chang, T.-H. / Hsieh, F.-L. / Harlos, K. / Jones, E.Y. | ||||||||||||
| Funding support |  United Kingdom, 3items United Kingdom, 3items
| ||||||||||||
 Citation Citation |  Journal: Elife / Year: 2015 Journal: Elife / Year: 2015Title: Structure and functional properties of Norrin mimic Wnt for signalling with Frizzled4, Lrp5/6, and proteoglycan. Authors: Chang, T.H. / Hsieh, F.L. / Zebisch, M. / Harlos, K. / Elegheert, J. / Jones, E.Y. | ||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  5bqb.cif.gz 5bqb.cif.gz | 98.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb5bqb.ent.gz pdb5bqb.ent.gz | 76.6 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  5bqb.json.gz 5bqb.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/bq/5bqb https://data.pdbj.org/pub/pdb/validation_reports/bq/5bqb ftp://data.pdbj.org/pub/pdb/validation_reports/bq/5bqb ftp://data.pdbj.org/pub/pdb/validation_reports/bq/5bqb | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  5bpbC 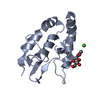 5bpqC  5bpuSC  5bq8C  5bqcC  5bqeC S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein |  / Norrie disease protein / X-linked exudative vitreoretinopathy 2 protein / Norrie disease protein / X-linked exudative vitreoretinopathy 2 proteinMass: 13614.706 Da / Num. of mol.: 4 / Fragment: residues 25-133 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Homo sapiens (human) / Gene: NDP, EVR2 / Plasmid: pHLIgK-STR-8H-SUMO-1D4 / Production host: Homo sapiens (human) / Gene: NDP, EVR2 / Plasmid: pHLIgK-STR-8H-SUMO-1D4 / Production host:   Homo sapiens (human) / References: UniProt: Q00604 Homo sapiens (human) / References: UniProt: Q00604#2: Chemical | ChemComp-CIT /  Citric acid Citric acid#3: Chemical |  Chloride Chloride#4: Water | ChemComp-HOH / |  Water Water |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.68 Å3/Da / Density % sol: 54.14 % |
|---|---|
Crystal grow | Temperature: 294 K / Method: vapor diffusion, sitting drop / Details: 0.1M citrate, pH 5.0, 30% PEG6000 |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Diamond Diamond  / Beamline: I03 / Wavelength: 0.9796 Å / Beamline: I03 / Wavelength: 0.9796 Å | |||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Feb 15, 2014 | |||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||
| Radiation wavelength | Wavelength : 0.9796 Å / Relative weight: 1 : 0.9796 Å / Relative weight: 1 | |||||||||||||||||||||||||||
| Reflection | Resolution: 2.3→44.19 Å / Num. obs: 26073 / % possible obs: 99.2 % / Redundancy: 5.8 % / Biso Wilson estimate: 51.94 Å2 / CC1/2: 0.999 / Rmerge(I) obs: 0.063 / Rpim(I) all: 0.028 / Net I/σ(I): 16.7 / Num. measured all: 151301 | |||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1 / Rejects: 0
|
-Phasing
Phasing | Method:  molecular replacement molecular replacement | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Phasing MR | Model details: Phaser MODE: MR_AUTO
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 5BPU Resolution: 2.3→44.19 Å / FOM work R set: 0.6505 / SU ML: 0.34 / Cross valid method: THROUGHOUT / σ(F): 1.36 / Phase error: 29.23 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 283.09 Å2 / Biso mean: 91.3 Å2 / Biso min: 24.76 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.3→44.19 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj





