+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7cy5 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Crystal Structure of CMD1 in complex with vitamin C | ||||||||||||
 要素 要素 | Maltodextrin-binding protein,5-methylcytosine-modifying enzyme 1 | ||||||||||||
 キーワード キーワード |  TRANSFERASE (転移酵素) / TET / TRANSFERASE (転移酵素) / TET /  Vitamin C (ビタミンC) / Vitamin C (ビタミンC) /  dioxygenase / 5gmC / DNA modification / dioxygenase / 5gmC / DNA modification /  2-oxoglutarate (Α-ケトグルタル酸) 2-oxoglutarate (Α-ケトグルタル酸) | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報methylcytosine to 5-glyceryl-methylcytosine dioxygenase activity /  regulation of photosynthesis / regulation of photosynthesis /  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 / 5-methylcytosine catabolic process / detection of maltose stimulus / 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 / 5-methylcytosine catabolic process / detection of maltose stimulus /  maltose binding / maltose transport complex / maltose transport / maltodextrin transmembrane transport / maltose binding / maltose transport complex / maltose transport / maltodextrin transmembrane transport /  dioxygenase activity ...methylcytosine to 5-glyceryl-methylcytosine dioxygenase activity / dioxygenase activity ...methylcytosine to 5-glyceryl-methylcytosine dioxygenase activity /  regulation of photosynthesis / regulation of photosynthesis /  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 / 5-methylcytosine catabolic process / detection of maltose stimulus / 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 / 5-methylcytosine catabolic process / detection of maltose stimulus /  maltose binding / maltose transport complex / maltose transport / maltodextrin transmembrane transport / maltose binding / maltose transport complex / maltose transport / maltodextrin transmembrane transport /  dioxygenase activity / carbohydrate transmembrane transporter activity / ATP-binding cassette (ABC) transporter complex, substrate-binding subunit-containing / carbohydrate transport / ATP-binding cassette (ABC) transporter complex / cell chemotaxis / outer membrane-bounded periplasmic space / dioxygenase activity / carbohydrate transmembrane transporter activity / ATP-binding cassette (ABC) transporter complex, substrate-binding subunit-containing / carbohydrate transport / ATP-binding cassette (ABC) transporter complex / cell chemotaxis / outer membrane-bounded periplasmic space /  ペリプラズム / iron ion binding / DNA damage response / ペリプラズム / iron ion binding / DNA damage response /  生体膜 / 生体膜 /  細胞核 細胞核類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌)  Chlamydomonas reinhardtii (クラミドモナス) Chlamydomonas reinhardtii (クラミドモナス) | ||||||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.2 Å 分子置換 / 解像度: 2.2 Å | ||||||||||||
 データ登録者 データ登録者 | Li, W. / Zhang, T. / Sun, M. / Ding, J. | ||||||||||||
| 資金援助 |  中国, 3件 中国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Molecular mechanism for vitamin C-derived C 5 -glyceryl-methylcytosine DNA modification catalyzed by algal TET homologue CMD1. 著者: Li, W. / Zhang, T. / Sun, M. / Shi, Y. / Zhang, X.J. / Xu, G.L. / Ding, J. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7cy5.cif.gz 7cy5.cif.gz | 364.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7cy5.ent.gz pdb7cy5.ent.gz | 290.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7cy5.json.gz 7cy5.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/cy/7cy5 https://data.pdbj.org/pub/pdb/validation_reports/cy/7cy5 ftp://data.pdbj.org/pub/pdb/validation_reports/cy/7cy5 ftp://data.pdbj.org/pub/pdb/validation_reports/cy/7cy5 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 98913.453 Da / 分子数: 1 / 断片: dioxygenase,dioxygenase / 変異: D108A, K109A, E198A, N199A, E385A, K388A, D389A / 由来タイプ: 組換発現 詳細: The fusion protein of Maltodextrin-binding protein UNP RESIDUES 27-392), linker, 5-methylcytosine-modifying enzyme 1 (UNP RESIDUES 1-532) and tags 由来: (組換発現)   Escherichia coli (大腸菌), (組換発現) Escherichia coli (大腸菌), (組換発現)   Chlamydomonas reinhardtii (クラミドモナス) Chlamydomonas reinhardtii (クラミドモナス)プラスミド: pET30a-V28E1 / 遺伝子: CMD1, CHLRE_12g553400v5 / 発現宿主:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌)参照: UniProt: A0A376KDN7, UniProt: A0A2K3D5Z7, UniProt: P0AEX9*PLUS, 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; ...参照: UniProt: A0A376KDN7, UniProt: A0A2K3D5Z7, UniProt: P0AEX9*PLUS,  酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; その他の電子対酸化酵素 | ||||
|---|---|---|---|---|---|
| #2: 化合物 | ChemComp-FE /  鉄 鉄 | ||||
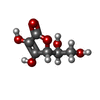
| #3: 糖 | ChemComp-ASC /  ビタミンC ビタミンC | ||||
| #4: 化合物 |  クエン酸 クエン酸#5: 水 | ChemComp-HOH / |  水 水研究の焦点であるリガンドがあるか | Y | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 3.08 Å3/Da / 溶媒含有率: 60.12 % |
|---|---|
結晶化 | 温度: 290 K / 手法: 蒸発脱水法 / pH: 5.6 / 詳細: 2% Tacsimate, 0.1M CIT pH 5.6, 16% PEG 3350 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SSRF SSRF  / ビームライン: BL19U1 / 波長: 0.9785 Å / ビームライン: BL19U1 / 波長: 0.9785 Å |
| 検出器 | タイプ: DECTRIS PILATUS3 S 6M / 検出器: PIXEL / 日付: 2019年6月27日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 0.9785 Å / 相対比: 1 : 0.9785 Å / 相対比: 1 |
| 反射 | 解像度: 2.2→48.38 Å / Num. obs: 55672 / % possible obs: 95.5 % / 冗長度: 4.9 % / CC1/2: 1 / Rmerge(I) obs: 0.084 / Net I/σ(I): 16.3 |
| 反射 シェル | 解像度: 2.2→2.25 Å / 冗長度: 5.1 % / Rmerge(I) obs: 1.03 / Mean I/σ(I) obs: 1.8 / Num. unique obs: 2783 / CC1/2: 0.65 / % possible all: 97.6 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: 7CY4 解像度: 2.2→48.38 Å / Cor.coef. Fo:Fc: 0.952 / Cor.coef. Fo:Fc free: 0.926 / SU B: 15.435 / SU ML: 0.157 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R Free: 0.184 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD / 詳細: U VALUES : WITH TLS ADDED
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 115.3 Å2 / Biso mean: 38.512 Å2 / Biso min: 7.58 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 2.2→48.38 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.201→2.258 Å / Rfactor Rfree error: 0 / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Origin x: 35.1771 Å / Origin y: 25.8259 Å / Origin z: 23.4049 Å
|
 ムービー
ムービー コントローラー
コントローラー

















 PDBj
PDBj