| 登録情報 | データベース: PDB / ID: 1zad
|
|---|
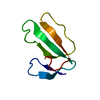
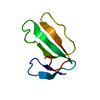
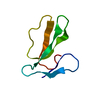
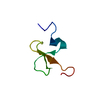
| タイトル | Structure of cytotoxin I (CTI) from Naja Oxiana in complex with DPC micelle |
|---|
 要素 要素 | Cytotoxin 1 細胞毒性 細胞毒性 |
|---|
 キーワード キーワード |  TOXIN (毒素) / antiparallel beta-sheet / beta-turn type I / beta-turn type II TOXIN (毒素) / antiparallel beta-sheet / beta-turn type I / beta-turn type II |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |   Naja oxiana (コブラ) Naja oxiana (コブラ) |
|---|
| 手法 |  溶液NMR / 溶液NMR /  simulated annealing simulated annealing |
|---|
 データ登録者 データ登録者 | Dubinnyi, M.A. / Pustovalova, Y.E. / Dubovskii, P.V. / Utkin, Y.N. / Konshina, A.G. / Efremov, R.G. / Arseniev, A.S. |
|---|
 引用 引用 | #1: ジャーナル: Biochemistry / 年: 2004タイトル: Comparative study of structure and activity of cytotoxins from venom of the cobras Naja oxiana, Naja kaouthia, and Naja haje 著者: Feofanov, A.V. / Sharonov, G.V. / Dubinnyi, M.A. / Astapova, M.V. / Kudelina, I.A. / Dubovskii, P.V. / Rodionov, D.I. / Utkin, Y.N. / Arseniev, A.S. |
|---|
| 履歴 | | 登録 | 2005年4月6日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2006年6月20日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月30日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2022年3月2日 | Group: Data collection / Database references / Derived calculations
カテゴリ: database_2 / pdbx_nmr_software ...database_2 / pdbx_nmr_software / pdbx_struct_assembly / pdbx_struct_oper_list
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_nmr_software.name |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 細胞毒性
細胞毒性  キーワード
キーワード TOXIN (毒素) / antiparallel beta-sheet / beta-turn type I / beta-turn type II
TOXIN (毒素) / antiparallel beta-sheet / beta-turn type I / beta-turn type II 機能・相同性情報
機能・相同性情報 toxin activity / killing of cells of another organism / extracellular region /
toxin activity / killing of cells of another organism / extracellular region /  生体膜
生体膜
 Naja oxiana (コブラ)
Naja oxiana (コブラ) 溶液NMR /
溶液NMR /  simulated annealing
simulated annealing  データ登録者
データ登録者 引用
引用 ジャーナル: Biochem.J. / 年: 2005
ジャーナル: Biochem.J. / 年: 2005 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1zad.cif.gz
1zad.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1zad.ent.gz
pdb1zad.ent.gz PDB形式
PDB形式 1zad.json.gz
1zad.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/za/1zad
https://data.pdbj.org/pub/pdb/validation_reports/za/1zad ftp://data.pdbj.org/pub/pdb/validation_reports/za/1zad
ftp://data.pdbj.org/pub/pdb/validation_reports/za/1zad リンク
リンク 集合体
集合体
 要素
要素 細胞毒性
細胞毒性
 Naja oxiana (コブラ) / Secretion: venom / 参照: UniProt: P01451
Naja oxiana (コブラ) / Secretion: venom / 参照: UniProt: P01451 溶液NMR
溶液NMR 試料調製
試料調製 : DRX / 磁場強度: 500 MHz
: DRX / 磁場強度: 500 MHz 解析
解析 simulated annealing / ソフトェア番号: 1
simulated annealing / ソフトェア番号: 1  ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj

