登録情報 データベース : PDB / ID : 1ewnタイトル CRYSTAL STRUCTURE OF THE HUMAN AAG DNA REPAIR GLYCOSYLASE COMPLEXED WITH 1,N6-ETHENOADENINE-DNA 3-METHYL-ADENINE DNA GLYCOSYLASE DNA (5'-D(*GP*AP*CP*AP*TP*GP*(EDA)P*TP*TP*GP*CP*C)-3')DNA (5'-D(P*GP*CP*AP*AP*TP*CP*AP*TP*GP*TP*CP*A)-3') キーワード / / / / / / / 機能・相同性 生物種 Homo sapiens (ヒト)手法 / / 解像度 : 2.1 Å データ登録者 Lau, A.Y. / Wyatt, M.D. / Glassner, B.J. / Samson, L.D. / Ellenberger, T. ジャーナル : Proc.Natl.Acad.Sci.USA / 年 : 2000タイトル : Molecular basis for discriminating between normal and damaged bases by the human alkyladenine glycosylase, AAG.著者 : Lau, A.Y. / Wyatt, M.D. / Glassner, B.J. / Samson, L.D. / Ellenberger, T. 履歴 登録 2000年4月26日 登録サイト / 処理サイト 改定 1.0 2000年12月11日 Provider / タイプ 改定 1.1 2008年4月27日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2021年11月3日 Group / Derived calculationsカテゴリ database_2 / pdbx_struct_conn_angle ... database_2 / pdbx_struct_conn_angle / struct_conn / struct_conn_type / struct_ref_seq_dif / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn_type.id / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id 改定 1.4 2024年2月7日 Group / カテゴリ / chem_comp_bond
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード DNA repair (DNA修復) /
DNA repair (DNA修復) /  glycosylase / AAG / ANPG / MPG / 3-methyladenine DNA glycosylase / hydrolase-DNA COMPLEX
glycosylase / AAG / ANPG / MPG / 3-methyladenine DNA glycosylase / hydrolase-DNA COMPLEX 機能・相同性情報
機能・相同性情報 DNA-3-メチルアデニングリコシラーゼII / DNA-7-methylguanine glycosylase activity /
DNA-3-メチルアデニングリコシラーゼII / DNA-7-methylguanine glycosylase activity /  DNA-3-methyladenine glycosylase activity /
DNA-3-methyladenine glycosylase activity /  depurination / DNA N-glycosylase activity / DNA alkylation repair / Displacement of DNA glycosylase by APEX1 ...alkylbase DNA N-glycosylase activity / DNA-7-methyladenine glycosylase activity / DNA-3-methylguanine glycosylase activity /
depurination / DNA N-glycosylase activity / DNA alkylation repair / Displacement of DNA glycosylase by APEX1 ...alkylbase DNA N-glycosylase activity / DNA-7-methyladenine glycosylase activity / DNA-3-methylguanine glycosylase activity /  DNA-3-メチルアデニングリコシラーゼII / DNA-7-methylguanine glycosylase activity /
DNA-3-メチルアデニングリコシラーゼII / DNA-7-methylguanine glycosylase activity /  DNA-3-methyladenine glycosylase activity /
DNA-3-methyladenine glycosylase activity /  depurination / DNA N-glycosylase activity / DNA alkylation repair / Displacement of DNA glycosylase by APEX1 / mitochondrial nucleoid / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine /
depurination / DNA N-glycosylase activity / DNA alkylation repair / Displacement of DNA glycosylase by APEX1 / mitochondrial nucleoid / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine /  塩基除去修復 / damaged DNA binding /
塩基除去修復 / damaged DNA binding /  核質 /
核質 /  細胞質基質
細胞質基質
 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン / 解像度: 2.1 Å
シンクロトロン / 解像度: 2.1 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2000
ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2000 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1ewn.cif.gz
1ewn.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1ewn.ent.gz
pdb1ewn.ent.gz PDB形式
PDB形式 1ewn.json.gz
1ewn.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ew/1ewn
https://data.pdbj.org/pub/pdb/validation_reports/ew/1ewn ftp://data.pdbj.org/pub/pdb/validation_reports/ew/1ewn
ftp://data.pdbj.org/pub/pdb/validation_reports/ew/1ewn リンク
リンク 集合体
集合体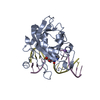
 要素
要素
 Homo sapiens (ヒト) / プラスミド: PLM1 / 発現宿主:
Homo sapiens (ヒト) / プラスミド: PLM1 / 発現宿主: 
 Escherichia coli (大腸菌) /
Escherichia coli (大腸菌) /  キーワード: 2
キーワード: 2 DNA-3-メチルアデニングリコシラーゼII
DNA-3-メチルアデニングリコシラーゼII 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  NSLS
NSLS  / ビームライン: X25 / 波長: 1.01
/ ビームライン: X25 / 波長: 1.01  : 1.01 Å / 相対比: 1
: 1.01 Å / 相対比: 1  解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj









































