+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-5801 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the mammalian ribosomal pre-termination complex associated with eRF1-eRF3-GDPNP | ||||||||||||
 マップデータ マップデータ | Reconstruction of the eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex assembled in vitro on a derivative of beta-globin mRNA encoding MVHL tetrapeptide followed by a UAA stop codon. The P-site is occupied by a tRNAleu. | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Translation termination /  eRF1 / eRF1 /  eRF3 / tRNAleu / eRF3 / tRNAleu /  ribosome (リボソーム) / ribosome (リボソーム) /  mammalian (哺乳類) mammalian (哺乳類) | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報translation termination factor activity / cytoplasmic translational termination / translation release factor complex / regulation of translational termination / translation release factor activity / translation release factor activity, codon specific /  protein methylation / sequence-specific mRNA binding / protein methylation / sequence-specific mRNA binding /  aminoacyl-tRNA hydrolase activity / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay ...translation termination factor activity / cytoplasmic translational termination / translation release factor complex / regulation of translational termination / translation release factor activity / translation release factor activity, codon specific / aminoacyl-tRNA hydrolase activity / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay ...translation termination factor activity / cytoplasmic translational termination / translation release factor complex / regulation of translational termination / translation release factor activity / translation release factor activity, codon specific /  protein methylation / sequence-specific mRNA binding / protein methylation / sequence-specific mRNA binding /  aminoacyl-tRNA hydrolase activity / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / aminoacyl-tRNA hydrolase activity / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay /  ヒドロキシル化 / Eukaryotic Translation Termination / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / translational termination / cytosolic ribosome / ヒドロキシル化 / Eukaryotic Translation Termination / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / translational termination / cytosolic ribosome /  加水分解酵素; 酸無水物に作用; GTPに作用・細胞または細胞小器官の運動に関与 / G1/S transition of mitotic cell cycle / Regulation of expression of SLITs and ROBOs / 加水分解酵素; 酸無水物に作用; GTPに作用・細胞または細胞小器官の運動に関与 / G1/S transition of mitotic cell cycle / Regulation of expression of SLITs and ROBOs /  ribosome binding / ribosome binding /  翻訳 (生物学) / 翻訳 (生物学) /  GTPase activity / GTP binding / GTPase activity / GTP binding /  RNA binding / RNA binding /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Oryctolagus cuniculus (ウサギ) / Oryctolagus cuniculus (ウサギ) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / クライオ電子顕微鏡法 /  ネガティブ染色法 / 解像度: 9.7 Å ネガティブ染色法 / 解像度: 9.7 Å | ||||||||||||
 データ登録者 データ登録者 | des Georges A / Hashem H / Unbehaun A / Grassucci RA / Taylor D / Hellen CUT / Pestova TV / Frank J | ||||||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2014 ジャーナル: Nucleic Acids Res / 年: 2014タイトル: Structure of the mammalian ribosomal pre-termination complex associated with eRF1.eRF3.GDPNP. 著者: Amédée des Georges / Yaser Hashem / Anett Unbehaun / Robert A Grassucci / Derek Taylor / Christopher U T Hellen / Tatyana V Pestova / Joachim Frank /  要旨: Eukaryotic translation termination results from the complex functional interplay between two release factors, eRF1 and eRF3, in which GTP hydrolysis by eRF3 couples codon recognition with peptidyl- ...Eukaryotic translation termination results from the complex functional interplay between two release factors, eRF1 and eRF3, in which GTP hydrolysis by eRF3 couples codon recognition with peptidyl-tRNA hydrolysis by eRF1. Here, we present a cryo-electron microscopy structure of pre-termination complexes associated with eRF1•eRF3•GDPNP at 9.7 -Å resolution, which corresponds to the initial pre-GTP hydrolysis stage of factor attachment and stop codon recognition. It reveals the ribosomal positions of eRFs and provides insights into the mechanisms of stop codon recognition and triggering of eRF3's GTPase activity. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_5801.map.gz emd_5801.map.gz | 101.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-5801-v30.xml emd-5801-v30.xml emd-5801.xml emd-5801.xml | 16.7 KB 16.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_5801_fsc.xml emd_5801_fsc.xml emd_5801_fsc_1.xml emd_5801_fsc_1.xml | 12.6 KB 12.7 KB | 表示 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_5801.jpg emd_5801.jpg | 48.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-5801 http://ftp.pdbj.org/pub/emdb/structures/EMD-5801 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5801 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5801 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_5801.map.gz / 形式: CCP4 / 大きさ: 104.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_5801.map.gz / 形式: CCP4 / 大きさ: 104.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of the eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex assembled in vitro on a derivative of beta-globin mRNA encoding MVHL tetrapeptide followed by a UAA stop codon. The P-site is occupied by a tRNAleu. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.5 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex
| 全体 | 名称: eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex |
|---|---|
| 要素 |
|
-超分子 #1000: eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex
| 超分子 | 名称: eRF1-eRF3-GDPNP-bound mammalian ribosomal pre-termination complex タイプ: sample / ID: 1000 / Number unique components: 5 |
|---|---|
| 分子量 | 理論値: 4.5 MDa / 手法: calculation |
-超分子 #1: 80S ribosome
| 超分子 | 名称: 80S ribosome / タイプ: complex / ID: 1 / 組換発現: No / データベース: NCBI / Ribosome-details: ribosome-eukaryote: ALL |
|---|---|
| 由来(天然) | 生物種:   Oryctolagus cuniculus (ウサギ) / 別称: rabbit / 組織: blood / 細胞: red blood cells Oryctolagus cuniculus (ウサギ) / 別称: rabbit / 組織: blood / 細胞: red blood cells |
| 分子量 | 理論値: 4.5 MDa |
-分子 #1: eukaryotic release factor 1
| 分子 | 名称: eukaryotic release factor 1 / タイプ: protein_or_peptide / ID: 1 / Name.synonym: eRF1 / コピー数: 1 / 集合状態: monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) / 別称: human Homo sapiens (ヒト) / 別称: human |
| 分子量 | 理論値: 480 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | UniProtKB: Eukaryotic peptide chain release factor subunit 1 |
-分子 #2: eukaryotic release factor 3
| 分子 | 名称: eukaryotic release factor 3 / タイプ: protein_or_peptide / ID: 2 / Name.synonym: eRF3 / 詳細: 138 aa N-terminal deletion / コピー数: 1 / 集合状態: monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) / 別称: human Homo sapiens (ヒト) / 別称: human |
| 分子量 | 理論値: 540 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | UniProtKB: Eukaryotic peptide chain release factor GTP-binding subunit ERF3A |
-分子 #3: Transfer-messenger RNA Leu
| 分子 | 名称: Transfer-messenger RNA Leu / タイプ: rna / ID: 3 / Name.synonym: tRNAleu 詳細: Native tRNAs were aminoacylated with Met, Val, His, and Leu using native aminoacyl-tRNA synthetases. 分類: OTHER / Structure: OTHER / Synthetic?: No |
|---|---|
| 由来(天然) | 生物種:   Oryctolagus cuniculus (ウサギ) / 別称: rabbit Oryctolagus cuniculus (ウサギ) / 別称: rabbit |
| 分子量 | 理論値: 25 KDa |
-分子 #4: messenger RNA
| 分子 | 名称: messenger RNA / タイプ: rna / ID: 4 / Name.synonym: mRNA 詳細: beta-globin mRNA encoding MVHL tetrapeptide followed by a UAA stop codon 分類: OTHER / Structure: SINGLE STRANDED / Synthetic?: Yes |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) / 別称: Human Homo sapiens (ヒト) / 別称: Human |
-実験情報
-構造解析
| 手法 |  ネガティブ染色法, ネガティブ染色法,  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 詳細: 20 mM Tris, 100 mM KOAc, 2.5 mM MgCl2, 2 mM DTT, 0.25 mM spermidine supplemented with 200 units RNasin, 0.4 mM ATP, 3 mM Mg-GMPPNP |
|---|---|
| 染色 | タイプ: NEGATIVE / 詳細: cryo |
| グリッド | 詳細: Quantifoil grids, glow discharged |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 93 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.1 mm Bright-field microscopy / Cs: 2.1 mm |
| 試料ステージ | 試料ホルダーモデル: GATAN HELIUM |
| 日付 | 2010年1月1日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: TVIPS TEMCAM-F415 (4k x 4k) 平均電子線量: 25 e/Å2 |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: Each Particle |
|---|---|
| 最終 再構成 | アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 9.7 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: RELION / 使用した粒子像数: 48973 |
| 詳細 | Images were classified and refined with RELION. |
FSC曲線 (解像度の算出) | 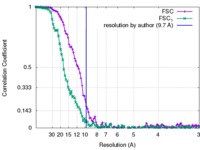 |
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - #0 - Chain ID: A / Chain - #1 - Chain ID: F |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Domains were fitted as rigid bodies using Chimera. Individual domains were then refined manually using hinge points as points of flexibility. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: Cross correlation |
| 得られたモデル |  PDB-3j5y: |
-原子モデル構築 2
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: Cross correlation |
| 得られたモデル |  PDB-3j5y: |
-原子モデル構築 3
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: Cross correlation |
| 得られたモデル |  PDB-3j5y: |
-原子モデル構築 4
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: Cross correlation |
| 得られたモデル |  PDB-3j5y: |
 ムービー
ムービー コントローラー
コントローラー





























