+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2501 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Substrate Recruitment Pathways in the Yeast Exosome by Electron Microscopy | |||||||||
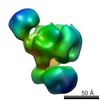
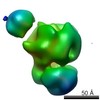
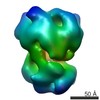
 マップデータ マップデータ | Exosome with tRNA | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | exosome / RNA degradation route | |||||||||
| 生物種 |   Saccharomyces cerevisiae (パン酵母) / synthetic construct (人工物) Saccharomyces cerevisiae (パン酵母) / synthetic construct (人工物) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 24.0 Å クライオ電子顕微鏡法 / 解像度: 24.0 Å | |||||||||
 データ登録者 データ登録者 | Liu J-J / Bratkowski MA / Liu XQ / Niu C-Y / Ke AL / Wang H-W | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2014 ジャーナル: Nat Struct Mol Biol / 年: 2014タイトル: Visualization of distinct substrate-recruitment pathways in the yeast exosome by EM. 著者: Jun-Jie Liu / Matthew A Bratkowski / Xueqi Liu / Chu-Ya Niu / Ailong Ke / Hong-Wei Wang /   要旨: The eukaryotic exosome is a multisubunit complex typically composed of a catalytically inactive core and the Rrp44 protein, which contains 3'-to-5' exo- and endo-RNase activities. RNA substrates have ...The eukaryotic exosome is a multisubunit complex typically composed of a catalytically inactive core and the Rrp44 protein, which contains 3'-to-5' exo- and endo-RNase activities. RNA substrates have been shown to be recruited through the core to reach Rrp44's exo-RNase (EXO) site. Using single-particle EM and biochemical analysis, we provide visual evidence that two distinct substrate-recruitment pathways exist. In the through-core route, channeling of the single-stranded substrates from the core to Rrp44 induces a characteristic conformational change in Rrp44. In the alternative direct-access route, this conformational change does not take place, and the RNA substrate is visualized to avoid the core and enter Rrp44's EXO site directly. Our results provide mechanistic explanations for several RNA processing scenarios by the eukaryotic exosome and indicate substrate-specific modes of degradation by this complex. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2501.map.gz emd_2501.map.gz | 2.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2501-v30.xml emd-2501-v30.xml emd-2501.xml emd-2501.xml | 16.9 KB 16.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  2501-Cryo-tRNA-RE.png 2501-Cryo-tRNA-RE.png | 55.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2501 http://ftp.pdbj.org/pub/emdb/structures/EMD-2501 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2501 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2501 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2501.map.gz / 形式: CCP4 / 大きさ: 6.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2501.map.gz / 形式: CCP4 / 大きさ: 6.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Exosome with tRNA | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Rrp44-Exosome with tRNA by Cryo-EMtRNA-RE
+超分子 #1000: Rrp44-Exosome with tRNA by Cryo-EMtRNA-RE
+分子 #1: Rrp44
+分子 #2: Rrp43
+分子 #3: Rrp4
+分子 #4: Csl4
+分子 #5: Rrp45
+分子 #6: Rrp46-TAP
+分子 #7: Rrp41
+分子 #8: Rrp42
+分子 #9: Mtr3
+分子 #10: Rrp40
+分子 #11: methionine tRNA
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2 mg/mL |
|---|---|
| 緩衝液 | pH: 8 / 詳細: 150mM NaCl, 50mM Tris-HCL,1mM DTT, 2mM MgCl2 |
| グリッド | 詳細: Quantifoil grids (2/2) with2~3 nm thin carbon on top |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 80 K / 装置: FEI VITROBOT MARK IV 手法: 4 ul of the reaction solution was then applied to glow-discharged C-flat grids (1.2/1.3) covered with a layer of continuous carbon with a thickness of ~4nm. The grids were then blotted and ...手法: 4 ul of the reaction solution was then applied to glow-discharged C-flat grids (1.2/1.3) covered with a layer of continuous carbon with a thickness of ~4nm. The grids were then blotted and plunged into liquid ethane in a FEI Vitrobot Mark IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 120 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 59000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): -3.5 µm / 最小 デフォーカス(公称値): -0.5 µm / 倍率(公称値): 59000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): -3.5 µm / 最小 デフォーカス(公称値): -0.5 µm / 倍率(公称値): 59000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 温度 | 最低: 80 K / 最高: 85 K / 平均: 82 K |
| 日付 | 2012年6月10日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GENERIC GATAN (4k x 4k) 実像数: 1200 / 平均電子線量: 20 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: both each particle and micrograph |
|---|---|
| 最終 角度割当 | 詳細: RELION: theta 45 degrees, phi 180 degrees |
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 24.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: eman, imagic, relion / 使用した粒子像数: 28800 |
| 詳細 | Micrographs of RE were collected using the AutoEMation software (Lei and Frank, 2005) installed on the microscope at low-dose condition with a dose of ~20 electron/A2 and a defocus value ranging from -1.2 to -4 um. The micrographs were collected on a FEI Eagle CCD camera with a pixel size of 1.5 A. |
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
 ムービー
ムービー コントローラー
コントローラー