+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7mos | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of HDAC2 in complex with a macrocyclic inhibitor (compound 4) | ||||||
 要素 要素 | Histone deacetylase 2 | ||||||
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / HISTONE DEACETYLASE / HYDROLASE / HYDROLASE-HYDROLASE INHIBITOR COMPLEX | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of male mating behavior / protein de-2-hydroxyisobutyrylase activity / protein lysine delactylase activity / negative regulation of dendritic spine development / p75NTR negatively regulates cell cycle via SC1 / epidermal cell differentiation / histone decrotonylase activity / fungiform papilla formation / NuRD complex / positive regulation of interleukin-1 production ...positive regulation of male mating behavior / protein de-2-hydroxyisobutyrylase activity / protein lysine delactylase activity / negative regulation of dendritic spine development / p75NTR negatively regulates cell cycle via SC1 / epidermal cell differentiation / histone decrotonylase activity / fungiform papilla formation / NuRD complex / positive regulation of interleukin-1 production / regulation of cell fate specification / : / EGR2 and SOX10-mediated initiation of Schwann cell myelination / negative regulation of stem cell population maintenance / histone deacetylase activity, hydrolytic mechanism / ESC/E(Z) complex / histone deacetylase / regulation of stem cell differentiation / behavioral response to ethanol / cellular response to dopamine / cardiac muscle hypertrophy / STAT3 nuclear events downstream of ALK signaling / histone deacetylase activity / protein lysine deacetylase activity / response to caffeine / 加水分解酵素; ペプチド以外のCN結合加水分解酵素; 鎖状アミドに作用 / embryonic digit morphogenesis / positive regulation of intracellular estrogen receptor signaling pathway / Notch-HLH transcription pathway / odontogenesis of dentin-containing tooth / Sin3-type complex / eyelid development in camera-type eye / histone deacetylase complex / positive regulation of stem cell population maintenance / response to amyloid-beta / dendrite development / positive regulation of proteolysis / progesterone receptor signaling pathway / RNA Polymerase I Transcription Initiation / positive regulation of oligodendrocyte differentiation / Regulation of MECP2 expression and activity / hair follicle placode formation / response to hyperoxia / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / NF-kappaB binding / cellular response to transforming growth factor beta stimulus / positive regulation of epithelial to mesenchymal transition / Transcriptional regulation of brown and beige adipocyte differentiation by EBF2 / Regulation of TP53 Activity through Acetylation / MECP2 regulates neuronal receptors and channels / cellular response to retinoic acid / heat shock protein binding / negative regulation of cell migration / SUMOylation of chromatin organization proteins / Regulation of PTEN gene transcription / transcription coregulator binding / response to amphetamine / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / response to nicotine / Regulation of endogenous retroelements by KRAB-ZFP proteins / response to cocaine / circadian regulation of gene expression / HDACs deacetylate histones / Regulation of endogenous retroelements by Piwi-interacting RNAs (piRNAs) / promoter-specific chromatin binding / negative regulation of transforming growth factor beta receptor signaling pathway / Negative Regulation of CDH1 Gene Transcription / NoRC negatively regulates rRNA expression / NOTCH1 Intracellular Domain Regulates Transcription / Constitutive Signaling by NOTCH1 PEST Domain Mutants / Constitutive Signaling by NOTCH1 HD+PEST Domain Mutants / histone deacetylase binding / cellular response to hydrogen peroxide / positive regulation of tumor necrosis factor production / heterochromatin formation / negative regulation of neuron projection development / cellular response to heat / Factors involved in megakaryocyte development and platelet production / histone binding / response to lipopolysaccharide / Potential therapeutics for SARS / RNA polymerase II-specific DNA-binding transcription factor binding / chromosome, telomeric region / chromatin remodeling / response to xenobiotic stimulus / negative regulation of DNA-templated transcription / positive regulation of cell population proliferation / chromatin binding / negative regulation of apoptotic process / positive regulation of DNA-templated transcription / chromatin / enzyme binding / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / protein-containing complex / RNA binding / nucleoplasm / nucleus / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  フーリエ合成 / 解像度: 1.704 Å フーリエ合成 / 解像度: 1.704 Å | ||||||
 データ登録者 データ登録者 | Klein, D.J. / Yu, W. | ||||||
 引用 引用 |  ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2021 ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2021タイトル: Discovery of macrocyclic HDACs 1, 2, and 3 selective inhibitors for HIV latency reactivation. 著者: Yu, W. / Fells, J. / Clausen, D. / Liu, J. / Klein, D.J. / Christine Chung, C. / Myers, R.W. / Wu, J. / Wu, G. / Howell, B.J. / Barnard, R.J.O. / Kozlowski, J. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7mos.cif.gz 7mos.cif.gz | 262.9 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7mos.ent.gz pdb7mos.ent.gz | 211.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7mos.json.gz 7mos.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/mo/7mos https://data.pdbj.org/pub/pdb/validation_reports/mo/7mos ftp://data.pdbj.org/pub/pdb/validation_reports/mo/7mos ftp://data.pdbj.org/pub/pdb/validation_reports/mo/7mos | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 3分子 ABC
| #1: タンパク質 | 分子量: 43061.988 Da / 分子数: 3 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: HDAC2 Homo sapiens (ヒト) / 遺伝子: HDAC2発現宿主:  参照: UniProt: Q92769, histone deacetylase |
|---|
-非ポリマー , 6種, 1110分子 



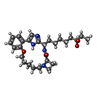






| #2: 化合物 | | #3: 化合物 | ChemComp-SO4 / #4: 化合物 | ChemComp-CA / #5: 化合物 | ChemComp-PEG / #6: 化合物 | #7: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.47 Å3/Da / 溶媒含有率: 50.26 % |
|---|---|
| 結晶化 | 温度: 293 K / 手法: 蒸気拡散法, ハンギングドロップ法 詳細: 25% PEG 3350, 0.2 M ammonium sulfate, 0.1 M Hepes pH 7.5 |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 17-ID / 波長: 1 Å / ビームライン: 17-ID / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M / 検出器: PIXEL / 日付: 2015年11月4日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1 Å / 相対比: 1 |
| 反射 | 解像度: 1.704→139.7 Å / Num. obs: 139918 / % possible obs: 99.9 % / 冗長度: 6.6 % / CC1/2: 0.999 / Net I/σ(I): 14.6 |
| 反射 シェル | 解像度: 1.704→1.71 Å / Num. unique obs: 1352 / CC1/2: 0.765 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  フーリエ合成 / 解像度: 1.704→80.75 Å / Cor.coef. Fo:Fc: 0.96 / Cor.coef. Fo:Fc free: 0.952 / SU R Cruickshank DPI: 0.1 / 交差検証法: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.107 / SU Rfree Blow DPI: 0.1 / SU Rfree Cruickshank DPI: 0.096 フーリエ合成 / 解像度: 1.704→80.75 Å / Cor.coef. Fo:Fc: 0.96 / Cor.coef. Fo:Fc free: 0.952 / SU R Cruickshank DPI: 0.1 / 交差検証法: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.107 / SU Rfree Blow DPI: 0.1 / SU Rfree Cruickshank DPI: 0.096
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 176.45 Å2 / Biso mean: 27.87 Å2 / Biso min: 7.97 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.21 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 1.704→80.75 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.704→1.72 Å / Rfactor Rfree error: 0
|
 ムービー
ムービー コントローラー
コントローラー
























 PDBj
PDBj






























