[English] 日本語
 Yorodumi
Yorodumi- PDB-7ktc: DNA Polymerase Mu, 8-oxodGTP:Ct Product State Ternary Complex, 10... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7ktc | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | DNA Polymerase Mu, 8-oxodGTP:Ct Product State Ternary Complex, 10 mM Mn2+ (120min) | ||||||||||||
 Components Components |
| ||||||||||||
 Keywords Keywords | REPLICATION / Time-Lapse Crystallography / Oxidized Nucleotide Insertion / DNA Polymerase Mu / Double Strand Break Repair | ||||||||||||
| Function / homology |  Function and homology information Function and homology informationsomatic hypermutation of immunoglobulin genes / B cell differentiation / Nonhomologous End-Joining (NHEJ) / double-strand break repair via nonhomologous end joining / DNA recombination / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / DNA binding / nucleoplasm / metal ion binding / nucleus Similarity search - Function | ||||||||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human)synthetic construct (others) | ||||||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.653 Å MOLECULAR REPLACEMENT / Resolution: 1.653 Å | ||||||||||||
 Authors Authors | Jamsen, J.A. / Wilson, S.H. | ||||||||||||
| Funding support |  United States, United States,  Japan, 3items Japan, 3items
| ||||||||||||
 Citation Citation |  Journal: Nat Commun / Year: 2021 Journal: Nat Commun / Year: 2021Title: Watching a double strand break repair polymerase insert a pro-mutagenic oxidized nucleotide. Authors: Jamsen, J.A. / Sassa, A. / Shock, D.D. / Beard, W.A. / Wilson, S.H. | ||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7ktc.cif.gz 7ktc.cif.gz | 196 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7ktc.ent.gz pdb7ktc.ent.gz | 147.7 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7ktc.json.gz 7ktc.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/kt/7ktc https://data.pdbj.org/pub/pdb/validation_reports/kt/7ktc ftp://data.pdbj.org/pub/pdb/validation_reports/kt/7ktc ftp://data.pdbj.org/pub/pdb/validation_reports/kt/7ktc | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  7kssC  7kstC  7ksuC  7ksvC  7kswC  7ksxC  7ksyC  7kszC  7kt0C  7kt1C  7kt2C  7kt3C  7kt4C  7kt5C  7kt6C  7kt7C  7kt8C  7kt9C  7ktaC  7ktbC  7ktdC  7kteC  7ktfC  7ktgC  7kthC  7ktiC  7ktjC  7ktkC  7ktlC  7ktmC  7ktnC  4m04S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 40054.434 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: POLM, polmu / Plasmid: pGEXM / Production host: Homo sapiens (human) / Gene: POLM, polmu / Plasmid: pGEXM / Production host:  |
|---|
-DNA chain , 3 types, 3 molecules TPD
| #2: DNA chain | Mass: 2716.787 Da / Num. of mol.: 1 / Source method: obtained synthetically / Source: (synth.) synthetic construct (others) |
|---|---|
| #3: DNA chain | Mass: 1536.036 Da / Num. of mol.: 1 / Source method: obtained synthetically / Source: (synth.) synthetic construct (others) |
| #4: DNA chain | Mass: 1191.818 Da / Num. of mol.: 1 / Source method: obtained synthetically / Source: (synth.) synthetic construct (others) |
-Non-polymers , 7 types, 419 molecules 


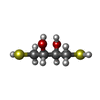
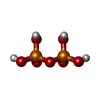








| #5: Chemical | ChemComp-NA / | ||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
| #6: Chemical | ChemComp-MN / #7: Chemical | ChemComp-EPE / | #8: Chemical | ChemComp-DTT / | #9: Chemical | ChemComp-PPV / | #10: Chemical | ChemComp-EDO / #11: Water | ChemComp-HOH / | |
-Details
| Has ligand of interest | Y |
|---|---|
| Has protein modification | Y |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.46 Å3/Da / Density % sol: 49.9 % / Mosaicity: 0.279 ° |
|---|---|
| Crystal grow | Temperature: 277 K / Method: vapor diffusion, sitting drop / pH: 7.5 / Details: 85-90mM HEPES pH 7.5, 17-18% PEG4000 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 22-ID / Wavelength: 1 Å / Beamline: 22-ID / Wavelength: 1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: RAYONIX MX300-HS / Detector: CCD / Date: Jul 22, 2016 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 1 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.65→50 Å / Num. obs: 54399 / % possible obs: 99.9 % / Redundancy: 5.9 % / Rmerge(I) obs: 0.098 / Rpim(I) all: 0.043 / Rrim(I) all: 0.108 / Χ2: 0.903 / Net I/σ(I): 8.8 / Num. measured all: 319975 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 4M04 Resolution: 1.653→35.02 Å / SU ML: 0.14 / Cross valid method: THROUGHOUT / σ(F): 1.35 / Phase error: 15.77 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 53.34 Å2 / Biso mean: 18.2024 Å2 / Biso min: 3.42 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.653→35.02 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Origin x: 4.3257 Å / Origin y: -4.5534 Å / Origin z: -13.6359 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller


 PDBj
PDBj













