+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6ozq | ||||||
|---|---|---|---|---|---|---|---|
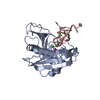
| タイトル | Crystal structure of Mus musculus (Mm) Endonuclease V (K155M) in complex with a 23mer RNA oligo containing an inosine after a 100 min soak in 10 mM Mn2+ and K+ | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | HYDROLASE / Nucleic acid hydrolysis / RNA recognition / metal ion dependent catalysis / DNA damage / adenosine deamination | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA endonuclease activity, producing 5'-phosphomonoesters / RNA endonuclease activity producing 5'-phosphomonoesters, hydrolytic mechanism / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エンドリボヌクレアーゼ / cytoplasmic stress granule / single-stranded RNA binding / DNA repair / nucleolus / magnesium ion binding / DNA binding / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  synthetic construct (人工物) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.153 Å 分子置換 / 解像度: 2.153 Å | ||||||
 データ登録者 データ登録者 | Samara, N.L. / Yang, W. | ||||||
 引用 引用 |  ジャーナル: Mol.Cell / 年: 2019 ジャーナル: Mol.Cell / 年: 2019タイトル: Evolution of Inosine-Specific Endonuclease V from Bacterial DNase to Eukaryotic RNase. 著者: Wu, J. / Samara, N.L. / Kuraoka, I. / Yang, W. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6ozq.cif.gz 6ozq.cif.gz | 248.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6ozq.ent.gz pdb6ozq.ent.gz | 195 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6ozq.json.gz 6ozq.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/oz/6ozq https://data.pdbj.org/pub/pdb/validation_reports/oz/6ozq ftp://data.pdbj.org/pub/pdb/validation_reports/oz/6ozq ftp://data.pdbj.org/pub/pdb/validation_reports/oz/6ozq | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 単位格子 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 非結晶学的対称性 (NCS) | NCSドメイン:
NCSドメイン領域:
|
 ムービー
ムービー コントローラー
コントローラー


























 PDBj
PDBj