+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6nbt | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | CRISPR Complex Subunit Csm3 from Staphylococcus epidermidis RP62a | ||||||
 要素 要素 | CRISPR-associated protein | ||||||
 キーワード キーワード | RNA BINDING PROTEIN / CRISPR / RNA Binding / RNA Recognition Motif / Samarium (III) chloride | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報endonuclease activity / defense response to virus / hydrolase activity / RNA binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  単波長異常分散 / 解像度: 2.4 Å 単波長異常分散 / 解像度: 2.4 Å | ||||||
 データ登録者 データ登録者 | Dorsey, B.W. / Mondragon, A. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2019 ジャーナル: Nucleic Acids Res / 年: 2019タイトル: Structural organization of a Type III-A CRISPR effector subcomplex determined by X-ray crystallography and cryo-EM. 著者: Bryan W Dorsey / Lei Huang / Alfonso Mondragón /  要旨: Clustered regularly interspaced short palindromic repeats (CRISPR) and their associated Cas proteins provide an immune-like response in many prokaryotes against extraneous nucleic acids. CRISPR-Cas ...Clustered regularly interspaced short palindromic repeats (CRISPR) and their associated Cas proteins provide an immune-like response in many prokaryotes against extraneous nucleic acids. CRISPR-Cas systems are classified into different classes and types. Class 1 CRISPR-Cas systems form multi-protein effector complexes that includes a guide RNA (crRNA) used to identify the target for destruction. Here we present crystal structures of Staphylococcus epidermidis Type III-A CRISPR subunits Csm2 and Csm3 and a 5.2 Å resolution single-particle cryo-electron microscopy (cryo-EM) reconstruction of an in vivo assembled effector subcomplex including the crRNA. The structures help to clarify the quaternary architecture of Type III-A effector complexes, and provide details on crRNA binding, target RNA binding and cleavage, and intermolecular interactions essential for effector complex assembly. The structures allow a better understanding of the organization of Type III-A CRISPR effector complexes as well as highlighting the overall similarities and differences with other Class 1 effector complexes. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6nbt.cif.gz 6nbt.cif.gz | 92.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6nbt.ent.gz pdb6nbt.ent.gz | 68.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6nbt.json.gz 6nbt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/nb/6nbt https://data.pdbj.org/pub/pdb/validation_reports/nb/6nbt ftp://data.pdbj.org/pub/pdb/validation_reports/nb/6nbt ftp://data.pdbj.org/pub/pdb/validation_reports/nb/6nbt | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 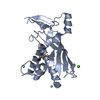
| ||||||||||||||||||
| 2 | 
| ||||||||||||||||||
| 3 | 
| ||||||||||||||||||
| 単位格子 |
| ||||||||||||||||||
| Components on special symmetry positions |
| ||||||||||||||||||
| 非結晶学的対称性 (NCS) | NCSドメイン:
NCSドメイン領域: Component-ID: _ / Ens-ID: 1 / Beg auth comp-ID: TYR / Beg label comp-ID: TYR / End auth comp-ID: LYS / End label comp-ID: LYS / Refine code: _ / Auth seq-ID: 2 - 214 / Label seq-ID: 26 - 238
|
- 要素
要素
| #1: タンパク質 | 分子量: 27012.383 Da / 分子数: 2 / 断片: Subunit Csm3 / 由来タイプ: 組換発現 由来: (組換発現)  Staphylococcus epidermidis (strain ATCC 35984 / RP62A) (表皮ブドウ球菌) Staphylococcus epidermidis (strain ATCC 35984 / RP62A) (表皮ブドウ球菌)株: ATCC 35984 / RP62A / 細胞株: 35984D-5 / 遺伝子: SERP2459 / プラスミド: pMCSG7 / 発現宿主:  #2: 化合物 | #3: 化合物 | ChemComp-SM / #4: 水 | ChemComp-HOH / | Has protein modification | Y | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.03 Å3/Da / 溶媒含有率: 39.51 % |
|---|---|
| 結晶化 | 温度: 287 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 6.5 詳細: PEG 8000, calcium acetate, 2-(N-morpholino)ethanesulfonic acid (MES) |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 21-ID-D / 波長: 1.0781 Å / ビームライン: 21-ID-D / 波長: 1.0781 Å |
| 検出器 | タイプ: DECTRIS EIGER X 9M / 検出器: PIXEL / 日付: 2018年2月28日 |
| 放射 | モノクロメーター: Si(111) / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.0781 Å / 相対比: 1 |
| 反射 | 解像度: 2.4→46.57 Å / Num. obs: 16891 / % possible obs: 98.2 % / 冗長度: 6.8 % / Net I/σ(I): 10.3 |
| 反射 シェル | 解像度: 2.4→2.49 Å |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  単波長異常分散 / 解像度: 2.4→25 Å / Cor.coef. Fo:Fc: 0.939 / Cor.coef. Fo:Fc free: 0.921 / SU B: 10.897 / SU ML: 0.246 / 交差検証法: THROUGHOUT / ESU R: 0.491 / ESU R Free: 0.284 / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS 単波長異常分散 / 解像度: 2.4→25 Å / Cor.coef. Fo:Fc: 0.939 / Cor.coef. Fo:Fc free: 0.921 / SU B: 10.897 / SU ML: 0.246 / 交差検証法: THROUGHOUT / ESU R: 0.491 / ESU R Free: 0.284 / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 50.19 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: 1 / 解像度: 2.4→25 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj





