+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5dwk | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Diacylglycerol Kinase solved by multi crystal multi orientation native SAD | ||||||
 要素 要素 | Diacylglycerol kinase | ||||||
 キーワード キーワード | TRANSFERASE / native SAD / DAGK / multi crystal / multi orientation | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報diacylglycerol kinase (ATP) / lipid kinase activity / ATP-dependent diacylglycerol kinase activity / phosphatidic acid biosynthetic process / response to UV / ATP binding / membrane / metal ion binding / identical protein binding / plasma membrane 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  単波長異常分散 / 解像度: 2.601 Å 単波長異常分散 / 解像度: 2.601 Å | ||||||
 データ登録者 データ登録者 | Weinert, T. / Olieric, V. / Finke, A.D. / Li, D. / Caffrey, M. / Wang, M. | ||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016タイトル: Data-collection strategy for challenging native SAD phasing. 著者: Olieric, V. / Weinert, T. / Finke, A.D. / Anders, C. / Li, D. / Olieric, N. / Borca, C.N. / Steinmetz, M.O. / Caffrey, M. / Jinek, M. / Wang, M. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5dwk.cif.gz 5dwk.cif.gz | 238.9 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5dwk.ent.gz pdb5dwk.ent.gz | 195 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5dwk.json.gz 5dwk.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/dw/5dwk https://data.pdbj.org/pub/pdb/validation_reports/dw/5dwk ftp://data.pdbj.org/pub/pdb/validation_reports/dw/5dwk ftp://data.pdbj.org/pub/pdb/validation_reports/dw/5dwk | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 6分子 ABCDEF
| #1: タンパク質 | 分子量: 14204.451 Da / 分子数: 6 / 断片: UNP residues 2-122 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|
-非ポリマー , 7種, 53分子 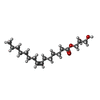
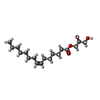











| #2: 化合物 | ChemComp-78N / ( #3: 化合物 | ChemComp-78M / ( #4: 化合物 | ChemComp-NA / | #5: 化合物 | ChemComp-ZN / | #6: 化合物 | ChemComp-CIT / | #7: 化合物 | ChemComp-ACT / | #8: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.91 Å3/Da / 溶媒含有率: 57.68 % |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 脂質キュービック相法 / pH: 5.6 詳細: 3-5 %(V/V) 2-METHYL-2, 4-PENTANEDIOL, 0.1 M SODIUM CHLORIDE, 0.06 M MAGNESIUM ACETATE, 0.1 M SODIUM CITRATE/HCL PH 5.6. CRYSTALLIZED USING THE IN MESO (LIPIDIC CUBIC PHASE) METHOD AT 4 DEGREE ...詳細: 3-5 %(V/V) 2-METHYL-2, 4-PENTANEDIOL, 0.1 M SODIUM CHLORIDE, 0.06 M MAGNESIUM ACETATE, 0.1 M SODIUM CITRATE/HCL PH 5.6. CRYSTALLIZED USING THE IN MESO (LIPIDIC CUBIC PHASE) METHOD AT 4 DEGREE CELSIUS WITH THE 7.8 MONOACYLGLYCEROL (7.8 MAG) AS THE HOSTING LIPID. |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X06DA / 波長: 2.0664 Å / ビームライン: X06DA / 波長: 2.0664 Å |
| 検出器 | タイプ: DECTRIS PILATUS 2M-F / 検出器: PIXEL / 日付: 2013年6月14日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 2.0664 Å / 相対比: 1 |
| 反射 | 解像度: 2.6→50 Å / Num. obs: 58770 / % possible obs: 99.6 % / 冗長度: 142.9 % / Rmerge(I) obs: 0.221 / Net I/σ(I): 36.46 |
| 反射 シェル | 解像度: 2.6→2.67 Å / 冗長度: 55.85 % / Rmerge(I) obs: 1.13 / Mean I/σ(I) obs: 4.18 / % possible all: 96.5 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  単波長異常分散 / 解像度: 2.601→45.785 Å / SU ML: 0.28 / 交差検証法: FREE R-VALUE / σ(F): 1.93 / 位相誤差: 23.79 / 立体化学のターゲット値: ML 単波長異常分散 / 解像度: 2.601→45.785 Å / SU ML: 0.28 / 交差検証法: FREE R-VALUE / σ(F): 1.93 / 位相誤差: 23.79 / 立体化学のターゲット値: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.601→45.785 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj




