+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3uvt | ||||||
|---|---|---|---|---|---|---|---|
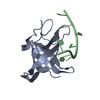
| タイトル | Crystal structure of the third catalytic domain of ERp46 | ||||||
 要素 要素 | Thioredoxin domain-containing protein 5 | ||||||
 キーワード キーワード | ISOMERASE / thioredoxin-like fold | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報酸化還元酵素; 含硫化合物に対し酸化酵素として働く; ジスルフィドが電子受容体 / protein disulfide-isomerase / Lysosome Vesicle Biogenesis / Golgi Associated Vesicle Biogenesis / protein disulfide isomerase activity / protein-disulfide reductase activity / lysosomal lumen / azurophil granule lumen / protein folding / endoplasmic reticulum lumen ...酸化還元酵素; 含硫化合物に対し酸化酵素として働く; ジスルフィドが電子受容体 / protein disulfide-isomerase / Lysosome Vesicle Biogenesis / Golgi Associated Vesicle Biogenesis / protein disulfide isomerase activity / protein-disulfide reductase activity / lysosomal lumen / azurophil granule lumen / protein folding / endoplasmic reticulum lumen / Neutrophil degranulation / negative regulation of apoptotic process / endoplasmic reticulum / extracellular exosome / extracellular region 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2 Å 分子置換 / 解像度: 2 Å | ||||||
 データ登録者 データ登録者 | Kozlov, G. / Gulerez, I.E. / Gehring, K. | ||||||
 引用 引用 |  ジャーナル: Acta Crystallogr.,Sect.F / 年: 2012 ジャーナル: Acta Crystallogr.,Sect.F / 年: 2012タイトル: Structure of the third catalytic domain of the protein disulfide isomerase ERp46. 著者: Gulerez, I.E. / Kozlov, G. / Rosenauer, A. / Gehring, K. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3uvt.cif.gz 3uvt.cif.gz | 221.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3uvt.ent.gz pdb3uvt.ent.gz | 180.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3uvt.json.gz 3uvt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  3uvt_validation.pdf.gz 3uvt_validation.pdf.gz | 470.8 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  3uvt_full_validation.pdf.gz 3uvt_full_validation.pdf.gz | 474.3 KB | 表示 | |
| XML形式データ |  3uvt_validation.xml.gz 3uvt_validation.xml.gz | 24.8 KB | 表示 | |
| CIF形式データ |  3uvt_validation.cif.gz 3uvt_validation.cif.gz | 35.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/uv/3uvt https://data.pdbj.org/pub/pdb/validation_reports/uv/3uvt ftp://data.pdbj.org/pub/pdb/validation_reports/uv/3uvt ftp://data.pdbj.org/pub/pdb/validation_reports/uv/3uvt | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3f8uS S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 4 | 
| ||||||||
| 5 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 12193.891 Da / 分子数: 5 / 断片: catalytic domain 3 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: TXNDC5, TLP46, UNQ364/PRO700 / プラスミド: pGEX-6P-1 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: TXNDC5, TLP46, UNQ364/PRO700 / プラスミド: pGEX-6P-1 / 発現宿主:  #2: 化合物 | ChemComp-SO4 / #3: 水 | ChemComp-HOH / | Has protein modification | Y | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.35 Å3/Da / 溶媒含有率: 47.76 % |
|---|---|
| 結晶化 | 温度: 294 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 5.5 詳細: 0.2 M ammonium sulfate, 0.1 M Bis-Tris (pH 5.5), 25% (w/v) PEG 3350, VAPOR DIFFUSION, HANGING DROP, temperature 294K |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  CHESS CHESS  / ビームライン: A1 / 波長: 0.977 Å / ビームライン: A1 / 波長: 0.977 Å |
| 検出器 | タイプ: ADSC QUANTUM 210 / 検出器: CCD / 日付: 2011年3月3日 |
| 放射 | モノクロメーター: Si 111 CHANNEL / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.977 Å / 相対比: 1 |
| 反射 | 解像度: 2→68.12 Å / Num. all: 36285 / Num. obs: 36285 / % possible obs: 100 % / Observed criterion σ(F): 1 / Observed criterion σ(I): 1 / 冗長度: 4.2 % / Rmerge(I) obs: 0.067 / Net I/σ(I): 21 |
| 反射 シェル | 解像度: 2→2.03 Å / 冗長度: 4.1 % / Rmerge(I) obs: 0.394 / Mean I/σ(I) obs: 3.3 / % possible all: 100 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB ENTRY 3F8U 解像度: 2→68.12 Å / Cor.coef. Fo:Fc: 0.945 / Cor.coef. Fo:Fc free: 0.92 / SU B: 8.43 / SU ML: 0.123 / 交差検証法: THROUGHOUT / σ(F): 1 / ESU R: 0.205 / ESU R Free: 0.176 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: BABINET MODEL WITH MASK | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 34.503 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2→68.12 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2→2.052 Å / Total num. of bins used: 20
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj









