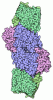
| 登録情報 | データベース: PDB / ID: 2xzl
|
|---|
| タイトル | Upf1-RNA complex |
|---|
 要素 要素 | - 5- R(*UP*UP*UP*UP*UP*UP*UP*UP*U) -3
- ATP-DEPENDENT HELICASE NAM7
|
|---|
 キーワード キーワード | HYDROLASE/RNA / HYDROLASE-RNA COMPLEX / NMD / RNA DEGRADATION / ALLOSTERIC REGULATION |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
cytoplasmic RNA surveillance / double-stranded DNA helicase activity / nuclear-transcribed mRNA catabolic process, 3'-5' exonucleolytic nonsense-mediated decay / regulation of translational termination / intracellular mRNA localization / silent mating-type cassette heterochromatin formation / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / DNA duplex unwinding / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) ...cytoplasmic RNA surveillance / double-stranded DNA helicase activity / nuclear-transcribed mRNA catabolic process, 3'-5' exonucleolytic nonsense-mediated decay / regulation of translational termination / intracellular mRNA localization / silent mating-type cassette heterochromatin formation / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / DNA duplex unwinding / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / nuclear-transcribed mRNA catabolic process / ribosomal small subunit binding / single-stranded DNA binding / DNA helicase / DNA recombination / RNA helicase activity / RNA helicase / protein ubiquitination / mRNA binding / ATP hydrolysis activity / RNA binding / zinc ion binding / ATP binding / cytoplasm類似検索 - 分子機能 Helix Hairpins - #1240 / Elongation Factor Tu (Ef-tu); domain 3 - #230 / RNA helicase UPF1, 1B domain / RNA helicase (UPF2 interacting domain) / RNA helicase UPF1, 1B domain / Upf1 cysteine-histidine-rich (CH-rich) domain profile. / RNA helicase UPF1, Cys/His rich zinc-binding domain / DNA2/NAM7 helicase, helicase domain / AAA domain / : ...Helix Hairpins - #1240 / Elongation Factor Tu (Ef-tu); domain 3 - #230 / RNA helicase UPF1, 1B domain / RNA helicase (UPF2 interacting domain) / RNA helicase UPF1, 1B domain / Upf1 cysteine-histidine-rich (CH-rich) domain profile. / RNA helicase UPF1, Cys/His rich zinc-binding domain / DNA2/NAM7 helicase, helicase domain / AAA domain / : / DNA2/NAM7-like helicase / Helix Hairpins / Elongation Factor Tu (Ef-tu); domain 3 / Helix non-globular / Special / DNA2/NAM7 helicase-like, C-terminal / AAA domain / P-loop containing nucleotide triphosphate hydrolases / ATPases associated with a variety of cellular activities / AAA+ ATPase domain / Beta Barrel / Rossmann fold / P-loop containing nucleoside triphosphate hydrolase / 3-Layer(aba) Sandwich / Mainly Beta / Alpha Beta類似検索 - ドメイン・相同性 ADENOSINE-5'-DIPHOSPHATE / TETRAFLUOROALUMINATE ION / RNA / ATP-dependent helicase NAM7類似検索 - 構成要素 |
|---|
| 生物種 |   SACCHAROMYCES CEREVISIAE (パン酵母) SACCHAROMYCES CEREVISIAE (パン酵母)
SYNTHETIC CONSTRUCT (人工物) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.4 Å 分子置換 / 解像度: 2.4 Å |
|---|
 データ登録者 データ登録者 | Chakrabarti, S. / Jayachandran, U. / Bonneau, F. / Fiorini, F. / Basquin, C. / Domcke, S. / Le Hir, H. / Conti, E. |
|---|
 引用 引用 |  ジャーナル: Mol.Cell / 年: 2011 ジャーナル: Mol.Cell / 年: 2011
タイトル: Molecular Mechanisms for the RNA-Dependent ATPase Activity of Upf1 and its Regulation by Upf2.
著者: Chakrabarti, S. / Jayachandran, U. / Bonneau, F. / Fiorini, F. / Basquin, C. / Domcke, S. / Le Hir, H. / Conti, E. |
|---|
| 履歴 | | 登録 | 2010年11月26日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2011年3月30日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年12月20日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Other / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_database_status / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_sf / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
| Remark 650 | HELIX DETERMINATION METHOD: AUTHOR PROVIDED. |
|---|
| Remark 700 | SHEET DETERMINATION METHOD: AUTHOR PROVIDED. |
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.4 Å
分子置換 / 解像度: 2.4 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Mol.Cell / 年: 2011
ジャーナル: Mol.Cell / 年: 2011 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2xzl.cif.gz
2xzl.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2xzl.ent.gz
pdb2xzl.ent.gz PDB形式
PDB形式 2xzl.json.gz
2xzl.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2xzl_validation.pdf.gz
2xzl_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2xzl_full_validation.pdf.gz
2xzl_full_validation.pdf.gz 2xzl_validation.xml.gz
2xzl_validation.xml.gz 2xzl_validation.cif.gz
2xzl_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/xz/2xzl
https://data.pdbj.org/pub/pdb/validation_reports/xz/2xzl ftp://data.pdbj.org/pub/pdb/validation_reports/xz/2xzl
ftp://data.pdbj.org/pub/pdb/validation_reports/xz/2xzl リンク
リンク 集合体
集合体
 要素
要素










 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SLS
SLS  / ビームライン: X10SA / 波長: 1
/ ビームライン: X10SA / 波長: 1  解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj