| 登録情報 | データベース: PDB / ID: 2lgy
|
|---|
| タイトル | Ubiquitin-like domain from HOIL-1 |
|---|
 要素 要素 | RanBP-type and C3HC4-type zinc finger-containing protein 1 |
|---|
 キーワード キーワード | LIGASE / ubiquitin / HOIP / E3 ligase / UBLD |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
protein linear polyubiquitination / LUBAC complex / RBR-type E3 ubiquitin transferase / negative regulation of necroptotic process / ubiquitin ligase activator activity / positive regulation of extrinsic apoptotic signaling pathway / TNFR1-induced proapoptotic signaling / negative regulation of NF-kappaB transcription factor activity / TNFR1-induced NF-kappa-B signaling pathway / protein sequestering activity ...protein linear polyubiquitination / LUBAC complex / RBR-type E3 ubiquitin transferase / negative regulation of necroptotic process / ubiquitin ligase activator activity / positive regulation of extrinsic apoptotic signaling pathway / TNFR1-induced proapoptotic signaling / negative regulation of NF-kappaB transcription factor activity / TNFR1-induced NF-kappa-B signaling pathway / protein sequestering activity / Regulation of TNFR1 signaling / ubiquitin binding / positive regulation of non-canonical NF-kappaB signal transduction / positive regulation of NF-kappaB transcription factor activity / protein polyubiquitination / ubiquitin-protein transferase activity / Antigen processing: Ubiquitination & Proteasome degradation / T cell receptor signaling pathway / proteasome-mediated ubiquitin-dependent protein catabolic process / transcription coactivator activity / positive regulation of canonical NF-kappaB signal transduction / defense response to bacterium / zinc ion binding / identical protein binding / cytosol類似検索 - 分子機能 : / : / : / LUBAC thetering domain / : / Zinc finger, RING-type, eukaryotic / RING-type zinc-finger / TRIAD supradomain / TRIAD supradomain profile. / Zinc finger domain ...: / : / : / LUBAC thetering domain / : / Zinc finger, RING-type, eukaryotic / RING-type zinc-finger / TRIAD supradomain / TRIAD supradomain profile. / Zinc finger domain / Zinc finger RanBP2 type profile. / Zinc finger, RanBP2-type superfamily / Zinc finger RanBP2-type signature. / Zinc finger, RanBP2-type / Zinc finger, RING-type, conserved site / Zinc finger RING-type signature. / Phosphatidylinositol 3-kinase Catalytic Subunit; Chain A, domain 1 / Ring finger / Zinc finger RING-type profile. / Zinc finger, RING-type / Ubiquitin-like (UB roll) / Ubiquitin domain profile. / Ubiquitin-like domain / Ubiquitin-like domain superfamily / Zinc finger, RING/FYVE/PHD-type / Roll / Alpha Beta類似検索 - ドメイン・相同性 RanBP-type and C3HC4-type zinc finger-containing protein 1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / molecular dynamics |
|---|
| Model details | closest to the average, model 4 |
|---|
 データ登録者 データ登録者 | Beasley, S.A. / Shaw, G.S. |
|---|
 引用 引用 |  ジャーナル: Protein Sci. / 年: 2012 ジャーナル: Protein Sci. / 年: 2012
タイトル: Solution structure of the E3 ligase HOIL-1 Ubl domain.
著者: Beasley, S.A. / Safadi, S.S. / Barber, K.R. / Shaw, G.S. |
|---|
| 履歴 | | 登録 | 2011年8月3日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2012年6月20日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2012年6月27日 | Group: Database references |
|---|
| 改定 1.2 | 2023年6月14日 | Group: Data collection / Database references / Other
カテゴリ: database_2 / pdbx_database_status ...database_2 / pdbx_database_status / pdbx_nmr_software / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data / _pdbx_nmr_software.name / _struct_ref_seq_dif.details |
|---|
| 改定 1.3 | 2024年5月15日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2 / Item: _database_2.pdbx_DOI |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: Protein Sci. / 年: 2012
ジャーナル: Protein Sci. / 年: 2012 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2lgy.cif.gz
2lgy.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2lgy.ent.gz
pdb2lgy.ent.gz PDB形式
PDB形式 2lgy.json.gz
2lgy.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2lgy_validation.pdf.gz
2lgy_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2lgy_full_validation.pdf.gz
2lgy_full_validation.pdf.gz 2lgy_validation.xml.gz
2lgy_validation.xml.gz 2lgy_validation.cif.gz
2lgy_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/lg/2lgy
https://data.pdbj.org/pub/pdb/validation_reports/lg/2lgy ftp://data.pdbj.org/pub/pdb/validation_reports/lg/2lgy
ftp://data.pdbj.org/pub/pdb/validation_reports/lg/2lgy リンク
リンク 集合体
集合体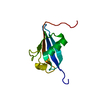
 要素
要素 Homo sapiens (ヒト) / 遺伝子: RBCK1, C20orf18, RNF54, UBCE7IP3, XAP3, XAP4 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: RBCK1, C20orf18, RNF54, UBCE7IP3, XAP3, XAP4 / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj




 HSQC
HSQC