| 登録情報 | データベース: PDB / ID: 2kbj
|
|---|
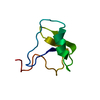
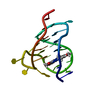
| タイトル | solution structure of BmKalphaTx11 (minor conformation) |
|---|
 要素 要素 | Toxin Bmka2 |
|---|
 キーワード キーワード | TOXIN / Protein / Ionic channel inhibitor / Neurotoxin / Secreted / Sodium channel inhibitor |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
sodium channel inhibitor activity / defense response / toxin activity / extracellular region類似検索 - 分子機能 Scorpion long chain toxin / LCN-type cysteine-stabilized alpha/beta (CS-alpha/beta) domain / LCN-type cysteine-stabilized alpha/beta (CS-alpha/beta) domain profile. / Scorpion long chain toxin/defensin / Scorpion toxin-like domain / Knottins / Knottin, scorpion toxin-like / Knottin, scorpion toxin-like / Knottin, scorpion toxin-like superfamily / Defensin A-like ...Scorpion long chain toxin / LCN-type cysteine-stabilized alpha/beta (CS-alpha/beta) domain / LCN-type cysteine-stabilized alpha/beta (CS-alpha/beta) domain profile. / Scorpion long chain toxin/defensin / Scorpion toxin-like domain / Knottins / Knottin, scorpion toxin-like / Knottin, scorpion toxin-like / Knottin, scorpion toxin-like superfamily / Defensin A-like / 2-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Mesobuthus martensii (サソリ) Mesobuthus martensii (サソリ) |
|---|
| 手法 | 溶液NMR / simulated annealing, torsion angle dynamics |
|---|
 データ登録者 データ登録者 | Zhu, J. / Wu, H. |
|---|
 引用 引用 |  ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2010 ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2010
タイトル: Solution structure of BmKalphaTx11, a toxin from the venom of the Chinese scorpion Buthus martensii Karsch
著者: Zhu, J. / Tong, X. / Cao, C. / Wu, G. / Zhang, N. / Wu, H. |
|---|
| 履歴 | | 登録 | 2008年11月28日 | 登録サイト: BMRB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2009年12月8日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2022年3月16日 | Group: Database references / Derived calculations
カテゴリ: database_2 / pdbx_struct_assembly / pdbx_struct_oper_list
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
| 改定 1.3 | 2024年11月6日 | Group: Data collection / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Mesobuthus martensii (サソリ)
Mesobuthus martensii (サソリ) データ登録者
データ登録者 引用
引用 ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2010
ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2010 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2kbj.cif.gz
2kbj.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2kbj.ent.gz
pdb2kbj.ent.gz PDB形式
PDB形式 2kbj.json.gz
2kbj.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2kbj_validation.pdf.gz
2kbj_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2kbj_full_validation.pdf.gz
2kbj_full_validation.pdf.gz 2kbj_validation.xml.gz
2kbj_validation.xml.gz 2kbj_validation.cif.gz
2kbj_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/kb/2kbj
https://data.pdbj.org/pub/pdb/validation_reports/kb/2kbj ftp://data.pdbj.org/pub/pdb/validation_reports/kb/2kbj
ftp://data.pdbj.org/pub/pdb/validation_reports/kb/2kbj リンク
リンク 集合体
集合体
 要素
要素 Mesobuthus martensii (サソリ) / 参照: UniProt: Q9NJC7
Mesobuthus martensii (サソリ) / 参照: UniProt: Q9NJC7 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj
 CYANA
CYANA