+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 298d | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
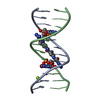
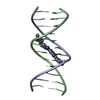
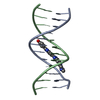
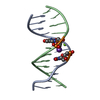
| タイトル | TARGETING THE MINOR GROOVE OF DNA: CRYSTAL STRUCTURES OF TWO COMPLEXES BETWEEN FURAN DERIVATIVES OF BERENIL AND THE DNA DODECAMER D(CGCGAATTCGCG)2 | ||||||||||||||||||
 要素 要素 | DNA (5'-D(* キーワード キーワードDNA / B-DNA / DOUBLE HELIX / COMPLEXED WITH DRUG | 機能・相同性 | Chem-D18 / DNA / DNA (> 10) |  機能・相同性情報 機能・相同性情報手法 |  X線回折 / 解像度: 2.2 Å X線回折 / 解像度: 2.2 Å  データ登録者 データ登録者Trent, J.O. / Clark, G.R. / Kumar, A. / Wilson, W.D. / Boykin, D.W. / Hall, J.E. / Tidwell, R.R. / Blagburn, B.L. / Neidle, S. |  引用 引用 ジャーナル: J.Med.Chem. / 年: 1996 ジャーナル: J.Med.Chem. / 年: 1996タイトル: Targeting the minor groove of DNA: crystal structures of two complexes between furan derivatives of berenil and the DNA dodecamer d(CGCGAATTCGCG)2. 著者: Trent, J.O. / Clark, G.R. / Kumar, A. / Wilson, W.D. / Boykin, D.W. / Hall, J.E. / Tidwell, R.R. / Blagburn, B.L. / Neidle, S. #1:  ジャーナル: Biochemistry / 年: 1996 ジャーナル: Biochemistry / 年: 1996タイトル: A Crystallographic and Spectroscopic Study of the Complex Between d(CGCGAATTCGCG)2 and 2,5-Bis(4-guanylphenyl)furan, an Analogue of Berenil. Structural Origins of Enhanced DNA-binding Affinity 著者: Laughton, C.A. / Tanious, F. / Nunn, C.M. / Boykin, D.W. / Wilson, W.D. / Neidle, S. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  298d.cif.gz 298d.cif.gz | 25.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb298d.ent.gz pdb298d.ent.gz | 16.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  298d.json.gz 298d.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/98/298d https://data.pdbj.org/pub/pdb/validation_reports/98/298d ftp://data.pdbj.org/pub/pdb/validation_reports/98/298d ftp://data.pdbj.org/pub/pdb/validation_reports/98/298d | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 3663.392 Da / 分子数: 2 / 由来タイプ: 天然 #2: 化合物 | ChemComp-D18 / | #3: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.2 Å3/Da / 溶媒含有率: 44.13 % | ||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 温度: 286 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 7 詳細: pH 7.00, VAPOR DIFFUSION, HANGING DROP, temperature 286.00K | ||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 |
| ||||||||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 温度: 286 K / pH: 7 | ||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 287 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / 波長: 1.5418 回転陽極 / 波長: 1.5418 |
| 検出器 | タイプ: XENTRONICS / 検出器: AREA DETECTOR / 日付: 1995年9月12日 |
| 放射 | モノクロメーター: GRAPHITE / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 最高解像度: 2.2 Å / Num. obs: 3146 / % possible obs: 87.6 % / Rmerge(I) obs: 0.073 |
| 反射 | *PLUS 最高解像度: 2.2 Å / Num. all: 3592 / % possible obs: 87.6 % |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 開始モデル: BDL001 解像度: 2.2→8 Å / σ(F): 2 /
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine Biso |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.2→8 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ソフトウェア | *PLUS 名称:  X-PLOR / 分類: refinement X-PLOR / 分類: refinement | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS 最高解像度: 3.5 Å / 最低解像度: 8 Å / σ(F): 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj