+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1sln | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
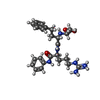
| タイトル | CRYSTAL STRUCTURE OF THE CATALYTIC DOMAIN OF HUMAN FIBROBLAST STROMELYSIN-1 INHIBITED WITH THE N-CARBOXY-ALKYL INHIBITOR L-702,842 | |||||||||
 要素 要素 | STROMELYSIN-1 | |||||||||
 キーワード キーワード | HYDROLASE / METALLOPROTEASE / FIBROBLAST / COLLAGEN DEGRADATION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報stromelysin 1 / cellular response to UV-A / regulation of neuroinflammatory response / Assembly of collagen fibrils and other multimeric structures / Activation of Matrix Metalloproteinases / response to amyloid-beta / Collagen degradation / collagen catabolic process / negative regulation of reactive oxygen species metabolic process / extracellular matrix disassembly ...stromelysin 1 / cellular response to UV-A / regulation of neuroinflammatory response / Assembly of collagen fibrils and other multimeric structures / Activation of Matrix Metalloproteinases / response to amyloid-beta / Collagen degradation / collagen catabolic process / negative regulation of reactive oxygen species metabolic process / extracellular matrix disassembly / Degradation of the extracellular matrix / extracellular matrix organization / EGFR Transactivation by Gastrin / extracellular matrix / cellular response to nitric oxide / negative regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / regulation of cell migration / cellular response to reactive oxygen species / cellular response to amino acid stimulus / positive regulation of protein-containing complex assembly / protein catabolic process / metalloendopeptidase activity / metallopeptidase activity / peptidase activity / cellular response to lipopolysaccharide / Interleukin-4 and Interleukin-13 signaling / endopeptidase activity / Extra-nuclear estrogen signaling / serine-type endopeptidase activity / innate immune response / mitochondrion / proteolysis / extracellular space / extracellular region / zinc ion binding / nucleus / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  X線回折 / 解像度: 2.27 Å X線回折 / 解像度: 2.27 Å | |||||||||
 データ登録者 データ登録者 | Becker, J.W. | |||||||||
 引用 引用 |  ジャーナル: Protein Sci. / 年: 1995 ジャーナル: Protein Sci. / 年: 1995タイトル: Stromelysin-1: three-dimensional structure of the inhibited catalytic domain and of the C-truncated proenzyme. 著者: Becker, J.W. / Marcy, A.I. / Rokosz, L.L. / Axel, M.G. / Burbaum, J.J. / Fitzgerald, P.M. / Cameron, P.M. / Esser, C.K. / Hagmann, W.K. / Hermes, J.D. / Springer, J.P. #1:  ジャーナル: Nat.Struct.Biol. / 年: 1994 ジャーナル: Nat.Struct.Biol. / 年: 1994タイトル: The NMR Structure of the Inhibited Catalytic Domain of Human Stromelysin-1 著者: Gooley, P.R. / O'Connell, J.F. / Marcy, A.I. / Cuca, G.C. / Salowe, S.P. / Bush, B.L. / Hermes, J.D. / Esser, C.K. / Hagmann, W.K. / Springer, J.P. / Johnson, B.A. #2:  ジャーナル: J.Med.Chem. / 年: 1993 ジャーナル: J.Med.Chem. / 年: 1993タイトル: Inhibition of Matrix Metalloproteinases by N-Carboxyalkyl Peptides 著者: Chapman, K.T. / Kopka, I.E. / Durette, P.L. / Esser, C.K. / Lanza, T.J. / Izquierdo-Martin, M. / Niedzwiecki, L. / Chang, B. / Harrison, R.K. / Kuo, D.W. / Lin, T.-T. / Stein, R.L. / Hagmann, W.K. #3:  ジャーナル: Biochemistry / 年: 1991 ジャーナル: Biochemistry / 年: 1991タイトル: Human Fibroblast Stromelysin Catalytic Domain: Expression, Purification, and Characterization of a C-Terminally Truncated Form 著者: Marcy, A.I. / Eiberger, L.L. / Harrison, R. / Chan, H.K. / Hutchinson, N.I. / Hagmann, W.K. / Cameron, P.M. / Boulton, D.A. / Hermes, J.D. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1sln.cif.gz 1sln.cif.gz | 59.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1sln.ent.gz pdb1sln.ent.gz | 41.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1sln.json.gz 1sln.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1sln_validation.pdf.gz 1sln_validation.pdf.gz | 743 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1sln_full_validation.pdf.gz 1sln_full_validation.pdf.gz | 743.9 KB | 表示 | |
| XML形式データ |  1sln_validation.xml.gz 1sln_validation.xml.gz | 9.1 KB | 表示 | |
| CIF形式データ |  1sln_validation.cif.gz 1sln_validation.cif.gz | 11.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/sl/1sln https://data.pdbj.org/pub/pdb/validation_reports/sl/1sln ftp://data.pdbj.org/pub/pdb/validation_reports/sl/1sln ftp://data.pdbj.org/pub/pdb/validation_reports/sl/1sln | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
| ||||||||
| Components on special symmetry positions |
|
- 要素
要素
| #1: タンパク質 | 分子量: 19416.529 Da / 分子数: 1 / 断片: CATALYTIC DOMAIN RESIDUES 83 - 255 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / Cell: FIBROBLAST / 発現宿主: Homo sapiens (ヒト) / Cell: FIBROBLAST / 発現宿主:  | ||||||||
|---|---|---|---|---|---|---|---|---|---|
| #2: 化合物 | | #3: 化合物 | #4: 化合物 | ChemComp-8MI / | #5: 水 | ChemComp-HOH / | 構成要素の詳細 | THERE IS A HYDROGEN BOND BETWEEN THE NITROGEN ATOM OF ALA 140 AND THE S-DELTA OF MET 143. | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.45 Å3/Da / 溶媒含有率: 49.3 % | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 5.54 詳細: HANGING DROP VAPOR DIFFUSION. 1.5 MICROLITER DROPS OF ENZYME:INHIBITOR SOLUTION (9 MG/ML ENZYME, 1.5 MILLIMOLAR INHIBITOR, 5.0 MILLIMOLAR CALCIUM CHLORIDE, 0.02% SODIUM AZIDE, 20 MILLIMOLAR ...詳細: HANGING DROP VAPOR DIFFUSION. 1.5 MICROLITER DROPS OF ENZYME:INHIBITOR SOLUTION (9 MG/ML ENZYME, 1.5 MILLIMOLAR INHIBITOR, 5.0 MILLIMOLAR CALCIUM CHLORIDE, 0.02% SODIUM AZIDE, 20 MILLIMOLAR TRIS HYDROCHLORIDE, PH 7.5) WERE MIXED WITH AN EQUAL VOLUME OF RESERVOIR BUFFER (10% PEG-6000, 15% SATURATED AMMONIUM ACETATE 0.02% SODIUM AZIDE, 0.1 M CACODYLATE, PH 5.54) AND INCUBATED AT ROOM TEMPERATURE., vapor diffusion - hanging drop PH範囲: 5.54-7.5 / Temp details: room temp | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 手法: 蒸気拡散法, ハンギングドロップ法 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 293 K |
|---|---|
| 放射光源 | 由来: SEALED TUBE / 波長: 1.5418 |
| 検出器 | タイプ: SIEMENS / 検出器: AREA DETECTOR / 日付: 1990年12月1日 |
| 放射 | モノクロメーター: GRAPHITE(002) / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 2.27→8 Å / Num. obs: 8311 / % possible obs: 88.9 % / Observed criterion σ(I): 1 / 冗長度: 2.79 % / Biso Wilson estimate: 11.76 Å2 / Rmerge(I) obs: 0.0598 / Rsym value: 0.0758 / Net I/σ(I): 11.9 |
| 反射 シェル | 解像度: 2.26→2.41 Å / 冗長度: 1.71 % / Mean I/σ(I) obs: 4.03 / Rsym value: 0.189 / % possible all: 60.9 |
| 反射 シェル | *PLUS % possible obs: 60.9 % / Rmerge(I) obs: 0.189 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 2.27→8 Å / 交差検証法: FREE-R / σ(F): 2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 11.69 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.27→8 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.27→2.37 Å / Total num. of bins used: 8
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ソフトウェア | *PLUS 名称:  X-PLOR / 分類: refinement X-PLOR / 分類: refinement | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj