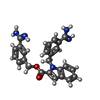
登録情報 データベース : PDB / ID : 1lpkタイトル CRYSTAL STRUCTURE OF FXA IN COMPLEX WITH 125. (Blood coagulation factor Xa) x 2 キーワード / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト)手法 / / 解像度 : 2.2 Å データ登録者 Schreuder, H.A. / Loenze, P. / Brachvogel, V. / Liesum, A. ジャーナル : J.Med.Chem. / 年 : 2002タイトル : Design and Quantitative Structure-Activity relationship of 3-amidinobenzyl-1H-indole-2-carboxamides as potent, nonchiral, and selective inhibitors of blood coagulation factor Xa著者 : Matter, H. / Defossa, E. / Heinelt, U. / Blohm, P.M. / Schneider, D. / Mueller, A. / Herok, S. / Schreuder, H.A. / Liesum, A. / Brachvogel, V. / Loenze, P. / Walser, A. / Al-Obeidi, F. / Wildgoose, P. 履歴 登録 2002年5月8日 登録サイト / 処理サイト 改定 1.0 2003年5月8日 Provider / タイプ 改定 1.1 2008年4月28日 Group 改定 1.2 2011年7月13日 Group 改定 2.0 2021年10月27日 Group Data collection / Database references ... Data collection / Database references / Derived calculations / Non-polymer description / Structure summary カテゴリ chem_comp / database_2 ... chem_comp / database_2 / entity / pdbx_struct_conn_angle / pdbx_validate_chiral / struct_conn / struct_site Item _chem_comp.formula / _chem_comp.formula_weight ... _chem_comp.formula / _chem_comp.formula_weight / _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _entity.formula_weight / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id 改定 2.1 2024年11月13日 Group / Structure summaryカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  分子置換 / 解像度: 2.2 Å
分子置換 / 解像度: 2.2 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2002
ジャーナル: J.Med.Chem. / 年: 2002 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1lpk.cif.gz
1lpk.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1lpk.ent.gz
pdb1lpk.ent.gz PDB形式
PDB形式 1lpk.json.gz
1lpk.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/lp/1lpk
https://data.pdbj.org/pub/pdb/validation_reports/lp/1lpk ftp://data.pdbj.org/pub/pdb/validation_reports/lp/1lpk
ftp://data.pdbj.org/pub/pdb/validation_reports/lp/1lpk リンク
リンク 集合体
集合体


 要素
要素 Homo sapiens (ヒト) / 参照: UniProt: P00742, coagulation factor Xa
Homo sapiens (ヒト) / 参照: UniProt: P00742, coagulation factor Xa Homo sapiens (ヒト) / 参照: UniProt: P00742, coagulation factor Xa
Homo sapiens (ヒト) / 参照: UniProt: P00742, coagulation factor Xa X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: ENRAF-NONIUS FR571 / 波長: 1.54128 Å
回転陽極 / タイプ: ENRAF-NONIUS FR571 / 波長: 1.54128 Å 解析
解析 分子置換 / 解像度: 2.2→8 Å / Isotropic thermal model: Isotropic / 交差検証法: THROUGHOUT / σ(F): -3 / 立体化学のターゲット値: Engh & Huber
分子置換 / 解像度: 2.2→8 Å / Isotropic thermal model: Isotropic / 交差検証法: THROUGHOUT / σ(F): -3 / 立体化学のターゲット値: Engh & Huber ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj