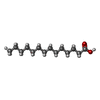
登録情報 データベース : PDB / ID : 1jsaタイトル MYRISTOYLATED RECOVERIN WITH TWO CALCIUMS BOUND, NMR, 24 STRUCTURES RECOVERIN キーワード / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Bos taurus (ウシ)手法 データ登録者 Ames, J.B. / Ishima, R. / Tanaka, T. / Gordon, J.I. / Stryer, L. / Ikura, M. ジャーナル : Nature / 年 : 1997タイトル : Molecular mechanics of calcium-myristoyl switches.著者 : Ames, J.B. / Ishima, R. / Tanaka, T. / Gordon, J.I. / Stryer, L. / Ikura, M. 履歴 登録 1997年6月4日 処理サイト 改定 1.0 1997年10月15日 Provider / タイプ 改定 1.1 2008年3月3日 Group 改定 1.2 2011年7月13日 Group 改定 1.3 2022年2月23日 Group / Derived calculations / Otherカテゴリ database_2 / pdbx_database_status ... database_2 / pdbx_database_status / pdbx_struct_assembly / pdbx_struct_conn_angle / pdbx_struct_oper_list / struct_conn / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.process_site / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id 改定 1.4 2024年10月16日 Group / Structure summaryカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / pdbx_entry_details / pdbx_modification_feature
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 引用
引用 ジャーナル: Nature / 年: 1997
ジャーナル: Nature / 年: 1997 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1jsa.cif.gz
1jsa.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1jsa.ent.gz
pdb1jsa.ent.gz PDB形式
PDB形式 1jsa.json.gz
1jsa.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/js/1jsa
https://data.pdbj.org/pub/pdb/validation_reports/js/1jsa ftp://data.pdbj.org/pub/pdb/validation_reports/js/1jsa
ftp://data.pdbj.org/pub/pdb/validation_reports/js/1jsa リンク
リンク 集合体
集合体
 要素
要素

 試料調製
試料調製 解析
解析 X-PLOR / 開発者: BRUNGER / 分類: 精密化
X-PLOR / 開発者: BRUNGER / 分類: 精密化 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj