| 登録情報 | データベース: PDB / ID: 1dbw
|
|---|
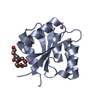
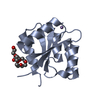
| タイトル | CRYSTAL STRUCTURE OF FIXJ-N |
|---|
 要素 要素 | TRANSCRIPTIONAL REGULATORY PROTEIN FIXJ |
|---|
 キーワード キーワード | TRANSCRIPTION / DOUBLY WOUND FIVE-STRANDED BETA/ALPHA FOLD / NITROGEN FIXATION REGULATION |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
nitrogen fixation / DNA-binding transcription activator activity / phosphorelay signal transduction system / protein-DNA complex / transcription cis-regulatory region binding / positive regulation of DNA-templated transcription / metal ion binding / cytoplasm類似検索 - 分子機能 LuxR-type HTH domain signature. / LuxR-type HTH domain profile. / Transcription regulator LuxR, C-terminal / Bacterial regulatory proteins, luxR family / helix_turn_helix, Lux Regulon / Signal transduction response regulator, C-terminal effector / Response regulator receiver domain / cheY-homologous receiver domain / Signal transduction response regulator, receiver domain / Response regulatory domain profile. ...LuxR-type HTH domain signature. / LuxR-type HTH domain profile. / Transcription regulator LuxR, C-terminal / Bacterial regulatory proteins, luxR family / helix_turn_helix, Lux Regulon / Signal transduction response regulator, C-terminal effector / Response regulator receiver domain / cheY-homologous receiver domain / Signal transduction response regulator, receiver domain / Response regulatory domain profile. / CheY-like superfamily / Response regulator / Winged helix-like DNA-binding domain superfamily / Rossmann fold / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Sinorhizobium meliloti (根粒菌) Sinorhizobium meliloti (根粒菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 1.6 Å シンクロトロン / 解像度: 1.6 Å |
|---|
 データ登録者 データ登録者 | Gouet, P. / Fabry, B. / Guillet, V. / Birck, C. / Mourey, L. / Kahn, D. / Samama, J.P. |
|---|
 引用 引用 | |
|---|
| 履歴 | | 登録 | 1999年11月3日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 1999年11月26日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月27日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2018年1月31日 | Group: Experimental preparation / カテゴリ: exptl_crystal_grow / Item: _exptl_crystal_grow.temp |
|---|
| 改定 1.4 | 2021年11月3日 | Group: Database references / Derived calculations / カテゴリ: database_2 / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.5 | 2024年2月7日 | Group: Data collection / カテゴリ: chem_comp_atom / chem_comp_bond |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Sinorhizobium meliloti (根粒菌)
Sinorhizobium meliloti (根粒菌) X線回折 /
X線回折 /  シンクロトロン / 解像度: 1.6 Å
シンクロトロン / 解像度: 1.6 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Structure Fold.Des. / 年: 1999
ジャーナル: Structure Fold.Des. / 年: 1999 ジャーナル: To be Published
ジャーナル: To be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1dbw.cif.gz
1dbw.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1dbw.ent.gz
pdb1dbw.ent.gz PDB形式
PDB形式 1dbw.json.gz
1dbw.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/db/1dbw
https://data.pdbj.org/pub/pdb/validation_reports/db/1dbw ftp://data.pdbj.org/pub/pdb/validation_reports/db/1dbw
ftp://data.pdbj.org/pub/pdb/validation_reports/db/1dbw リンク
リンク 集合体
集合体
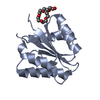

 要素
要素 Sinorhizobium meliloti (根粒菌) / プラスミド: PT7-7 / 発現宿主:
Sinorhizobium meliloti (根粒菌) / プラスミド: PT7-7 / 発現宿主: 
 X線回折 / 使用した結晶の数: 2
X線回折 / 使用した結晶の数: 2  試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj