+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9040 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Analysis of bacteriophage phiX174 tomograms using the locked self-rotation function | ||||||||||||
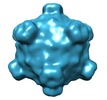
 マップデータ マップデータ | The map was calculated by averaging of ten icosahedrally-averaged maps of individual phiX174 particles. | ||||||||||||
 試料 試料 |
| ||||||||||||
| 生物種 |  Enterobacteria phage phiX174 (ファージ) Enterobacteria phage phiX174 (ファージ) | ||||||||||||
| 手法 | 電子線トモグラフィー法 / クライオ電子顕微鏡法 | ||||||||||||
 データ登録者 データ登録者 | Fokine A / Sun Y / Khare B / Rossmann MG | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: J Struct Biol / 年: 2019 ジャーナル: J Struct Biol / 年: 2019タイトル: Enhancement of tomogram interpretability using the locked self-rotation function. 著者: Andrei Fokine / Baldeep Khare / Yingyuan Sun / Michael G Rossmann /  要旨: The interpretation of cryo-electron tomograms of macromolecular complexes can be difficult because of the large amount of noise and because of the missing wedge effect. Here it is shown how the ...The interpretation of cryo-electron tomograms of macromolecular complexes can be difficult because of the large amount of noise and because of the missing wedge effect. Here it is shown how the presence of rotational symmetry in a sample can be utilized to enhance the quality of a tomographic analysis. The orientation of symmetry axes in a sub-tomogram can be determined using a locked self-rotation function. Given this knowledge, the sub-tomogram density can then be averaged to improve its interpretability. Sub-tomograms of the icosahedral bacteriophage phiX174 are used to demonstrate the procedure. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9040.map.gz emd_9040.map.gz | 474.2 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9040-v30.xml emd-9040-v30.xml emd-9040.xml emd-9040.xml | 33.7 KB 33.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_9040.png emd_9040.png | 106.8 KB | ||
| その他 |  emd_9040_additional_1.map.gz emd_9040_additional_1.map.gz emd_9040_additional_10.map.gz emd_9040_additional_10.map.gz emd_9040_additional_11.map.gz emd_9040_additional_11.map.gz emd_9040_additional_2.map.gz emd_9040_additional_2.map.gz emd_9040_additional_3.map.gz emd_9040_additional_3.map.gz emd_9040_additional_4.map.gz emd_9040_additional_4.map.gz emd_9040_additional_5.map.gz emd_9040_additional_5.map.gz emd_9040_additional_6.map.gz emd_9040_additional_6.map.gz emd_9040_additional_7.map.gz emd_9040_additional_7.map.gz emd_9040_additional_8.map.gz emd_9040_additional_8.map.gz emd_9040_additional_9.map.gz emd_9040_additional_9.map.gz | 1.8 MB 1.8 MB 518.5 KB 1.8 MB 1.8 MB 1.8 MB 1.8 MB 7.4 MB 1.8 MB 1.8 MB 1.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9040 http://ftp.pdbj.org/pub/emdb/structures/EMD-9040 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9040 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9040 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_9040_validation.pdf.gz emd_9040_validation.pdf.gz | 78.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_9040_full_validation.pdf.gz emd_9040_full_validation.pdf.gz | 77.3 KB | 表示 | |
| XML形式データ |  emd_9040_validation.xml.gz emd_9040_validation.xml.gz | 497 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9040 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9040 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9040 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9040 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9040.map.gz / 形式: CCP4 / 大きさ: 2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9040.map.gz / 形式: CCP4 / 大きさ: 2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | The map was calculated by averaging of ten icosahedrally-averaged maps of individual phiX174 particles. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 5.2 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: The map was produced by averaging of eight...
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
+追加マップ: Tomogram of one bacteriophage phiX174 particle.
- 試料の構成要素
試料の構成要素
-全体 : Enterobacteria phage phiX174
| 全体 | 名称:  Enterobacteria phage phiX174 (ファージ) Enterobacteria phage phiX174 (ファージ) |
|---|---|
| 要素 |
|
-超分子 #1: Enterobacteria phage phiX174
| 超分子 | 名称: Enterobacteria phage phiX174 / タイプ: virus / ID: 1 / 親要素: 0 / 詳細: The virus was grown in E.coli cells. / NCBI-ID: 10847 / 生物種: Enterobacteria phage phiX174 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  |
| ウイルス殻 | Shell ID: 1 / 直径: 320.0 Å / T番号(三角分割数): 1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線トモグラフィー法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 構成要素:
| ||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: C-flat-2/2 4C / 材質: COPPER / 前処理 - タイプ: GLOW DISCHARGE | ||||||||||||||
| 凍結 | 凍結剤: ETHANE / 装置: GATAN CRYOPLUNGE 3 | ||||||||||||||
| 詳細 | The concentration of the virus was 10**12 pfu/ml | ||||||||||||||
| 切片作成 | その他: NO SECTIONING | ||||||||||||||
| 位置合わせマーカー | Manufacturer: Aurion, Wageningen, Netherland / 直径: 10 nm |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 1.73 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最小 デフォーカス(公称値): 3.0 µm / 倍率(公称値): 11000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | アルゴリズム: BACK PROJECTION / ソフトウェア - 名称:  IMOD / 使用した粒子像数: 41 IMOD / 使用した粒子像数: 41 |
|---|
 ムービー
ムービー コントローラー
コントローラー








 Z
Z Y
Y X
X