+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23885 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM Map of the NPR1-SA complex | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
| 生物種 |  | ||||||||||||
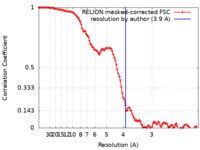
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | ||||||||||||
 データ登録者 データ登録者 | Kumar S / Zhou Y / Dillard L / Borgnia M / Bartesaghi A / Zhou P | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2022 ジャーナル: Nature / 年: 2022タイトル: Structural basis of NPR1 in activating plant immunity. 著者: Shivesh Kumar / Raul Zavaliev / Qinglin Wu / Ye Zhou / Jie Cheng / Lucas Dillard / Jordan Powers / John Withers / Jinshi Zhao / Ziqiang Guan / Mario J Borgnia / Alberto Bartesaghi / Xinnian Dong / Pei Zhou /  要旨: NPR1 is a master regulator of the defence transcriptome induced by the plant immune signal salicylic acid. Despite the important role of NPR1 in plant immunity, understanding of its regulatory ...NPR1 is a master regulator of the defence transcriptome induced by the plant immune signal salicylic acid. Despite the important role of NPR1 in plant immunity, understanding of its regulatory mechanisms has been hindered by a lack of structural information. Here we report cryo-electron microscopy and crystal structures of Arabidopsis NPR1 and its complex with the transcription factor TGA3. Cryo-electron microscopy analysis reveals that NPR1 is a bird-shaped homodimer comprising a central Broad-complex, Tramtrack and Bric-à-brac (BTB) domain, a BTB and carboxyterminal Kelch helix bundle, four ankyrin repeats and a disordered salicylic-acid-binding domain. Crystal structure analysis reveals a unique zinc-finger motif in BTB for interacting with ankyrin repeats and mediating NPR1 oligomerization. We found that, after stimulation, salicylic-acid-induced folding and docking of the salicylic-acid-binding domain onto ankyrin repeats is required for the transcriptional cofactor activity of NPR1, providing a structural explanation for a direct role of salicylic acid in regulating NPR1-dependent gene expression. Moreover, our structure of the TGA3-NPR1-TGA3 complex, DNA-binding assay and genetic data show that dimeric NPR1 activates transcription by bridging two fatty-acid-bound TGA3 dimers to form an enhanceosome. The stepwise assembly of the NPR1-TGA complex suggests possible hetero-oligomeric complex formation with other transcription factors, revealing how NPR1 reprograms the defence transcriptome. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23885.map.gz emd_23885.map.gz | 98.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23885-v30.xml emd-23885-v30.xml emd-23885.xml emd-23885.xml | 14.6 KB 14.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23885_fsc.xml emd_23885_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23885.png emd_23885.png | 84.4 KB | ||
| マスクデータ |  emd_23885_msk_1.map emd_23885_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| その他 |  emd_23885_half_map_1.map.gz emd_23885_half_map_1.map.gz emd_23885_half_map_2.map.gz emd_23885_half_map_2.map.gz | 98.6 MB 98.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23885 http://ftp.pdbj.org/pub/emdb/structures/EMD-23885 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23885 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23885 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_23885_validation.pdf.gz emd_23885_validation.pdf.gz | 573 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_23885_full_validation.pdf.gz emd_23885_full_validation.pdf.gz | 572.5 KB | 表示 | |
| XML形式データ |  emd_23885_validation.xml.gz emd_23885_validation.xml.gz | 18.5 KB | 表示 | |
| CIF形式データ |  emd_23885_validation.cif.gz emd_23885_validation.cif.gz | 24.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23885 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23885 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23885 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23885 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23885.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23885.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.065 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
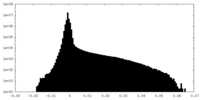
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_23885_msk_1.map emd_23885_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
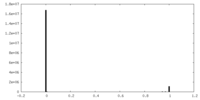
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_23885_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
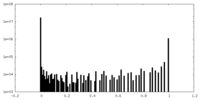
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_23885_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
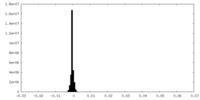
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : NPR1 in the presence of SA
| 全体 | 名称: NPR1 in the presence of SA |
|---|---|
| 要素 |
|
-超分子 #1: NPR1 in the presence of SA
| 超分子 | 名称: NPR1 in the presence of SA / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
-分子 #1: NPR1
| 分子 | 名称: NPR1 / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: GPLMDTTIDG FADSYEISST SFVATDNTDS SIVYLAAEQV LTGPDVSALQ LLSNSFESVF DSPDDFYSDA KLVLSDGREV SFHRCVLSA RSSFFKSALA AAKKEKDSNN TAAVKLELKE IAKDYEVGFD SVVTVLAYVY SSRVRPPPKG VSECADENCC H VACRPAVD ...文字列: GPLMDTTIDG FADSYEISST SFVATDNTDS SIVYLAAEQV LTGPDVSALQ LLSNSFESVF DSPDDFYSDA KLVLSDGREV SFHRCVLSA RSSFFKSALA AAKKEKDSNN TAAVKLELKE IAKDYEVGFD SVVTVLAYVY SSRVRPPPKG VSECADENCC H VACRPAVD FMLEVLYLAF IFKIPELITL YQRHLLDVVD KVVIEDTLVI LKLANICGKA CMKLLDRCKE IIVKSNVDMV SL EKSLPEE LVKEIIDRRK ELGLEVPKVK KHVSNVHKAL DSDDIELVKL LLKEDHTNLD DACALHFAVA YCNVKTATDL LKL DLADVN HRNPRGYTVL HVAAMRKEPQ LILSLLEKGA SASEATLEGR TALMIAKQAT MAVECNNIPE QCKHSLKGRL CVEI LEQED KREQIPRDVP PSFAVAADEL KMTLLDLENR VALAQRLFPT EAQAAMEIAE MKGTCEFIVT SLEPDRLTGT KRTSP GVKI APFRILEEHQ SRLKALSKTV ELGKRFFPRC SAVLDQIMNC EDLTQLACGE DDTAEKRLQK KQRYMEIQET LKKAFS EDN LELGNSSLTD STSSTSKSTG GKRSNRKLSH RRRGGWSHPQ FEK |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | モデル: UltrAuFoil / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: PLASMA CLEANING |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー


























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)