+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21910 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The yeast Ctf3 complex with Cnn1-Wip1 | |||||||||
 マップデータ マップデータ | CMMCW | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | kinetochore / cell cycle / chromosome segregation / CCAN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of kinetochore assembly / attachment of spindle microtubules to kinetochore / centromeric DNA binding / establishment of mitotic sister chromatid cohesion / mitotic spindle assembly checkpoint signaling / DNA replication initiation / meiotic cell cycle / chromosome segregation / kinetochore / cell division ...negative regulation of kinetochore assembly / attachment of spindle microtubules to kinetochore / centromeric DNA binding / establishment of mitotic sister chromatid cohesion / mitotic spindle assembly checkpoint signaling / DNA replication initiation / meiotic cell cycle / chromosome segregation / kinetochore / cell division / protein-containing complex binding / nucleus 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
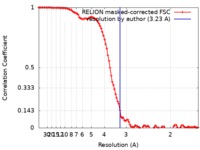
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.23 Å | |||||||||
 データ登録者 データ登録者 | Hinshaw SM / Harrison SC | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Curr Biol / 年: 2020 ジャーナル: Curr Biol / 年: 2020タイトル: The Structural Basis for Kinetochore Stabilization by Cnn1/CENP-T. 著者: Stephen M Hinshaw / Stephen C Harrison /  要旨: Chromosome segregation depends on a regulated connection between spindle microtubules and centromeric DNA. The kinetochore mediates this connection and ensures it persists during anaphase, when ...Chromosome segregation depends on a regulated connection between spindle microtubules and centromeric DNA. The kinetochore mediates this connection and ensures it persists during anaphase, when sister chromatids must transit into daughter cells uninterrupted. The Ctf19 complex (Ctf19c) forms the centromeric base of the kinetochore in budding yeast. Biochemical experiments show that Ctf19c members associate hierarchically when purified from cell extract [1], an observation that is mostly explained by the structure of the complex [2]. The Ctf3 complex (Ctf3c), which is not required for the assembly of most other Ctf19c factors, disobeys the biochemical assembly hierarchy when observed in dividing cells that lack more basal components [3]. Thus, the biochemical experiments do not completely recapitulate the logic of centromeric Ctf19c assembly. We now present a high-resolution structure of the Ctf3c bound to the Cnn1-Wip1 heterodimer. Associated live-cell imaging experiments provide a mechanism for Ctf3c and Cnn1-Wip1 recruitment to the kinetochore. The mechanism suggests feedback regulation of Ctf19c assembly and unanticipated similarities in kinetochore organization between yeast and vertebrates. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21910.map.gz emd_21910.map.gz | 77.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21910-v30.xml emd-21910-v30.xml emd-21910.xml emd-21910.xml | 20.4 KB 20.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_21910_fsc.xml emd_21910_fsc.xml | 10.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_21910.png emd_21910.png | 172.4 KB | ||
| Filedesc metadata |  emd-21910.cif.gz emd-21910.cif.gz | 6.9 KB | ||
| その他 |  emd_21910_additional.map.gz emd_21910_additional.map.gz | 77.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21910 http://ftp.pdbj.org/pub/emdb/structures/EMD-21910 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21910 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21910 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21910.map.gz / 形式: CCP4 / 大きさ: 93 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21910.map.gz / 形式: CCP4 / 大きさ: 93 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CMMCW | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.825 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: CMMCW-N
| ファイル | emd_21910_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CMMCW-N | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Single particle reconstruction of the Ctf3c bound to Cnn1-Wip1
| 全体 | 名称: Single particle reconstruction of the Ctf3c bound to Cnn1-Wip1 |
|---|---|
| 要素 |
|
-超分子 #1: Single particle reconstruction of the Ctf3c bound to Cnn1-Wip1
| 超分子 | 名称: Single particle reconstruction of the Ctf3c bound to Cnn1-Wip1 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Inner kinetochore subunit MCM16
| 分子 | 名称: Inner kinetochore subunit MCM16 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 21.438359 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SNAMTNSSEK QWERIQQLEK EHVEVYRELL ITLDRLYLIR KHNHAVILSH TQQRLLEIRH QLQINLEKTA LLIRLLEKPD NTNVLFTKL QNLLEESNSL DYELLQSLGA QSSLHKQLIE SRAERDELMS KLIELSSKFP KPTIPPDDSD TAGKQVEVEK E NETIQELM IALQIHSGYT NISYTI UniProtKB: Inner kinetochore subunit MCM16 |
-分子 #2: Inner kinetochore subunit CTF3
| 分子 | 名称: Inner kinetochore subunit CTF3 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 84.617891 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SNAMSLILDD IILSLTNANE RTPPQALKTT LSLLYEKSKQ YGLSSPQLQA LVRLLCETSI IDTVTKVYIV ENCFLPDGYL TKELLLEII NHLGTPTVFS RYRIQTPPVL QSALCKWLVH VYFLFPVHSE REHNISSSIW LHLWQFSFLQ KWITPLVIWQ A TTPVDVKP ...文字列: SNAMSLILDD IILSLTNANE RTPPQALKTT LSLLYEKSKQ YGLSSPQLQA LVRLLCETSI IDTVTKVYIV ENCFLPDGYL TKELLLEII NHLGTPTVFS RYRIQTPPVL QSALCKWLVH VYFLFPVHSE REHNISSSIW LHLWQFSFLQ KWITPLVIWQ A TTPVDVKP WKLSIIKRCA MHPGYRDAPG SATLILQRFQ CLVGASSQIT ESIITINCNR KTLKSHRNLK LDAHFLSILK RI LSRAHPA NFPADTVQNT IDMYLSEIHQ LGADSIYPLR LQSLPEYVPS DSTVSLWDVT SLEQLAQNWP QLHIPNDVDY MMK PSLNSN VLLPRKVMSR DSLKHLYSSI ILIKNSRDES SSPYEWCIWQ LKRCFAHQIE TPQEVIPIII SVSSMDNKLS SRII QTFCN LKYLKLDELT LKKVCGGILP LWKPELISGT REFFVKFMAS IFMWSTRDGH DNNCTFSETC FYVLQMITNW VLDDK LIAL GLTLLHDMQS LLTLDKIFNN ATSNRFSTMA FISSLDILTQ LSKQTKSDYA IQYLIVGPDI MNKVFSSDDP LLLSAA CRY LVATKNKLMQ YPSTNKFVRM QNQYIMDLTN YLYRNKVLSS KSLFGVSPDF FKQILENLYI PTADFKNAKF FTITGIP AL SYICIIILRR LETAENTKIK FTSGIINEET FNNFFRVHHD EIGQHGWIKG VNNIHDLRVK ILMHLSNTAN PYRDIAAF L FTYLKSLSKY SVQNS UniProtKB: Inner kinetochore subunit CTF3 |
-分子 #3: Inner kinetochore subunit MCM22
| 分子 | 名称: Inner kinetochore subunit MCM22 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 27.874799 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SNAMDVEKDV LDVYIKNLEN QIGNKRYFLK QAQGAIDEIT KRSLDTEGKP VNSEVFTELL RKPMFFSERA DPIGFSLTSN FLSLRAQSS SEWLSLMNDQ SVDQKAMLLL QNNINSDLKE LLRKLQHQMT IMDSKKQDHA HIRTRKARNK ELWDSLADFL K GYLVPNLD ...文字列: SNAMDVEKDV LDVYIKNLEN QIGNKRYFLK QAQGAIDEIT KRSLDTEGKP VNSEVFTELL RKPMFFSERA DPIGFSLTSN FLSLRAQSS SEWLSLMNDQ SVDQKAMLLL QNNINSDLKE LLRKLQHQMT IMDSKKQDHA HIRTRKARNK ELWDSLADFL K GYLVPNLD DNDESIDSLT NEVMLLMKRL IEHDLNLTLN DFSSKTIPIY RLLLRANIIT VIEGSTNPGT KYIKLIDFNE TS LT UniProtKB: Inner kinetochore subunit MCM22 |
-分子 #4: Inner kinetochore subunit WIP1
| 分子 | 名称: Inner kinetochore subunit WIP1 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 10.527717 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: SNAMDTEALA NYLLRQLSLD AEENKLEDLL QRQNEDQESS QEYNKKLLLA CGFQAILRKI LLDARTRATA EGLREVYPYH IEAATQAFL DSQ UniProtKB: Inner kinetochore subunit WIP1 |
-分子 #5: Inner kinetochore subunit CNN1
| 分子 | 名称: Inner kinetochore subunit CNN1 / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 41.359785 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSTPRKAAGN NENTEVSEIR TPFRERALEE QRLKDEVLIR NTPGYRKLLS ASTKSHDILN KDPNEVRSFL QDLSQVLARK SQGNDTTTN KTQARNLIDE LAYEESQPEE NELLRSRSEK LTDNNIGNET QPDYTSLSQT VFAKLQERDK GLKSRKIDPI I IQDVPTTG ...文字列: MSTPRKAAGN NENTEVSEIR TPFRERALEE QRLKDEVLIR NTPGYRKLLS ASTKSHDILN KDPNEVRSFL QDLSQVLARK SQGNDTTTN KTQARNLIDE LAYEESQPEE NELLRSRSEK LTDNNIGNET QPDYTSLSQT VFAKLQERDK GLKSRKIDPI I IQDVPTTG HEDELTVHSP DKANSISMEV LRTSPSIGMD QVDEPPVRDP VPISITQQEE PLSEDLPSDD KEETEEAENE DY SFENTSD ENLDDIGNDP IRLNVPAVRR SSIKPLQIMD LKHLTRQFLN ENRIILPKQT WSTIQEESLN IMDFLKQKIG TLQ KQELVD SFIDMGIINN VDDMFELAHE LLPLELQSRI ESYLF UniProtKB: Inner kinetochore subunit CNN1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)