[English] 日本語
 Yorodumi
Yorodumi- PDB-6wti: The Cryo-EM structure of the ubiquinol oxidase from Escherichia coli -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6wti | ||||||
|---|---|---|---|---|---|---|---|
| Title | The Cryo-EM structure of the ubiquinol oxidase from Escherichia coli | ||||||
 Components Components |
| ||||||
 Keywords Keywords | OXIDOREDUCTASE / ubiquinol oxidase cytochrome bo3 / membrane protein | ||||||
| Function / homology |  Function and homology information Function and homology informationcytochrome bo3 ubiquinol oxidase activity => GO:0009486 / oxidoreduction-driven active transmembrane transporter activity / cytochrome o ubiquinol oxidase complex / ubiquinol oxidase (H+-transporting) / cytochrome bo3 ubiquinol oxidase activity / aerobic electron transport chain / : / oxidoreductase activity, acting on diphenols and related substances as donors, oxygen as acceptor / respiratory chain complex / cytochrome-c oxidase activity ...cytochrome bo3 ubiquinol oxidase activity => GO:0009486 / oxidoreduction-driven active transmembrane transporter activity / cytochrome o ubiquinol oxidase complex / ubiquinol oxidase (H+-transporting) / cytochrome bo3 ubiquinol oxidase activity / aerobic electron transport chain / : / oxidoreductase activity, acting on diphenols and related substances as donors, oxygen as acceptor / respiratory chain complex / cytochrome-c oxidase activity / proton transmembrane transporter activity / ubiquinone binding / electron transport coupled proton transport / membrane => GO:0016020 / ATP synthesis coupled electron transport / aerobic respiration / respiratory electron transport chain / electron transfer activity / copper ion binding / heme binding / plasma membrane Similarity search - Function | ||||||
| Biological species |  | ||||||
| Method | ELECTRON MICROSCOPY / single particle reconstruction / cryo EM / Resolution: 2.38 Å | ||||||
 Authors Authors | Su, C.-C. | ||||||
| Funding support |  United States, 1items United States, 1items
| ||||||
 Citation Citation |  Journal: Nat Methods / Year: 2021 Journal: Nat Methods / Year: 2021Title: A 'Build and Retrieve' methodology to simultaneously solve cryo-EM structures of membrane proteins. Authors: Chih-Chia Su / Meinan Lyu / Christopher E Morgan / Jani Reddy Bolla / Carol V Robinson / Edward W Yu /   Abstract: Single-particle cryo-electron microscopy (cryo-EM) has become a powerful technique in the field of structural biology. However, the inability to reliably produce pure, homogeneous membrane protein ...Single-particle cryo-electron microscopy (cryo-EM) has become a powerful technique in the field of structural biology. However, the inability to reliably produce pure, homogeneous membrane protein samples hampers the progress of their structural determination. Here, we develop a bottom-up iterative method, Build and Retrieve (BaR), that enables the identification and determination of cryo-EM structures of a variety of inner and outer membrane proteins, including membrane protein complexes of different sizes and dimensions, from a heterogeneous, impure protein sample. We also use the BaR methodology to elucidate structural information from Escherichia coli K12 crude membrane and raw lysate. The findings demonstrate that it is possible to solve high-resolution structures of a number of relatively small (<100 kDa) and less abundant (<10%) unidentified membrane proteins within a single, heterogeneous sample. Importantly, these results highlight the potential of cryo-EM for systems structural proteomics. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Movie |
 Movie viewer Movie viewer |
|---|---|
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6wti.cif.gz 6wti.cif.gz | 236.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6wti.ent.gz pdb6wti.ent.gz | 183.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6wti.json.gz 6wti.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/wt/6wti https://data.pdbj.org/pub/pdb/validation_reports/wt/6wti ftp://data.pdbj.org/pub/pdb/validation_reports/wt/6wti ftp://data.pdbj.org/pub/pdb/validation_reports/wt/6wti | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  21897MC  6wtzC  6wu0C  6wu6C  7jz2C  7jz3C  7jz6C  7jzhC M: map data used to model this data C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
|
|---|---|
| 1 |
|
- Components
Components
-Cytochrome o ubiquinol oxidase, subunit ... , 2 types, 2 molecules AD
| #1: Protein | Mass: 74424.469 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   References: UniProt: H4KCU1, UniProt: P0ABI8*PLUS, Oxidoreductases; Acting on diphenols and related substances as donors; With oxygen as acceptor |
|---|---|
| #4: Protein | Mass: 12037.402 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   References: UniProt: I2RK84, UniProt: P0ABJ6*PLUS, Oxidoreductases; Acting on diphenols and related substances as donors; With oxygen as acceptor |
-Protein , 2 types, 2 molecules BC
| #2: Protein | Mass: 34947.203 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   |
|---|---|
| #3: Protein | Mass: 22642.566 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   |
-Non-polymers , 6 types, 14 molecules 




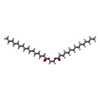





| #5: Chemical | ChemComp-HEM / | ||
|---|---|---|---|
| #6: Chemical | ChemComp-HEO / | ||
| #7: Chemical | ChemComp-CU / | ||
| #8: Chemical | ChemComp-UQ8 / | ||
| #9: Chemical | ChemComp-3PE / #10: Chemical | ChemComp-U9V / | |
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method: ELECTRON MICROSCOPY |
|---|---|
| EM experiment | Aggregation state: PARTICLE / 3D reconstruction method: single particle reconstruction |
- Sample preparation
Sample preparation
| Component | Name: ubiquinol oxidase / Type: COMPLEX / Entity ID: #1-#4 / Source: RECOMBINANT |
|---|---|
| Source (natural) | Organism:  |
| Source (recombinant) | Organism:  |
| Buffer solution | pH: 7.5 |
| Specimen | Conc.: 0.5 mg/ml / Embedding applied: NO / Shadowing applied: NO / Staining applied: NO / Vitrification applied: YES |
| Specimen support | Grid material: COPPER / Grid mesh size: 300 divisions/in. / Grid type: Quantifoil R1.2/1.3 |
| Vitrification | Cryogen name: ETHANE |
- Electron microscopy imaging
Electron microscopy imaging
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
|---|---|
| Microscopy | Model: FEI TITAN KRIOS |
| Electron gun | Electron source:  FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: FLOOD BEAM FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: FLOOD BEAM |
| Electron lens | Mode: BRIGHT FIELD |
| Image recording | Electron dose: 50 e/Å2 / Film or detector model: GATAN K3 BIOQUANTUM (6k x 4k) |
- Processing
Processing
| CTF correction | Type: PHASE FLIPPING AND AMPLITUDE CORRECTION |
|---|---|
| 3D reconstruction | Resolution: 2.38 Å / Resolution method: FSC 0.143 CUT-OFF / Num. of particles: 334222 / Symmetry type: POINT |
 Movie
Movie Controller
Controller



















 PDBj
PDBj












