+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Intact V-ATPase State 3 and synaptophysin complex in mouse brain isolated synaptic vesicles | |||||||||
 マップデータ マップデータ | Full map of V-ATPase State 3 synaptophysin complex in wild-type ISVs. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  V-ATPase / V-ATPase /  synaptic vesicle (シナプス小胞) / synaptic vesicle (シナプス小胞) /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of opioid receptor signaling pathway / Ion channel transport / Amino acids regulate mTORC1 / clathrin-sculpted glutamate transport vesicle membrane / Transferrin endocytosis and recycling /  ヒトの虹彩の色 / Insulin receptor recycling / ヒトの虹彩の色 / Insulin receptor recycling /  central nervous system maturation / transporter activator activity / negative regulation of autophagic cell death ...regulation of opioid receptor signaling pathway / Ion channel transport / Amino acids regulate mTORC1 / clathrin-sculpted glutamate transport vesicle membrane / Transferrin endocytosis and recycling / central nervous system maturation / transporter activator activity / negative regulation of autophagic cell death ...regulation of opioid receptor signaling pathway / Ion channel transport / Amino acids regulate mTORC1 / clathrin-sculpted glutamate transport vesicle membrane / Transferrin endocytosis and recycling /  ヒトの虹彩の色 / Insulin receptor recycling / ヒトの虹彩の色 / Insulin receptor recycling /  central nervous system maturation / transporter activator activity / negative regulation of autophagic cell death / RHOA GTPase cycle / rostrocaudal neural tube patterning / Metabolism of Angiotensinogen to Angiotensins / cellular response to increased oxygen levels / positive regulation of transforming growth factor beta1 production / proton-transporting V-type ATPase, V1 domain / synaptic vesicle lumen acidification / endosome to plasma membrane protein transport / proton-transporting V-type ATPase, V0 domain / central nervous system maturation / transporter activator activity / negative regulation of autophagic cell death / RHOA GTPase cycle / rostrocaudal neural tube patterning / Metabolism of Angiotensinogen to Angiotensins / cellular response to increased oxygen levels / positive regulation of transforming growth factor beta1 production / proton-transporting V-type ATPase, V1 domain / synaptic vesicle lumen acidification / endosome to plasma membrane protein transport / proton-transporting V-type ATPase, V0 domain /  extrinsic component of synaptic vesicle membrane / P-type proton-exporting transporter activity / ROS and RNS production in phagocytes / intracellular organelle / plasma membrane proton-transporting V-type ATPase complex / lysosomal lumen acidification / clathrin-coated vesicle membrane / vacuolar proton-transporting V-type ATPase, V1 domain / vacuolar proton-transporting V-type ATPase, V0 domain / endosomal lumen acidification / vacuolar transport / proton-transporting V-type ATPase complex / neuron spine / head morphogenesis / vacuolar proton-transporting V-type ATPase complex / protein localization to cilium / regulation of short-term neuronal synaptic plasticity / neuron projection terminus / vacuolar acidification / dendritic spine membrane / regulation of cellular pH / extrinsic component of synaptic vesicle membrane / P-type proton-exporting transporter activity / ROS and RNS production in phagocytes / intracellular organelle / plasma membrane proton-transporting V-type ATPase complex / lysosomal lumen acidification / clathrin-coated vesicle membrane / vacuolar proton-transporting V-type ATPase, V1 domain / vacuolar proton-transporting V-type ATPase, V0 domain / endosomal lumen acidification / vacuolar transport / proton-transporting V-type ATPase complex / neuron spine / head morphogenesis / vacuolar proton-transporting V-type ATPase complex / protein localization to cilium / regulation of short-term neuronal synaptic plasticity / neuron projection terminus / vacuolar acidification / dendritic spine membrane / regulation of cellular pH /  syntaxin-1 binding / osteoclast development / regulation of synaptic vesicle exocytosis / : / syntaxin-1 binding / osteoclast development / regulation of synaptic vesicle exocytosis / : /  cholesterol binding / cholesterol binding /  ATPase complex / presynaptic active zone / regulation of neuronal synaptic plasticity / autophagosome membrane / ATPase complex / presynaptic active zone / regulation of neuronal synaptic plasticity / autophagosome membrane /  微絨毛 / 微絨毛 /  regulation of MAPK cascade / ATPase activator activity / synaptic vesicle endocytosis / regulation of MAPK cascade / ATPase activator activity / synaptic vesicle endocytosis /  excitatory synapse / transmembrane transporter complex / positive regulation of Wnt signaling pathway / excitatory synapse / transmembrane transporter complex / positive regulation of Wnt signaling pathway /  cilium assembly / angiotensin maturation / cilium assembly / angiotensin maturation /  regulation of macroautophagy / regulation of macroautophagy /  細胞内膜系 / axon terminus / ATP metabolic process / 細胞内膜系 / axon terminus / ATP metabolic process /  ATP合成酵素 / phagocytic vesicle / RNA endonuclease activity / ruffle / proton transmembrane transport / proton-transporting ATPase activity, rotational mechanism / Neutrophil degranulation / endoplasmic reticulum-Golgi intermediate compartment membrane / ATP合成酵素 / phagocytic vesicle / RNA endonuclease activity / ruffle / proton transmembrane transport / proton-transporting ATPase activity, rotational mechanism / Neutrophil degranulation / endoplasmic reticulum-Golgi intermediate compartment membrane /  SH2 domain binding / proton-transporting ATP synthase activity, rotational mechanism / SH2 domain binding / proton-transporting ATP synthase activity, rotational mechanism /  SNARE binding / SNARE binding /  receptor-mediated endocytosis / receptor-mediated endocytosis /  分泌 / regulation of long-term neuronal synaptic plasticity / Schaffer collateral - CA1 synapse / 分泌 / regulation of long-term neuronal synaptic plasticity / Schaffer collateral - CA1 synapse /  neuromuscular junction / neuromuscular junction /  terminal bouton / transmembrane transport / terminal bouton / transmembrane transport /  繊毛 / synaptic vesicle membrane / 繊毛 / synaptic vesicle membrane /  small GTPase binding / small GTPase binding /  エンドサイトーシス / エンドサイトーシス /  メラノソーム / positive regulation of canonical Wnt signaling pathway / メラノソーム / positive regulation of canonical Wnt signaling pathway /  シナプス小胞 / presynapse / apical part of cell / シナプス小胞 / presynapse / apical part of cell /  髄鞘 / 髄鞘 /  presynaptic membrane / presynaptic membrane /  signaling receptor activity / signaling receptor activity /  cell body / cell body /  ATPase binding / chemical synaptic transmission / ATPase binding / chemical synaptic transmission /  postsynaptic membrane / intracellular iron ion homeostasis / receptor-mediated endocytosis of virus by host cell / postsynaptic membrane / intracellular iron ion homeostasis / receptor-mediated endocytosis of virus by host cell /  加水分解酵素; エステル加水分解酵素 / 加水分解酵素; エステル加水分解酵素 /  postsynaptic density postsynaptic density類似検索 - 分子機能 | |||||||||
| 生物種 |   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.3 Å クライオ電子顕微鏡法 / 解像度: 4.3 Å | |||||||||
 データ登録者 データ登録者 | Wang C / Jiang W / Yang K / Wang X / Guo Q / Brunger AT | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2024 ジャーナル: Nature / 年: 2024タイトル: Structure and topography of the synaptic V-ATPase-synaptophysin complex. 著者: Chuchu Wang / Wenhong Jiang / Jeremy Leitz / Kailu Yang / Luis Esquivies / Xing Wang / Xiaotao Shen / Richard Held / Daniel J Adams / Tamara Basta / Lucas Hampton / Ruiqi Jian / Lihua Jiang / ...著者: Chuchu Wang / Wenhong Jiang / Jeremy Leitz / Kailu Yang / Luis Esquivies / Xing Wang / Xiaotao Shen / Richard Held / Daniel J Adams / Tamara Basta / Lucas Hampton / Ruiqi Jian / Lihua Jiang / Michael H B Stowell / Wolfgang Baumeister / Qiang Guo / Axel T Brunger /    要旨: Synaptic vesicles are organelles with a precisely defined protein and lipid composition, yet the molecular mechanisms for the biogenesis of synaptic vesicles are mainly unknown. Here, we discovered a ...Synaptic vesicles are organelles with a precisely defined protein and lipid composition, yet the molecular mechanisms for the biogenesis of synaptic vesicles are mainly unknown. Here, we discovered a well-defined interface between the synaptic vesicle V-ATPase and synaptophysin by in situ cryo-electron tomography and single particle cryo-electron microscopy of functional synaptic vesicles isolated from mouse brains. The synaptic vesicle V-ATPase is an ATP-dependent proton pump that establishes the protein gradient across the synaptic vesicle, which in turn drives the uptake of neurotransmitters. Synaptophysin and its paralogs synaptoporin and synaptogyrin belong to a family of abundant synaptic vesicle proteins whose function is still unclear. We performed structural and functional studies of synaptophysin knockout mice, confirming the identity of synaptophysin as an interaction partner with the V-ATPase. Although there is little change in the conformation of the V-ATPase upon interaction with synaptophysin, the presence of synaptophysin in synaptic vesicles profoundly affects the copy number of V-ATPases. This effect on the topography of synaptic vesicles suggests that synaptophysin assists in their biogenesis. In support of this model, we observed that synaptophysin knockout mice exhibit severe seizure susceptibility, suggesting an imbalance of neurotransmitter release as a physiological consequence of the absence of synaptophysin. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_44840.map.gz emd_44840.map.gz | 322 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-44840-v30.xml emd-44840-v30.xml emd-44840.xml emd-44840.xml | 39 KB 39 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_44840.png emd_44840.png | 152.9 KB | ||
| Filedesc metadata |  emd-44840.cif.gz emd-44840.cif.gz | 10 KB | ||
| その他 |  emd_44840_additional_1.map.gz emd_44840_additional_1.map.gz emd_44840_additional_2.map.gz emd_44840_additional_2.map.gz emd_44840_half_map_1.map.gz emd_44840_half_map_1.map.gz emd_44840_half_map_2.map.gz emd_44840_half_map_2.map.gz | 319.3 MB 273.8 MB 318 MB 318 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-44840 http://ftp.pdbj.org/pub/emdb/structures/EMD-44840 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-44840 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-44840 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9brqMC  9braC  9brrC  9brsC  9brtC  9bruC  9bryC  9brzC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_44840.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_44840.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full map of V-ATPase State 3 synaptophysin complex in wild-type ISVs. | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.11138 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: EMhancer map of V-ATPase State 3 synaptophysin complex...
| ファイル | emd_44840_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EMhancer map of V-ATPase State 3 synaptophysin complex in wild-type ISVs. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
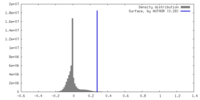
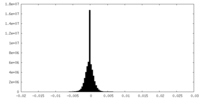
| 密度ヒストグラム |
-追加マップ: Unsharpened map of V-ATPase State 3
| ファイル | emd_44840_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map of V-ATPase State 3 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
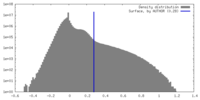
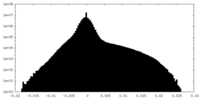
| 密度ヒストグラム |
-ハーフマップ: Half map of V-ATPase State 3 synaptophysin complex in wild-type ISVs.
| ファイル | emd_44840_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map of V-ATPase State 3 synaptophysin complex in wild-type ISVs. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
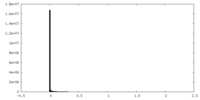
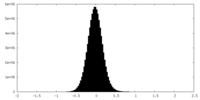
| 密度ヒストグラム |
-ハーフマップ: Half map of V-ATPase State 3 synaptophysin complex in wild-type ISVs.
| ファイル | emd_44840_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map of V-ATPase State 3 synaptophysin complex in wild-type ISVs. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
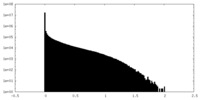
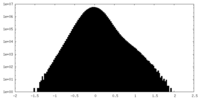
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Mouse brain isolated glutamatergic synaptic vesicles
+超分子 #1: Mouse brain isolated glutamatergic synaptic vesicles
+分子 #1: V-type proton ATPase 21 kDa proteolipid subunit c''
+分子 #2: V-type proton ATPase 16 kDa proteolipid subunit c
+分子 #3: V-type proton ATPase catalytic subunit A
+分子 #4: V-type proton ATPase subunit B, brain isoform
+分子 #5: V-type proton ATPase subunit D
+分子 #6: V-type proton ATPase subunit E 1
+分子 #7: V-type proton ATPase subunit G 2
+分子 #8: V-type proton ATPase subunit F
+分子 #9: V-type proton ATPase subunit C 1
+分子 #10: V-type proton ATPase subunit H
+分子 #11: V-type proton ATPase subunit d 1
+分子 #12: V-type proton ATPase 116 kDa subunit a 1
+分子 #13: V-type proton ATPase subunit S1
+分子 #14: Renin receptor cytoplasmic fragment
+分子 #15: Ribonuclease kappa
+分子 #16: Synaptophysin
+分子 #17: V-type proton ATPase subunit e 2
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | cell |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
| 詳細 | The specimen state should be an intact subcellular component. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.0 µm Bright-field microscopy / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER |
|---|---|
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 34536 |
-原子モデル構築 1
| 精密化 | プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-9brq: |
 ムービー
ムービー コントローラー
コントローラー





























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)