+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22898 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of SARS-CoV-2 ORF3a | |||||||||
 マップデータ マップデータ | Sharpened and locally filtered map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | SARS-CoV-2 / coronavirus / transport protein / viral protein / viroporin / membrane protein | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報host cell lysosome / induction by virus of host reticulophagy / Maturation of protein 3a / Defective ABCA1 causes TGD / Scavenging by Class B Receptors / HDL clearance / high-density lipoprotein particle receptor binding / spherical high-density lipoprotein particle / positive regulation of hydrolase activity / SARS-CoV-2 modulates autophagy ...host cell lysosome / induction by virus of host reticulophagy / Maturation of protein 3a / Defective ABCA1 causes TGD / Scavenging by Class B Receptors / HDL clearance / high-density lipoprotein particle receptor binding / spherical high-density lipoprotein particle / positive regulation of hydrolase activity / SARS-CoV-2 modulates autophagy / negative regulation of response to cytokine stimulus / regulation of intestinal cholesterol absorption / protein oxidation / vitamin transport / cholesterol import / high-density lipoprotein particle binding / ABC transporters in lipid homeostasis / blood vessel endothelial cell migration / negative regulation of heterotypic cell-cell adhesion / apolipoprotein receptor binding / apolipoprotein A-I receptor binding / negative regulation of cytokine production involved in immune response / negative regulation of cell adhesion molecule production / HDL assembly / negative regulation of very-low-density lipoprotein particle remodeling / peptidyl-methionine modification / phosphatidylcholine biosynthetic process / glucocorticoid metabolic process / acylglycerol homeostasis / Chylomicron remodeling / phosphatidylcholine-sterol O-acyltransferase activator activity / positive regulation of phospholipid efflux / Chylomicron assembly / positive regulation of cholesterol metabolic process / lipid storage / high-density lipoprotein particle clearance / phospholipid homeostasis / chylomicron / high-density lipoprotein particle remodeling / phospholipid efflux / chemorepellent activity / very-low-density lipoprotein particle / reverse cholesterol transport / cholesterol transfer activity / high-density lipoprotein particle assembly / cholesterol transport / low-density lipoprotein particle / positive regulation of CoA-transferase activity / lipoprotein biosynthetic process / high-density lipoprotein particle / regulation of Cdc42 protein signal transduction / triglyceride homeostasis / inorganic cation transmembrane transport / HDL remodeling / endothelial cell proliferation / voltage-gated calcium channel complex / negative regulation of interleukin-1 beta production / Scavenging by Class A Receptors / cholesterol efflux / host cell endoplasmic reticulum / negative chemotaxis / adrenal gland development / positive regulation of Rho protein signal transduction / cholesterol binding / cholesterol biosynthetic process / endocytic vesicle / negative regulation of tumor necrosis factor-mediated signaling pathway / positive regulation of cholesterol efflux / Scavenging of heme from plasma / SARS-CoV-2 targets host intracellular signalling and regulatory pathways / Retinoid metabolism and transport / positive regulation of substrate adhesion-dependent cell spreading / positive regulation of phagocytosis / voltage-gated potassium channel complex / positive regulation of stress fiber assembly / endocytic vesicle lumen / heat shock protein binding / cholesterol metabolic process / molecular function activator activity / integrin-mediated signaling pathway / cholesterol homeostasis / Post-translational protein phosphorylation / regulation of protein phosphorylation / Heme signaling / PPARA activates gene expression / cytoplasmic side of plasma membrane / phospholipid binding / negative regulation of inflammatory response / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / extracellular vesicle / Platelet degranulation / protein complex oligomerization / monoatomic ion channel activity / amyloid-beta binding / host cell endosome / cytoplasmic vesicle / secretory granule lumen / collagen-containing extracellular matrix / Translation of Structural Proteins / Virion Assembly and Release 類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.08 Å | |||||||||
 データ登録者 データ登録者 | Kern DM / Hoel CM | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 | ジャーナル: bioRxiv / 年: 2021 タイトル: Cryo-EM structure of the SARS-CoV-2 3a ion channel in lipid nanodiscs. 著者: David M Kern / Ben Sorum / Sonali S Mali / Christopher M Hoel / Savitha Sridharan / Jonathan P Remis / Daniel B Toso / Abhay Kotecha / Diana M Bautista / Stephen G Brohawn /   要旨: Severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) is the virus that causes the coronavirus disease 2019 (COVID-19). SARS-CoV-2 encodes three putative ion channels: E, 8a, and 3a. 3a is ...Severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) is the virus that causes the coronavirus disease 2019 (COVID-19). SARS-CoV-2 encodes three putative ion channels: E, 8a, and 3a. 3a is expressed in SARS patient tissue and anti-3a antibodies are observed in patient plasma. 3a has been implicated in viral release, inhibition of autophagy, inflammasome activation, and cell death and its deletion reduces viral titer and morbidity in mice, raising the possibility that 3a could be an effective vaccine or therapeutic target. Here, we present the first cryo-EM structures of SARS-CoV-2 3a to 2.1 Å resolution and demonstrate 3a forms an ion channel in reconstituted liposomes. The structures in lipid nanodiscs reveal 3a dimers and tetramers adopt a novel fold with a large polar cavity that spans halfway across the membrane and is accessible to the cytosol and the surrounding bilayer through separate water- and lipid-filled openings. Electrophysiology and fluorescent ion imaging experiments show 3a forms Ca-permeable non-selective cation channels. We identify point mutations that alter ion permeability and discover polycationic inhibitors of 3a channel activity. We find 3a-like proteins in multiple and lineages that infect bats and humans. These data show 3a forms a functional ion channel that may promote COVID-19 pathogenesis and suggest targeting 3a could broadly treat coronavirus diseases. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22898.map.gz emd_22898.map.gz | 3.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22898-v30.xml emd-22898-v30.xml emd-22898.xml emd-22898.xml | 21.1 KB 21.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_22898.png emd_22898.png | 152.7 KB | ||
| Filedesc metadata |  emd-22898.cif.gz emd-22898.cif.gz | 6.2 KB | ||
| その他 |  emd_22898_additional_1.map.gz emd_22898_additional_1.map.gz emd_22898_half_map_1.map.gz emd_22898_half_map_1.map.gz emd_22898_half_map_2.map.gz emd_22898_half_map_2.map.gz | 5.7 MB 95.6 MB 95.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22898 http://ftp.pdbj.org/pub/emdb/structures/EMD-22898 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22898 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22898 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22898_validation.pdf.gz emd_22898_validation.pdf.gz | 885.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22898_full_validation.pdf.gz emd_22898_full_validation.pdf.gz | 884.7 KB | 表示 | |
| XML形式データ |  emd_22898_validation.xml.gz emd_22898_validation.xml.gz | 13.6 KB | 表示 | |
| CIF形式データ |  emd_22898_validation.cif.gz emd_22898_validation.cif.gz | 15.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22898 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22898 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22898 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22898 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7kjrMC  6xdcC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10612 (タイトル: High-resolution SARS-CoV-2 ORF3a dimer in an MSP1E3D1 lipid nanodisc EMPIAR-10612 (タイトル: High-resolution SARS-CoV-2 ORF3a dimer in an MSP1E3D1 lipid nanodiscData size: 3.2 TB Data #1: Unaligned movies in EER format of SARS-CoV-2 3a in MSP1E3D1 lipid nanodiscs - 1379 frames [micrographs - multiframe] Data #2: Unaligned movies in EER format of SARS-CoV-2 3a in MSP1E3D1 lipid nanodiscs - 1449 frames [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22898.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22898.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened and locally filtered map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.727 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Density modified map
| ファイル | emd_22898_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Density modified map | ||||||||||||
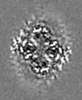
| 投影像・断面図 |
| ||||||||||||
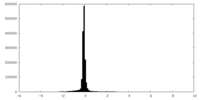
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_22898_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
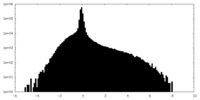
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_22898_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
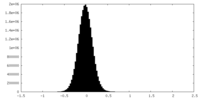
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SARS-CoV-2 protein 3A in lipid nanodiscs
| 全体 | 名称: SARS-CoV-2 protein 3A in lipid nanodiscs |
|---|---|
| 要素 |
|
-超分子 #1: SARS-CoV-2 protein 3A in lipid nanodiscs
| 超分子 | 名称: SARS-CoV-2 protein 3A in lipid nanodiscs / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 62 KDa |
-分子 #1: ORF3a protein
| 分子 | 名称: ORF3a protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 32.165902 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDLFMRIFTI GTVTLKQGEI KDATPSDFVR ATATIPIQAS LPFGWLIVGV ALLAVFQSAS KIITLKKRWQ LALSKGVHFV CNLLLLFVT VYSHLLLVAA GLEAPFLYLY ALVYFLQSIN FVRIIMRLWL CWKCRSKNPL LYDANYFLCW HTNCYDYCIP Y NSVTSSIV ...文字列: MDLFMRIFTI GTVTLKQGEI KDATPSDFVR ATATIPIQAS LPFGWLIVGV ALLAVFQSAS KIITLKKRWQ LALSKGVHFV CNLLLLFVT VYSHLLLVAA GLEAPFLYLY ALVYFLQSIN FVRIIMRLWL CWKCRSKNPL LYDANYFLCW HTNCYDYCIP Y NSVTSSIV ITSGDGTTSP ISEHDYQIGG YTEKWESGVK DCVVLHSYFT SDYYQLYSTQ LSTDTGVEHV TFFIYNKIVD EP EEHVQIH TIDGSSGVVN PVMEPIYDEP TTTTSVPLSN SLEVLFQ UniProtKB: ORF3a protein |
-分子 #2: Apolipoprotein A-I
| 分子 | 名称: Apolipoprotein A-I / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.647678 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: HHHHHHHDYD IPTTENLYFQ GSTFSKLREQ LGPVTQEFWD NLEKETEGLR QEMSKDLEEV KAKVQPYLDD FQKKWQEEME LYRQKVEPL RAELQEGARQ KLHELQEKLS PLGEEMRDRA RAHVDALRTH LAPYSDELRQ RLAARLEALK ENGGARLAEY H AKATEHLS ...文字列: HHHHHHHDYD IPTTENLYFQ GSTFSKLREQ LGPVTQEFWD NLEKETEGLR QEMSKDLEEV KAKVQPYLDD FQKKWQEEME LYRQKVEPL RAELQEGARQ KLHELQEKLS PLGEEMRDRA RAHVDALRTH LAPYSDELRQ RLAARLEALK ENGGARLAEY H AKATEHLS TLSEKAKPAL EDLRQGLLPV LESFKVSFLS ALEEYTKKLN TQ UniProtKB: Apolipoprotein A-I |
-分子 #3: 1,2-dioleoyl-sn-glycero-3-phosphoethanolamine
| 分子 | 名称: 1,2-dioleoyl-sn-glycero-3-phosphoethanolamine / タイプ: ligand / ID: 3 / コピー数: 2 / 式: PEE |
|---|---|
| 分子量 | 理論値: 744.034 Da |
| Chemical component information |  ChemComp-PEE: |
-分子 #4: water
| 分子 | 名称: water / タイプ: ligand / ID: 4 / コピー数: 122 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.1 mg/mL | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| |||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE | |||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV 詳細: 1 blot force 5 second wait time 3 second blot time. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER / 詳細: Ab initio model |
|---|---|
| 最終 再構成 | 使用したクラス数: 1 / 解像度のタイプ: BY AUTHOR / 解像度: 2.08 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 91218 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|---|
| 得られたモデル |  PDB-7kjr: |
 ムービー
ムービー コントローラー
コントローラー






























 Z
Z Y
Y X
X