+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9269 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Single-Molecule 3D Image of Low-Density Lipoprotein in Complex with Cholesteryl Ester Transfer Protein (No. 02) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
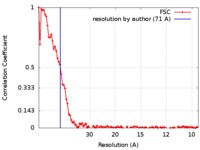
| 手法 | 電子線トモグラフィー法 / クライオ電子顕微鏡法 / 解像度: 71.0 Å | |||||||||
 データ登録者 データ登録者 | Wu H / Zhai X / Lei D / Liu J / Yu Y / Bie R / Ren G | |||||||||
 引用 引用 |  ジャーナル: Sci Rep / 年: 2018 ジャーナル: Sci Rep / 年: 2018タイトル: An Algorithm for Enhancing the Image Contrast of Electron Tomography. 著者: Hao Wu / Xiaobo Zhai / Dongsheng Lei / Jianfang Liu / Yadong Yu / Rongfang Bie / Gang Ren /   要旨: Three-dimensional (3D) reconstruction of a single protein molecule is essential for understanding the relationship between the structural dynamics and functions of the protein. Electron tomography ...Three-dimensional (3D) reconstruction of a single protein molecule is essential for understanding the relationship between the structural dynamics and functions of the protein. Electron tomography (ET) provides a tool for imaging an individual particle of protein from a series of tilted angles. Individual-particle electron tomography (IPET) provides an approach for reconstructing a 3D density map from a single targeted protein particle (without averaging from different particles of this type of protein), in which the target particle was imaged from a series of tilting angles. However, owing to radiation damage limitations, low-dose images (high noise, and low image contrast) are often challenging to be aligned for 3D reconstruction at intermediate resolution (1-3 nm). Here, we propose a computational method to enhance the image contrast, without increasing any experimental dose, for IPET 3D reconstruction. Using an edge-preserving smoothing-based multi-scale image decomposition algorithm, this method can detect the object against a high-noise background and enhance the object image contrast without increasing the noise level or significantly decreasing the image resolution. The method was validated by using both negative staining (NS) ET and cryo-ET images. The successful 3D reconstruction of a small molecule (<100 kDa) indicated that this method can be used as a supporting tool to current ET 3D reconstruction methods for studying protein dynamics via structure determination from each individual particle of the same type of protein. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9269.map.gz emd_9269.map.gz | 3.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9269-v30.xml emd-9269-v30.xml emd-9269.xml emd-9269.xml | 10.9 KB 10.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_9269_fsc.xml emd_9269_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_9269.png emd_9269.png | 20.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9269 http://ftp.pdbj.org/pub/emdb/structures/EMD-9269 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9269 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9269 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_9269_validation.pdf.gz emd_9269_validation.pdf.gz | 79.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_9269_full_validation.pdf.gz emd_9269_full_validation.pdf.gz | 78.3 KB | 表示 | |
| XML形式データ |  emd_9269_validation.xml.gz emd_9269_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9269 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9269 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9269 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9269 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9269.map.gz / 形式: CCP4 / 大きさ: 3.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9269.map.gz / 形式: CCP4 / 大きさ: 3.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 4.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Human plasma low-density lipoprotein in complex with cholesteryl ...
| 全体 | 名称: Human plasma low-density lipoprotein in complex with cholesteryl ester transfer protein |
|---|---|
| 要素 |
|
-超分子 #1: Human plasma low-density lipoprotein in complex with cholesteryl ...
| 超分子 | 名称: Human plasma low-density lipoprotein in complex with cholesteryl ester transfer protein タイプ: complex / ID: 1 / 親要素: 0 詳細: Low-density lipoproteins (LDLs) were isolated from human plasma by density gradient ultracentrifugation (Children's Hospital Oakland Research Institute). Cholesteryl ester transfer protein ...詳細: Low-density lipoproteins (LDLs) were isolated from human plasma by density gradient ultracentrifugation (Children's Hospital Oakland Research Institute). Cholesteryl ester transfer protein (CETP) was produced by MERCK. LDL and CETP were incubated at 37 degC for 15 minutes at a molar ratio of ~4:1. |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 2.5 MDa |
-超分子 #2: Human plasma low-density lipoprotein
| 超分子 | 名称: Human plasma low-density lipoprotein / タイプ: complex / ID: 2 / 親要素: 1 詳細: Low-density lipoproteins (LDLs) were isolated from human plasma by density gradient ultracentrifugation (Children's Hospital Oakland Research Institute). |
|---|
-超分子 #3: Cholesteryl ester transfer protein
| 超分子 | 名称: Cholesteryl ester transfer protein / タイプ: organelle_or_cellular_component / ID: 3 / 親要素: 1 詳細: Cholesteryl ester transfer protein (CETP) was produced by MERCK. |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 組織: Blood Homo sapiens (ヒト) / 組織: Blood |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線トモグラフィー法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7 / 詳細: 1X Dulbeccos phosphate-buffered saline |
|---|---|
| グリッド | モデル: Homemade / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / 装置: LEICA EM GP |
| 詳細 | Low-density lipoproteins (LDLs) were isolated from human plasma by density gradient ultracentrifugation (Children's Hospital Oakland Research Institute). Cholesteryl ester transfer protein (CETP) was produced by MERCK. LDL and CETP were incubated at 37 degC for 15 minutes at a molar ratio of ~4:1. |
| 切片作成 | その他: NO SECTIONING |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | ZEISS LIBRA120PLUS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: In-column Omega Filter エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 平均電子線量: 0.26 e/Å2 |
| 電子線 | 加速電圧: 120 kV / 電子線源: LAB6 |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.2 mm / 倍率(公称値): 50000 |
 ムービー
ムービー コントローラー
コントローラー



 UCSF Chimera
UCSF Chimera













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)