[English] 日本語
 Yorodumi
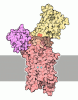
Yorodumi- PDB-7ky5: Structure of the S. cerevisiae phosphatidylcholine flippase Dnf2-... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7ky5 | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | Structure of the S. cerevisiae phosphatidylcholine flippase Dnf2-Lem3 complex in the E2P transition state | |||||||||||||||||||||
 Components Components |
| |||||||||||||||||||||
 Keywords Keywords | TRANSLOCASE / P4 ATPase / Phosphatidylcholine Flippases | |||||||||||||||||||||
| Function / homology |  Function and homology information Function and homology informationregulation of vacuole organization / glycosylceramide flippase activity / mating projection tip membrane / aminophospholipid translocation / Ion transport by P-type ATPases / aminophospholipid flippase activity / phosphatidylserine flippase activity / phospholipid-translocating ATPase complex / ceramide translocation / phosphatidylserine floppase activity ...regulation of vacuole organization / glycosylceramide flippase activity / mating projection tip membrane / aminophospholipid translocation / Ion transport by P-type ATPases / aminophospholipid flippase activity / phosphatidylserine flippase activity / phospholipid-translocating ATPase complex / ceramide translocation / phosphatidylserine floppase activity / ATPase-coupled intramembrane lipid carrier activity / phosphatidylcholine floppase activity / cellular bud neck / P-type phospholipid transporter / phospholipid translocation / establishment or maintenance of cell polarity / cell periphery / endocytosis / protein transport / cell surface receptor signaling pathway / magnesium ion binding / endoplasmic reticulum / Golgi apparatus / ATP hydrolysis activity / ATP binding / plasma membrane / cytoplasm Similarity search - Function | |||||||||||||||||||||
| Biological species |  | |||||||||||||||||||||
| Method | ELECTRON MICROSCOPY / single particle reconstruction / cryo EM / Resolution: 3.98 Å | |||||||||||||||||||||
 Authors Authors | Bai, L. / You, Q. / Jain, B.K. / Duan, H.D. / Kovach, A. / Graham, T.R. / Li, H. | |||||||||||||||||||||
| Funding support |  United States, 1items United States, 1items
| |||||||||||||||||||||
 Citation Citation |  Journal: Elife / Year: 2020 Journal: Elife / Year: 2020Title: Transport mechanism of P4 ATPase phosphatidylcholine flippases. Authors: Lin Bai / Qinglong You / Bhawik K Jain / H Diessel Duan / Amanda Kovach / Todd R Graham / Huilin Li /   Abstract: The P4 ATPases use ATP hydrolysis to transport large lipid substrates across lipid bilayers. The structures of the endosome- and Golgi-localized phosphatidylserine flippases-such as the yeast Drs2 ...The P4 ATPases use ATP hydrolysis to transport large lipid substrates across lipid bilayers. The structures of the endosome- and Golgi-localized phosphatidylserine flippases-such as the yeast Drs2 and human ATP8A1-have recently been reported. However, a substrate-binding site on the cytosolic side has not been found, and the transport mechanisms of P4 ATPases with other substrates are unknown. Here, we report structures of the Dnf1-Lem3 and Dnf2-Lem3 complexes. We captured substrate phosphatidylcholine molecules on both the exoplasmic and cytosolic sides and found that they have similar structures. Unexpectedly, Lem3 contributes to substrate binding. The conformational transitions of these phosphatidylcholine transporters match those of the phosphatidylserine transporters, suggesting a conserved mechanism among P4 ATPases. Dnf1/Dnf2 have a unique P domain helix-turn-helix insertion that is important for function. Therefore, P4 ATPases may have retained an overall transport mechanism while evolving distinct features for different lipid substrates. | |||||||||||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Movie |
 Movie viewer Movie viewer |
|---|---|
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7ky5.cif.gz 7ky5.cif.gz | 298.8 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7ky5.ent.gz pdb7ky5.ent.gz | 230.8 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7ky5.json.gz 7ky5.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ky/7ky5 https://data.pdbj.org/pub/pdb/validation_reports/ky/7ky5 ftp://data.pdbj.org/pub/pdb/validation_reports/ky/7ky5 ftp://data.pdbj.org/pub/pdb/validation_reports/ky/7ky5 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  23068MC  7ky6C  7ky7C  7ky8C  7ky9C  7kyaC  7kybC  7kycC M: map data used to model this data C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
|
|---|---|
| 1 |
|
- Components
Components
-Protein , 2 types, 2 molecules AB
| #1: Protein | Mass: 182834.469 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: DNF2, YDR093W, YD8557.01 / Production host:  References: UniProt: Q12675, P-type phospholipid transporter |
|---|---|
| #2: Protein | Mass: 47490.395 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: LEM3, BRE3, ROS3, YNL323W, N0333 / Production host:  |
-Sugars , 2 types, 7 molecules 
| #3: Polysaccharide | Source method: isolated from a genetically manipulated source #7: Sugar | ChemComp-NAG / |
|---|
-Non-polymers , 3 types, 4 molecules 
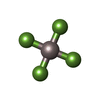

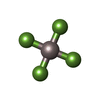

| #4: Chemical | | #5: Chemical | ChemComp-ALF / | #6: Chemical | ChemComp-MG / | |
|---|
-Details
| Has ligand of interest | N |
|---|---|
| Has protein modification | Y |
-Experimental details
-Experiment
| Experiment | Method: ELECTRON MICROSCOPY |
|---|---|
| EM experiment | Aggregation state: PARTICLE / 3D reconstruction method: single particle reconstruction |
- Sample preparation
Sample preparation
| Component | Name: S. cerevisiae phosphatidylcholine flippase Dnf2-Lem3 complex in the E2P transition state Type: COMPLEX / Entity ID: #1-#2 / Source: RECOMBINANT |
|---|---|
| Source (natural) | Organism:  Strain: ATCC 204508 / S288c |
| Source (recombinant) | Organism:  Strain: ATCC 204508 / S288c |
| Buffer solution | pH: 7.4 |
| Specimen | Conc.: 1.5 mg/ml / Embedding applied: NO / Shadowing applied: NO / Staining applied: NO / Vitrification applied: YES |
| Vitrification | Cryogen name: ETHANE |
- Electron microscopy imaging
Electron microscopy imaging
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
|---|---|
| Microscopy | Model: FEI TITAN KRIOS |
| Electron gun | Electron source:  FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: OTHER FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: OTHER |
| Electron lens | Mode: BRIGHT FIELD |
| Image recording | Electron dose: 64 e/Å2 / Film or detector model: GATAN K3 (6k x 4k) |
- Processing
Processing
| Software | Name: PHENIX / Version: 1.18.2_3874: / Classification: refinement | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EM software | Name: PHENIX / Category: model refinement | ||||||||||||||||||||||||
| CTF correction | Type: NONE | ||||||||||||||||||||||||
| 3D reconstruction | Resolution: 3.98 Å / Resolution method: FSC 0.143 CUT-OFF / Num. of particles: 127442 / Symmetry type: POINT | ||||||||||||||||||||||||
| Refine LS restraints |
|
 Movie
Movie Controller
Controller


















 PDBj
PDBj