+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6zoo | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Photosystem I reduced Plastocyanin Complex | ||||||||||||||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||||||||||||||
 キーワード キーワード | PHOTOSYNTHESIS / Photosystem I / membrane protein | ||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報response to low light intensity stimulus / plastoglobule / response to high light intensity / chloroplast thylakoid / photosynthesis, light harvesting in photosystem I / photosynthesis, light harvesting / thylakoid / chloroplast thylakoid lumen / chloroplast envelope / photosystem I reaction center ...response to low light intensity stimulus / plastoglobule / response to high light intensity / chloroplast thylakoid / photosynthesis, light harvesting in photosystem I / photosynthesis, light harvesting / thylakoid / chloroplast thylakoid lumen / chloroplast envelope / photosystem I reaction center / photosystem I / photosynthetic electron transport in photosystem I / photosystem I / photosystem II / chlorophyll binding / chloroplast thylakoid membrane / response to light stimulus / photosynthesis / response to cold / chloroplast / 4 iron, 4 sulfur cluster binding / electron transfer activity / oxidoreductase activity / copper ion binding / protein domain specific binding / mRNA binding / magnesium ion binding / metal ion binding 類似検索 - 分子機能 | ||||||||||||||||||||||||||||||
| 生物種 |  Pisum sativum (マメ科) Pisum sativum (マメ科) | ||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.74 Å | ||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Nelson, N. / Caspy, I. / Shkolnisky, Y. | ||||||||||||||||||||||||||||||
| 資金援助 |  イスラエル, イスラエル,  ベルギー, 4件 ベルギー, 4件
| ||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Biochem J / 年: 2021 ジャーナル: Biochem J / 年: 2021タイトル: Structure of plant photosystem I-plastocyanin complex reveals strong hydrophobic interactions. 著者: Ido Caspy / Mariia Fadeeva / Sebastian Kuhlgert / Anna Borovikova-Sheinker / Daniel Klaiman / Gal Masrati / Friedel Drepper / Nir Ben-Tal / Michael Hippler / Nathan Nelson /    要旨: Photosystem I is defined as plastocyanin-ferredoxin oxidoreductase. Taking advantage of genetic engineering, kinetic analyses and cryo-EM, our data provide novel mechanistic insights into binding and ...Photosystem I is defined as plastocyanin-ferredoxin oxidoreductase. Taking advantage of genetic engineering, kinetic analyses and cryo-EM, our data provide novel mechanistic insights into binding and electron transfer between PSI and Pc. Structural data at 2.74 Å resolution reveals strong hydrophobic interactions in the plant PSI-Pc ternary complex, leading to exclusion of water molecules from PsaA-PsaB/Pc interface once the PSI-Pc complex forms. Upon oxidation of Pc, a slight tilt of bound oxidized Pc allows water molecules to accommodate the space between Pc and PSI to drive Pc dissociation. Such a scenario is consistent with the six times larger dissociation constant of oxidized as compared with reduced Pc and mechanistically explains how this molecular machine optimized electron transfer for fast turnover. | ||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6zoo.cif.gz 6zoo.cif.gz | 871.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6zoo.ent.gz pdb6zoo.ent.gz | 764.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6zoo.json.gz 6zoo.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zo/6zoo https://data.pdbj.org/pub/pdb/validation_reports/zo/6zoo ftp://data.pdbj.org/pub/pdb/validation_reports/zo/6zoo ftp://data.pdbj.org/pub/pdb/validation_reports/zo/6zoo | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-Photosystem I P700 chlorophyll a apoprotein ... , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 82717.672 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: A0A0F6NFW5, photosystem I Pisum sativum (マメ科) / 参照: UniProt: A0A0F6NFW5, photosystem I |
|---|---|
| #2: タンパク質 | 分子量: 82381.734 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: A0A0F6NGI2, photosystem I Pisum sativum (マメ科) / 参照: UniProt: A0A0F6NGI2, photosystem I |
-タンパク質 , 7種, 7分子 CDEGL2P
| #3: タンパク質 | 分子量: 8860.276 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: P10793, photosystem I Pisum sativum (マメ科) / 参照: UniProt: P10793, photosystem I |
|---|---|
| #4: タンパク質 | 分子量: 16041.408 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: E1C9K8 Pisum sativum (マメ科) / 参照: UniProt: E1C9K8 |
| #5: タンパク質 | 分子量: 7479.422 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: E1C9K6 Pisum sativum (マメ科) / 参照: UniProt: E1C9K6 |
| #7: タンパク質 | 分子量: 10678.027 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: A0A0M3KL13 Pisum sativum (マメ科) / 参照: UniProt: A0A0M3KL13 |
| #12: タンパク質 | 分子量: 16863.270 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) Pisum sativum (マメ科) |
| #14: タンパク質 | 分子量: 22845.812 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: Q41038 Pisum sativum (マメ科) / 参照: UniProt: Q41038 |
| #17: タンパク質 | 分子量: 10353.487 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: P16002 Pisum sativum (マメ科) / 参照: UniProt: P16002 |
-Photosystem I reaction center subunit ... , 5種, 5分子 FHIJK
| #6: タンパク質 | 分子量: 17137.857 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: A0A0M3KL12 Pisum sativum (マメ科) / 参照: UniProt: A0A0M3KL12 |
|---|---|
| #8: タンパク質 | 分子量: 10043.313 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) Pisum sativum (マメ科) |
| #9: タンパク質・ペプチド | 分子量: 3409.198 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: P17227 Pisum sativum (マメ科) / 参照: UniProt: P17227 |
| #10: タンパク質・ペプチド | 分子量: 4767.609 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: D5MAL3 Pisum sativum (マメ科) / 参照: UniProt: D5MAL3 |
| #11: タンパク質 | 分子量: 8135.471 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: E1C9L3 Pisum sativum (マメ科) / 参照: UniProt: E1C9L3 |
-Chlorophyll a-b binding protein ... , 3種, 3分子 134
| #13: タンパク質 | 分子量: 21335.439 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: Q01667 Pisum sativum (マメ科) / 参照: UniProt: Q01667 |
|---|---|
| #15: タンパク質 | 分子量: 24139.521 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: Q32904 Pisum sativum (マメ科) / 参照: UniProt: Q32904 |
| #16: タンパク質 | 分子量: 21994.029 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Pisum sativum (マメ科) / 参照: UniProt: Q9SQL2 Pisum sativum (マメ科) / 参照: UniProt: Q9SQL2 |
-糖 , 2種, 13分子 

| #24: 糖 | ChemComp-LMT / #27: 糖 | ChemComp-DGD / |
|---|
-非ポリマー , 14種, 232分子 






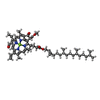
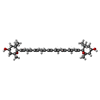
















| #18: 化合物 | ChemComp-CL0 / | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| #19: 化合物 | ChemComp-CLA / #20: 化合物 | #21: 化合物 | #22: 化合物 | ChemComp-BCR / #23: 化合物 | ChemComp-LHG / #25: 化合物 | ChemComp-LMG / #26: 化合物 | #28: 化合物 | ChemComp-LUT / ( #29: 化合物 | ChemComp-CHL / #30: 化合物 | #31: 化合物 | ChemComp-3PH / | #32: 化合物 | ChemComp-CU / | #33: 水 | ChemComp-HOH / | |
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Photosystem I plastocyanin complex / タイプ: COMPLEX / Entity ID: #1, #10-#11, #13-#14, #16-#17, #2-#7, #9 / 由来: NATURAL |
|---|---|
| 分子量 | 値: 0.65 kDa/nm / 実験値: YES |
| 由来(天然) | 生物種:  Pisum sativum (マメ科) Pisum sativum (マメ科) |
| 緩衝液 | pH: 7 / 詳細: 20mM Mes-Tris, 10mM sodium ascorbate |
| 試料 | 濃度: 2.8 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 130000 X / 最大 デフォーカス(公称値): 1500 nm / 最小 デフォーカス(公称値): 300 nm / Calibrated defocus min: 300 nm / 最大 デフォーカス(補正後): 1500 nm / C2レンズ絞り径: 20 µm |
| 試料ホルダ | 凍結剤: NITROGEN |
| 撮影 | 平均露光時間: 2.49 sec. / 電子線照射量: 40.8 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 実像数: 6129 |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19.2_4158: / 分類: 精密化 | ||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 359977 | ||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.74 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 104127 / クラス平均像の数: 4 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||
| 原子モデル構築 | B value: 38.8 / プロトコル: RIGID BODY FIT / 空間: REAL | ||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6YEZ Accession code: 6YEZ / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 53.84 Å2 | ||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj
























