+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-3171 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | P22 bacteriophage Empty Procapsid | |||||||||
 マップデータ マップデータ | Reconstruction of bacteriophage P22 Empty Procapsid | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | P22 / bacteriophage / GFP / beta glucosidase / virus / AFM / cryoEM / cargo / nanocage | |||||||||
| 生物種 |  Enterobacteria phage P22 (ファージ) Enterobacteria phage P22 (ファージ) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / ネガティブ染色法 / 解像度: 12.6 Å | |||||||||
 データ登録者 データ登録者 | Llauro A / Luque D / Trus BL / Edwards E / Avera J / Reguera D / Douglas T / Pablo PJ / Caston JR | |||||||||
 引用 引用 |  ジャーナル: Nanoscale / 年: 2016 ジャーナル: Nanoscale / 年: 2016タイトル: Cargo-shell and cargo-cargo couplings govern the mechanics of artificially loaded virus-derived cages. 著者: Aida Llauró / Daniel Luque / Ethan Edwards / Benes L Trus / John Avera / David Reguera / Trevor Douglas / Pedro J de Pablo / José R Castón /   要旨: Nucleic acids are the natural cargo of viruses and key determinants that affect viral shell stability. In some cases the genome structurally reinforces the shell, whereas in others genome packaging ...Nucleic acids are the natural cargo of viruses and key determinants that affect viral shell stability. In some cases the genome structurally reinforces the shell, whereas in others genome packaging causes internal pressure that can induce destabilization. Although it is possible to pack heterologous cargoes inside virus-derived shells, little is known about the physical determinants of these artificial nanocontainers' stability. Atomic force and three-dimensional cryo-electron microscopy provided mechanical and structural information about the physical mechanisms of viral cage stabilization beyond the mere presence/absence of cargos. We analyzed the effects of cargo-shell and cargo-cargo interactions on shell stability after encapsulating two types of proteinaceous payloads. While bound cargo to the inner capsid surface mechanically reinforced the capsid in a structural manner, unbound cargo diffusing freely within the shell cavity pressurized the cages up to ∼30 atm due to steric effects. Strong cargo-cargo coupling reduces the resilience of these nanocompartments in ∼20% when bound to the shell. Understanding the stability of artificially loaded nanocages will help to design more robust and durable molecular nanocontainers. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_3171.map.gz emd_3171.map.gz | 20.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-3171-v30.xml emd-3171-v30.xml emd-3171.xml emd-3171.xml | 8.7 KB 8.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_3171.png emd_3171.png | 1.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-3171 http://ftp.pdbj.org/pub/emdb/structures/EMD-3171 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3171 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3171 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_3171_validation.pdf.gz emd_3171_validation.pdf.gz | 278.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_3171_full_validation.pdf.gz emd_3171_full_validation.pdf.gz | 277.5 KB | 表示 | |
| XML形式データ |  emd_3171_validation.xml.gz emd_3171_validation.xml.gz | 6.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3171 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3171 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3171 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3171 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_3171.map.gz / 形式: CCP4 / 大きさ: 21.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_3171.map.gz / 形式: CCP4 / 大きさ: 21.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of bacteriophage P22 Empty Procapsid | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 4.32 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
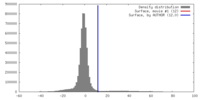
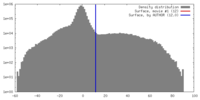
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Bacteriophage P22 Empty Procapsid
| 全体 | 名称: Bacteriophage P22 Empty Procapsid |
|---|---|
| 要素 |
|
-超分子 #1000: Bacteriophage P22 Empty Procapsid
| 超分子 | 名称: Bacteriophage P22 Empty Procapsid / タイプ: sample / ID: 1000 / 集合状態: 60 / Number unique components: 1 |
|---|
-超分子 #1: Enterobacteria phage P22
| 超分子 | 名称: Enterobacteria phage P22 / タイプ: virus / ID: 1 / NCBI-ID: 10754 / 生物種: Enterobacteria phage P22 / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: OTHER / ウイルス・エンベロープ: No / ウイルス・中空状態: Yes |
|---|---|
| 宿主 | 生物種:  Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌) Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌)別称: BACTERIA(EUBACTERIA) |
| Host system | 生物種:  |
| ウイルス殻 | Shell ID: 1 / 直径: 596 Å / T番号(三角分割数): 7 |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 染色 | タイプ: NEGATIVE 詳細: Samples were applied to grids, blotted and plunged into liquid ethane |
|---|---|
| グリッド | 詳細: R 2/2 Quantifoil grids |
| 凍結 | 凍結剤: ETHANE / 装置: LEICA EM CPC |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 日付 | 2015年3月17日 |
| 撮影 | カテゴリ: CCD / フィルム・検出器のモデル: FEI EAGLE (4k x 4k) / デジタル化 - サンプリング間隔: 15 µm / 実像数: 385 / 平均電子線量: 10 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 69444 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.26 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 0.75 µm / 倍率(公称値): 69444 |
| 試料ステージ | 試料ホルダー: Eucentric / 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: Phase flipping & amplitude decay |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: I (正20面体型対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 12.6 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Xmipp / 使用した粒子像数: 9810 |
 ムービー
ムービー コントローラー
コントローラー


















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)