+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30647 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of Calcium-Sensing Receptor in complex with Evocalcet | |||||||||
 マップデータ マップデータ | Full map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | CaSR / Calcium-Sensing Receptor / Evocalcet / MEMBRANE PROTEIN | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Wen TL / Yang X | |||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2021 ジャーナル: Sci Adv / 年: 2021タイトル: Structural basis for activation and allosteric modulation of full-length calcium-sensing receptor. 著者: Tianlei Wen / Ziyu Wang / Xiaozhe Chen / Yue Ren / Xuhang Lu / Yangfei Xing / Jing Lu / Shenghai Chang / Xing Zhang / Yuequan Shen / Xue Yang /  要旨: Calcium-sensing receptor (CaSR) is a class C G protein-coupled receptor (GPCR) that plays an important role in calcium homeostasis and parathyroid hormone secretion. Here, we present multiple cryo- ...Calcium-sensing receptor (CaSR) is a class C G protein-coupled receptor (GPCR) that plays an important role in calcium homeostasis and parathyroid hormone secretion. Here, we present multiple cryo-electron microscopy structures of full-length CaSR in distinct ligand-bound states. Ligands (Ca and l-tryptophan) bind to the extracellular domain of CaSR and induce large-scale conformational changes, leading to the closure of two heptahelical transmembrane domains (7TMDs) for activation. The positive modulator (evocalcet) and the negative allosteric modulator (NPS-2143) occupy the similar binding pocket in 7TMD. The binding of NPS-2143 causes a considerable rearrangement of two 7TMDs, forming an inactivated TM6/TM6 interface. Moreover, a total of 305 disease-causing missense mutations of CaSR have been mapped to the structure in the active state, creating hotspot maps of five clinical endocrine disorders. Our results provide a structural framework for understanding the activation, allosteric modulation mechanism, and disease therapy for class C GPCRs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30647.map.gz emd_30647.map.gz | 97.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30647-v30.xml emd-30647-v30.xml emd-30647.xml emd-30647.xml | 16.2 KB 16.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30647.png emd_30647.png | 64.3 KB | ||
| Filedesc metadata |  emd-30647.cif.gz emd-30647.cif.gz | 6.2 KB | ||
| その他 |  emd_30647_additional_1.map.gz emd_30647_additional_1.map.gz emd_30647_additional_2.map.gz emd_30647_additional_2.map.gz | 2.3 MB 81.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30647 http://ftp.pdbj.org/pub/emdb/structures/EMD-30647 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30647 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30647 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30647.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30647.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Full map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
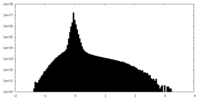
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.014 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: EM map for TM domain
| ファイル | emd_30647_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EM map for TM domain | ||||||||||||
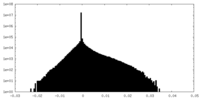
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: ECD
| ファイル | emd_30647_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | ECD | ||||||||||||
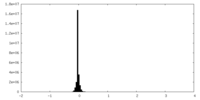
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Calcium-Sensing Receptor in complex with Evocalcet
| 全体 | 名称: Calcium-Sensing Receptor in complex with Evocalcet |
|---|---|
| 要素 |
|
-超分子 #1: Calcium-Sensing Receptor in complex with Evocalcet
| 超分子 | 名称: Calcium-Sensing Receptor in complex with Evocalcet / タイプ: cell / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Calcium-Sensing Receptor
| 分子 | 名称: Calcium-Sensing Receptor / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 119.314234 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MTLYSCCLIL LLFTWNTAAY GPNQRAQKKG DIILGGLFPI HFGVAAKDQD LKSRPESVEC IRYNFRGFRW LQAMIFAIEE INNSPNLLP NMTLGYRIFD TCNTVSKALE ATLSFVAQNK IDSLNLDEFC NCSEHIPSTI AVVGATGSGV STAVANLLGL F YIPQVSYA ...文字列: MTLYSCCLIL LLFTWNTAAY GPNQRAQKKG DIILGGLFPI HFGVAAKDQD LKSRPESVEC IRYNFRGFRW LQAMIFAIEE INNSPNLLP NMTLGYRIFD TCNTVSKALE ATLSFVAQNK IDSLNLDEFC NCSEHIPSTI AVVGATGSGV STAVANLLGL F YIPQVSYA SSSRLLSNKN QFKSFLRTIP NDEHQATAMA DIIEYFRWNW VGTIAADDDY GRPGIEKFRE EAEERDICID FS ELISQYS DEEEIQQVVE VIQNSTARVI VVFSSGPDLE PLIKEIVRRN ITGKIWLASE AWASSSLIAM PEFFRVIGST IGF ALKAGQ IPGFREFLQK VHPKKSANNG FAKEFWEETF NCYLPSESKN SPASASFHKA HEEGLGAGNG TAAFRPPCTG DENI TSVET PYMDFTHLRI SYNVYLAVYS IAHALQDIYT CTPGKGLFTN GSCADIKKVE AWQVLKHLRH LNFTSNMGEQ VDFDE FGDL VGNYSIINWH LSPEDGSVVF EEVGHYNVYA KKGERLFINE NKILWSGFSK EVPFSNCSRD CLPGTRKGII EGEPTC CFE CVDCPDGEYS DETDASACDK CPEDYWSNEN HTSCIPKQIE FLSWTEPFGI ALTLFAVLGI FLTSFVLGVF TKFRNTP IV KATNRELSYL LLFSLLCCFS SSLFFIGEPQ NWTCRLRQPA FGISFVLCIS CILVKTNRVL LVFEAKIPTS LHRKWWGL N LQFLLVFLCT FVQIVICVIW LYTAPPSSYR NHELEDEIIF ITCHEGSLMA LGFLIGYTCL LAAICFFFAF KSRKLPENF NEAKFITFSM LIFFIVWISF IPAYASTYGK FVSAVEVIAI LAASFGLLAC IFFNKVYIIL FKPSRNTIEE VRCSTAAHAF KVAARATLR RSNVSRKRSN SLGGSTGSTP SSSISSKSNH EDPFPLPASA ERQRQQQRGC KQKVSFGSGT VTLSLSFEEP Q KNAMANRN AKRRNSLEAQ NSDDSLMRHR ALLALQNSES LSAEPGFQTA SSPETSSQES VVGDNKEEVP NPEAEPSLPS AN SRNFIGT GGSSVTENTV HSLESALEVL FQ |
-分子 #3: CHLORIDE ION
| 分子 | 名称: CHLORIDE ION / タイプ: ligand / ID: 3 / コピー数: 2 / 式: CL |
|---|---|
| 分子量 | 理論値: 35.453 Da |
-分子 #4: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 4 / コピー数: 6 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-分子 #5: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 5 / コピー数: 6 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #6: TRYPTOPHAN
| 分子 | 名称: TRYPTOPHAN / タイプ: ligand / ID: 6 / コピー数: 2 / 式: TRP |
|---|---|
| 分子量 | 理論値: 204.225 Da |
| Chemical component information |  ChemComp-TRP: |
-分子 #7: 2-[4-[(3S)-3-[[(1R)-1-naphthalen-1-ylethyl]amino]pyrrolidin-1-yl]...
| 分子 | 名称: 2-[4-[(3S)-3-[[(1R)-1-naphthalen-1-ylethyl]amino]pyrrolidin-1-yl]phenyl]ethanoic acid タイプ: ligand / ID: 7 / コピー数: 2 / 式: H43 |
|---|---|
| 分子量 | 理論値: 374.475 Da |
| Chemical component information | 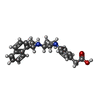 ChemComp-H43: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | モデル: Quantifoil R2/1 / 材質: GOLD / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 110530 |
| 初期 角度割当 | タイプ: NOT APPLICABLE |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-7dd7: |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)