[日本語] English
 万見
万見- EMDB-2976: Time-resolved Cryo Electron Microscopy of ribosome subunit association -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2976 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Time-resolved Cryo Electron Microscopy of ribosome subunit association | |||||||||
 マップデータ マップデータ | Reconstruction of E. Coli naked 70S ribosome in non-rotated (NR) conformation | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | time-resolved / cryo-EM / mixing-spraying / ribosome subunit association / structural dynamics | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 9.7 Å | |||||||||
 データ登録者 データ登録者 | Chen B / Kaledhonkar S / Sun M / Shen B / Lu Z / Barnard D / Lu T / Gonzalez Jr R / Frank J | |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2015 ジャーナル: Structure / 年: 2015タイトル: Structural dynamics of ribosome subunit association studied by mixing-spraying time-resolved cryogenic electron microscopy. 著者: Bo Chen / Sandip Kaledhonkar / Ming Sun / Bingxin Shen / Zonghuan Lu / David Barnard / Toh-Ming Lu / Ruben L Gonzalez / Joachim Frank /  要旨: Ribosomal subunit association is a key checkpoint in translation initiation but its structural dynamics are poorly understood. Here, we used a recently developed mixing-spraying, time-resolved, ...Ribosomal subunit association is a key checkpoint in translation initiation but its structural dynamics are poorly understood. Here, we used a recently developed mixing-spraying, time-resolved, cryogenic electron microscopy (cryo-EM) method to study ribosomal subunit association in the sub-second time range. We have improved this method and increased the cryo-EM data yield by tenfold. Pre-equilibrium states of the association reaction were captured by reacting the mixture of ribosomal subunits for 60 ms and 140 ms. We also identified three distinct ribosome conformations in the associated ribosomes. The observed proportions of these conformations are the same in these two time points, suggesting that ribosomes equilibrate among the three conformations within less than 60 ms upon formation. Our results demonstrate that the mixing-spraying method can capture multiple states of macromolecules during a sub-second reaction. Other fast processes, such as translation initiation, decoding, and ribosome recycling, are amenable to study with this method. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2976.map.gz emd_2976.map.gz | 14.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2976-v30.xml emd-2976-v30.xml emd-2976.xml emd-2976.xml | 8.9 KB 8.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_2976.png emd_2976.png | 304.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2976 http://ftp.pdbj.org/pub/emdb/structures/EMD-2976 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2976 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2976 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_2976_validation.pdf.gz emd_2976_validation.pdf.gz | 243.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_2976_full_validation.pdf.gz emd_2976_full_validation.pdf.gz | 242.7 KB | 表示 | |
| XML形式データ |  emd_2976_validation.xml.gz emd_2976_validation.xml.gz | 5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2976 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2976 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2976 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2976 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2976.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2976.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of E. Coli naked 70S ribosome in non-rotated (NR) conformation | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
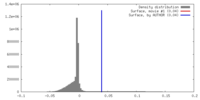
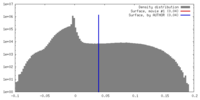
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : E. Coli 70S Ribosome
| 全体 | 名称: E. Coli 70S Ribosome |
|---|---|
| 要素 |
|
-超分子 #1000: E. Coli 70S Ribosome
| 超分子 | 名称: E. Coli 70S Ribosome / タイプ: sample / ID: 1000 / Number unique components: 1 |
|---|
-超分子 #1: Escherichia coli 70S ribosome
| 超分子 | 名称: Escherichia coli 70S ribosome / タイプ: complex / ID: 1 / 組換発現: No / Ribosome-details: ribosome-prokaryote: LSU 50S, SSU 30S |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.6 詳細: 25 mM Tris-HCl, 60 mM NH4Cl, 5 mM 2-mercaptoethanol, 3.5 mM MgCl2 |
|---|---|
| グリッド | 詳細: Quantifoil R2/2 300 mesh copper grid with thin carbon sipport |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 80 % / チャンバー内温度: 80 K / 装置: OTHER 詳細: Equal volume of 1.2 microM 30S and 0.6 microM 50S (final concentration after mixing) were injected into the mixing-spraying device each at flow rate of 3 microL/s. The computer-controlled ...詳細: Equal volume of 1.2 microM 30S and 0.6 microM 50S (final concentration after mixing) were injected into the mixing-spraying device each at flow rate of 3 microL/s. The computer-controlled plunging device was purchased from Dr. Howard White (Eastern Virginia Medical School, VA). Timed resolved state: Vitrified after spraying |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 温度 | 平均: 80 K |
| 詳細 | Low dose, Data was collected over two years time |
| 日付 | 2013年9月13日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) 実像数: 3402 / 平均電子線量: 17 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 66318 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2 mm / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 2.0 µm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| 詳細 | The partciles were selected with Autopicker (Langlois et al., 2014), and 3D classification and reconstruction with RELION |
|---|---|
| CTF補正 | 詳細: each Micrograph |
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 9.7 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Arachnid, RELION, SPIDER / 使用した粒子像数: 39678 |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)