+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-25586 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of somatostatin receptor 2 in complex with somatostatin-14 and Gi3 | |||||||||
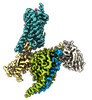
 マップデータ マップデータ | CryoEM structure of SSTR2/Gi3 complex bound to SST14 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報somatostatin signaling pathway / dynorphin receptor activity / response to acrylamide / regulation of saliva secretion / MECP2 regulates transcription of neuronal ligands / sensory perception of temperature stimulus / positive regulation of eating behavior / somatostatin receptor activity / adenylate cyclase-inhibiting opioid receptor signaling pathway / hormone-mediated apoptotic signaling pathway ...somatostatin signaling pathway / dynorphin receptor activity / response to acrylamide / regulation of saliva secretion / MECP2 regulates transcription of neuronal ligands / sensory perception of temperature stimulus / positive regulation of eating behavior / somatostatin receptor activity / adenylate cyclase-inhibiting opioid receptor signaling pathway / hormone-mediated apoptotic signaling pathway / G protein-coupled opioid receptor activity / negative regulation of luteinizing hormone secretion / G protein-coupled opioid receptor signaling pathway / peristalsis / positive regulation of dopamine secretion / sensory perception / positive regulation of potassium ion transmembrane transport / conditioned place preference / negative regulation of adenylate cyclase activity / maternal behavior / receptor serine/threonine kinase binding / neuropeptide binding / response to acidic pH / hyperosmotic response / GTP metabolic process / cellular response to glucocorticoid stimulus / response to steroid hormone / positive regulation of p38MAPK cascade / G protein-coupled dopamine receptor signaling pathway / eating behavior / neuronal dense core vesicle / regulation of postsynaptic membrane neurotransmitter receptor levels / response to starvation / behavioral response to cocaine / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / positive regulation of macroautophagy / estrous cycle / GABA-ergic synapse / Adenylate cyclase inhibitory pathway / neuropeptide signaling pathway / response to amino acid / MECP2 regulates neuronal receptors and channels / axon terminus / forebrain development / regulation of cell migration / sensory perception of pain / digestion / T-tubule / adenylate cyclase-inhibiting G protein-coupled receptor signaling pathway / Peptide ligand-binding receptors / cerebellum development / response to nutrient / sarcoplasmic reticulum / locomotory behavior / cellular response to estradiol stimulus / PDZ domain binding / G protein-coupled receptor binding / cellular response to glucose stimulus / response to nicotine / G-protein beta/gamma-subunit complex binding / Olfactory Signaling Pathway / response to insulin / Activation of the phototransduction cascade / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / G beta:gamma signalling through PLC beta / Presynaptic function of Kainate receptors / Thromboxane signalling through TP receptor / G-protein activation / G protein-coupled acetylcholine receptor signaling pathway / Activation of G protein gated Potassium channels / Inhibition of voltage gated Ca2+ channels via Gbeta/gamma subunits / hormone activity / Prostacyclin signalling through prostacyclin receptor / Glucagon signaling in metabolic regulation / G beta:gamma signalling through CDC42 / ADP signalling through P2Y purinoceptor 12 / G beta:gamma signalling through BTK / Synthesis, secretion, and inactivation of Glucagon-like Peptide-1 (GLP-1) / Sensory perception of sweet, bitter, and umami (glutamate) taste / synaptic vesicle membrane / photoreceptor disc membrane / Adrenaline,noradrenaline inhibits insulin secretion / Glucagon-type ligand receptors / Vasopressin regulates renal water homeostasis via Aquaporins / G alpha (z) signalling events / cellular response to catecholamine stimulus / Glucagon-like Peptide-1 (GLP1) regulates insulin secretion / ADORA2B mediated anti-inflammatory cytokines production / sensory perception of taste / response to estrogen / ADP signalling through P2Y purinoceptor 1 / adenylate cyclase-activating dopamine receptor signaling pathway / G beta:gamma signalling through PI3Kgamma / cellular response to prostaglandin E stimulus / Cooperation of PDCL (PhLP1) and TRiC/CCT in G-protein beta folding / GPER1 signaling / GDP binding / G-protein beta-subunit binding / Inactivation, recovery and regulation of the phototransduction cascade / heterotrimeric G-protein complex 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.5 Å | |||||||||
 データ登録者 データ登録者 | Robertson MJ / Skinotis G | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2022 ジャーナル: Nat Struct Mol Biol / 年: 2022タイトル: Plasticity in ligand recognition at somatostatin receptors. 著者: Michael J Robertson / Justin G Meyerowitz / Ouliana Panova / Kenneth Borrelli / Georgios Skiniotis /  要旨: Somatostatin is a signaling peptide that plays a pivotal role in physiologic processes relating to metabolism and growth through its actions at somatostatin receptors (SSTRs). Members of the SSTR ...Somatostatin is a signaling peptide that plays a pivotal role in physiologic processes relating to metabolism and growth through its actions at somatostatin receptors (SSTRs). Members of the SSTR subfamily, particularly SSTR2, are key drug targets for neuroendocrine neoplasms, with synthetic peptide agonists currently in clinical use. Here, we show the cryogenic-electron microscopy structures of active-state SSTR2 in complex with heterotrimeric G and either the endogenous ligand SST14 or the FDA-approved drug octreotide. Complemented by biochemical assays and molecular dynamics simulations, these structures reveal key details of ligand recognition and receptor activation at SSTRs. We find that SSTR ligand recognition is highly diverse, as demonstrated by ligand-induced conformational changes in ECL2 and substantial sequence divergence across subtypes in extracellular regions. Despite this complexity, we rationalize several known sources of SSTR subtype selectivity and identify an additional interaction for specific binding. These results provide valuable insights for structure-based drug discovery at SSTRs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_25586.map.gz emd_25586.map.gz | 168 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-25586-v30.xml emd-25586-v30.xml emd-25586.xml emd-25586.xml | 15.1 KB 15.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_25586.png emd_25586.png | 130.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-25586 http://ftp.pdbj.org/pub/emdb/structures/EMD-25586 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25586 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25586 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_25586_validation.pdf.gz emd_25586_validation.pdf.gz | 447.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_25586_full_validation.pdf.gz emd_25586_full_validation.pdf.gz | 447.2 KB | 表示 | |
| XML形式データ |  emd_25586_validation.xml.gz emd_25586_validation.xml.gz | 6.9 KB | 表示 | |
| CIF形式データ |  emd_25586_validation.cif.gz emd_25586_validation.cif.gz | 7.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25586 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25586 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25586 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25586 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7t10MC  7t11C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10931 (タイトル: Cryogenic electron microscopy of somatostatin receptor 2/SST14/Gi3 complex EMPIAR-10931 (タイトル: Cryogenic electron microscopy of somatostatin receptor 2/SST14/Gi3 complexData size: 4.5 TB Data #1: Raw movies of SSTR2/SST14/Gi3 complex collected on a K3 [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_25586.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_25586.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | CryoEM structure of SSTR2/Gi3 complex bound to SST14 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8521 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Somatostatin receptor 2 in complex with Somatostatin-14 and Gi3.
| 全体 | 名称: Somatostatin receptor 2 in complex with Somatostatin-14 and Gi3. |
|---|---|
| 要素 |
|
-超分子 #1: Somatostatin receptor 2 in complex with Somatostatin-14 and Gi3.
| 超分子 | 名称: Somatostatin receptor 2 in complex with Somatostatin-14 and Gi3. タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#6 |
|---|
-分子 #1: Somatostatin receptor type 2,Kappa-type opioid receptor
| 分子 | 名称: Somatostatin receptor type 2,Kappa-type opioid receptor タイプ: protein_or_peptide / ID: 1 詳細: Somatostatin receptor type 2 with intracellular loop 3 (ICL3) replaced with the ICL3 from the Kappa-type opioid receptor コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 45.784211 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DYKDDDDAMG QPGNGSAFLL APNRSHAPDH DVENLYFQGM DMADEPLNGS HTWLSIPFDL NGSVVSTNTS NQTEPYYDLT SNAVLTFIY FVVCIIGLCG NTLVIYVILR YAKMKTITNI YILNLAIADE LFMLGLPFLA MQVALVHWPF GKAICRVVMT V DGINQFTS ...文字列: DYKDDDDAMG QPGNGSAFLL APNRSHAPDH DVENLYFQGM DMADEPLNGS HTWLSIPFDL NGSVVSTNTS NQTEPYYDLT SNAVLTFIY FVVCIIGLCG NTLVIYVILR YAKMKTITNI YILNLAIADE LFMLGLPFLA MQVALVHWPF GKAICRVVMT V DGINQFTS IFCLTVMSID RYLAVVHPIK SAKWRRPRTA KMITMAVWGV SLLVILPIMI YAGLRSNQWG RSSCTINWPG ES GAWYTGF IIYTFILGFL VPLTIICLCY LFIIIKVKSV RLLSGSREKD RNLRKVTRMV SIVVAVFIFC WLPFYIFNVS SVS MAISPT PALKGMFDFV VVLTYANSCA NPILYAFLSD NFKKSFQNVL CLVKVSGTDD GERSDSKQDK SRLNETTETQ RTLL NGDLQ TSI |
-分子 #2: Guanine nucleotide-binding protein G(i) subunit alpha-3
| 分子 | 名称: Guanine nucleotide-binding protein G(i) subunit alpha-3 タイプ: protein_or_peptide / ID: 2 / 詳細: dominant negative / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 40.584156 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MGCTLSAEDK AAVERSKMID RNLREDGEKA AKEVKLLLLG AGESGKNTIV KQMKIIHEDG YSEDECKQYK VVVYSNTIQS IIAIIRAMG RLKIDFGEAA RADDARQLFV LAGSAEEGVM TPELAGVIKR LWRDGGVQAC FSRSREYQLN DSASYYLNDL D RISQSNYI ...文字列: MGCTLSAEDK AAVERSKMID RNLREDGEKA AKEVKLLLLG AGESGKNTIV KQMKIIHEDG YSEDECKQYK VVVYSNTIQS IIAIIRAMG RLKIDFGEAA RADDARQLFV LAGSAEEGVM TPELAGVIKR LWRDGGVQAC FSRSREYQLN DSASYYLNDL D RISQSNYI PTQQDVLRTR VKTTGIVETH FTFKDLYFKM FDVGAQRSER KKWIHCFEGV TAIIFCVALS DYDLVLAEDE EM NRMHASM KLFDSICNNK WFTETSIILF LNKKDLFEEK IKRSPLTICY PEYTGSNTYE EAAAYIQCQF EDLNRRKDTK EIY THFTCS TDTKNVQFVF DAVTDVIIKN NLKECGLY |
-分子 #3: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1
| 分子 | 名称: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1 タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 37.671102 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: PGSSGSELDQ LRQEAEQLKN QIRDARKACA DATLSQITNN IDPVGRIQMR TRRTLRGHLA KIYAMHWGTD SRLLVSASQD GKLIIWDSY TTNKVHAIPL RSSWVMTCAY APSGNYVACG GLDNICSIYN LKTREGNVRV SRELAGHTGY LSCCRFLDDN Q IVTSSGDT ...文字列: PGSSGSELDQ LRQEAEQLKN QIRDARKACA DATLSQITNN IDPVGRIQMR TRRTLRGHLA KIYAMHWGTD SRLLVSASQD GKLIIWDSY TTNKVHAIPL RSSWVMTCAY APSGNYVACG GLDNICSIYN LKTREGNVRV SRELAGHTGY LSCCRFLDDN Q IVTSSGDT TCALWDIETG QQTTTFTGHT GDVMSLSLAP DTRLFVSGAC DASAKLWDVR EGMCRQTFTG HESDINAICF FP NGNAFAT GSDDATCRLF DLRADQELMT YSHDNIICGI TSVSFSKSGR LLLAGYDDFN CNVWDALKAD RAGVLAGHDN RVS CLGVTD DGMAVATGSW DSFLKIWN |
-分子 #4: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2
| 分子 | 名称: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2 タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 7.861143 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MASNNTASIA QARKLVEQLK MEANIDRIKV SKAAADLMAY CEAHAKEDPL LTPVPASENP FREKKFFCAI L |
-分子 #5: Somatostatin-14
| 分子 | 名称: Somatostatin-14 / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 1.641909 KDa |
| 配列 | 文字列: AGCKNFFWKT FTSC |
-分子 #6: scFv16
| 分子 | 名称: scFv16 / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 27.784896 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DVQLVESGGG LVQPGGSRKL SCSASGFAFS SFGMHWVRQA PEKGLEWVAY ISSGSGTIYY ADTVKGRFTI SRDDPKNTLF LQMTSLRSE DTAMYYCVRS IYYYGSSPFD FWGQGTTLTV SSGGGGSGGG GSGGGGSDIV MTQATSSVPV TPGESVSISC R SSKSLLHS ...文字列: DVQLVESGGG LVQPGGSRKL SCSASGFAFS SFGMHWVRQA PEKGLEWVAY ISSGSGTIYY ADTVKGRFTI SRDDPKNTLF LQMTSLRSE DTAMYYCVRS IYYYGSSPFD FWGQGTTLTV SSGGGGSGGG GSGGGGSDIV MTQATSSVPV TPGESVSISC R SSKSLLHS NGNTYLYWFL QRPGQSPQLL IYRMSNLASG VPDRFSGSGS GTAFTLTISR LEAEDVGVYY CMQHLEYPLT FG AGTKLEL KAAAHHHHHH HH |
-分子 #7: water
| 分子 | 名称: water / タイプ: ligand / ID: 7 / コピー数: 5 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 1.04 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER / 詳細: ab initio |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 442863 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー