+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0627 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM map of human MCU | |||||||||
 マップデータ マップデータ | Apo form of a cation channel | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報uniporter activity / Processing of SMDT1 / mitochondrial calcium ion transmembrane transport / uniplex complex / Mitochondrial calcium ion transport / positive regulation of mitochondrial calcium ion concentration / mitochondrial calcium ion homeostasis / calcium import into the mitochondrion / cellular response to calcium ion starvation / positive regulation of neutrophil chemotaxis ...uniporter activity / Processing of SMDT1 / mitochondrial calcium ion transmembrane transport / uniplex complex / Mitochondrial calcium ion transport / positive regulation of mitochondrial calcium ion concentration / mitochondrial calcium ion homeostasis / calcium import into the mitochondrion / cellular response to calcium ion starvation / positive regulation of neutrophil chemotaxis / positive regulation of mitochondrial fission / protein complex oligomerization / calcium channel complex / calcium-mediated signaling / positive regulation of insulin secretion / calcium channel activity / glucose homeostasis / mitochondrial inner membrane / mitochondrion / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.7 Å | |||||||||
 データ登録者 データ登録者 | Wang Y / Bai X / Jiang Y | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2019 ジャーナル: Cell / 年: 2019タイトル: Structural Mechanism of EMRE-Dependent Gating of the Human Mitochondrial Calcium Uniporter. 著者: Yan Wang / Nam X Nguyen / Ji She / Weizhong Zeng / Yi Yang / Xiao-Chen Bai / Youxing Jiang /  要旨: Mitochondrial calcium uptake is crucial to the regulation of eukaryotic Ca homeostasis and is mediated by the mitochondrial calcium uniporter (MCU). While MCU alone can transport Ca in primitive ...Mitochondrial calcium uptake is crucial to the regulation of eukaryotic Ca homeostasis and is mediated by the mitochondrial calcium uniporter (MCU). While MCU alone can transport Ca in primitive eukaryotes, metazoans require an essential single membrane-spanning auxiliary component called EMRE to form functional channels; however, the molecular mechanism of EMRE regulation remains elusive. Here, we present the cryo-EM structure of the human MCU-EMRE complex, which defines the interactions between MCU and EMRE as well as pinpoints the juxtamembrane loop of MCU and extended linker of EMRE as the crucial elements in the EMRE-dependent gating mechanism among metazoan MCUs. The structure also features the dimerization of two MCU-EMRE complexes along an interface at the N-terminal domain (NTD) of human MCU that is a hotspot for post-translational modifications. Thus, the human MCU-EMRE complex, which constitutes the minimal channel components among metazoans, provides a framework for future mechanistic studies on MCU. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0627.map.gz emd_0627.map.gz | 20.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0627-v30.xml emd-0627-v30.xml emd-0627.xml emd-0627.xml | 9.1 KB 9.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_0627.png emd_0627.png | 72.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0627 http://ftp.pdbj.org/pub/emdb/structures/EMD-0627 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0627 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0627 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_0627_validation.pdf.gz emd_0627_validation.pdf.gz | 78.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_0627_full_validation.pdf.gz emd_0627_full_validation.pdf.gz | 78 KB | 表示 | |
| XML形式データ |  emd_0627_validation.xml.gz emd_0627_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-0627 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-0627 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-0627 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-0627 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0627.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0627.map.gz / 形式: CCP4 / 大きさ: 22.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Apo form of a cation channel | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.07 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
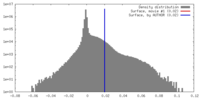
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : MCU
| 全体 | 名称: MCU |
|---|---|
| 要素 |
|
-超分子 #1: MCU
| 超分子 | 名称: MCU / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: MCU
| 分子 | 名称: MCU / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MAAAAGRSLL LLLSSRGGGG GGAGGCGALT AGCFPGLGVS RHRQQQHHRT VHQRIASWQN LGAVYCSTVV PSDDVTVVYQ NGLPVISVR LPSRRERCQF TLKPISDSVG VFLRQLQEED RGIDRVAIYS PDGVRVAAST GIDLLLLDDF KLVINDLTYH V RPPKRDLL ...文字列: MAAAAGRSLL LLLSSRGGGG GGAGGCGALT AGCFPGLGVS RHRQQQHHRT VHQRIASWQN LGAVYCSTVV PSDDVTVVYQ NGLPVISVR LPSRRERCQF TLKPISDSVG VFLRQLQEED RGIDRVAIYS PDGVRVAAST GIDLLLLDDF KLVINDLTYH V RPPKRDLL SHENAATLND VKTLVQQLYT TLCIEQHQLN KERELIERLE DLKEQLAPLE KVRIEISRKA EKRTTLVLWG GL AYMATQF GILARLTWWE YSWDIMEPVT YFITYGSAMA MYAYFVMTRQ EYVYPEARDR QYLLFFHKGA KKSRFDLEKY NQL KDAIAQ AEMDLKRLRD PLQVHLPLRQ IGEKD |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | 詳細: unspecified |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 2.2 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 7.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 93255 |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)