+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5zvt | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of RNA polymerase complex and genome within a dsRNA virus provides insights into the mechanisms of transcription and assembly | ||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||
 キーワード キーワード |  VIRUS (ウイルス) / VIRUS (ウイルス) /  icosahedral capsid (カプシド) / symmetry-mismatch / icosahedral capsid (カプシド) / symmetry-mismatch /  genome (ゲノム) / genome (ゲノム) /  RNA-dependent RNA polymerase (RNA依存性RNAポリメラーゼ) RNA-dependent RNA polymerase (RNA依存性RNAポリメラーゼ) | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報host cell surface binding / viral inner capsid / viral outer capsid / permeabilization of host organelle membrane involved in viral entry into host cell / symbiont entry into host cell via permeabilization of inner membrane / 7-methylguanosine mRNA capping /  カプシド / カプシド /  mRNA guanylyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / mRNA guanylyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity /  RNA helicase activity ...host cell surface binding / viral inner capsid / viral outer capsid / permeabilization of host organelle membrane involved in viral entry into host cell / symbiont entry into host cell via permeabilization of inner membrane / 7-methylguanosine mRNA capping / RNA helicase activity ...host cell surface binding / viral inner capsid / viral outer capsid / permeabilization of host organelle membrane involved in viral entry into host cell / symbiont entry into host cell via permeabilization of inner membrane / 7-methylguanosine mRNA capping /  カプシド / カプシド /  mRNA guanylyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / mRNA guanylyltransferase activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity /  RNA helicase activity / RNA helicase activity /  ヘリカーゼ / ヘリカーゼ /  hydrolase activity / GTP binding / hydrolase activity / GTP binding /  ATP binding / ATP binding /  metal ion binding metal ion binding類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |   Grass carp reovirus (ウイルス) Grass carp reovirus (ウイルス) | ||||||||||||||||||
| 手法 |  電子顕微鏡法 / 電子顕微鏡法 /  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.3 Å クライオ電子顕微鏡法 / 解像度: 3.3 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Liu, H. / Fang, Q. / Cheng, L. | ||||||||||||||||||
| 資金援助 |  中国, 5件 中国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2018 ジャーナル: Proc Natl Acad Sci U S A / 年: 2018タイトル: Structure of RNA polymerase complex and genome within a dsRNA virus provides insights into the mechanisms of transcription and assembly. 著者: Xurong Wang / Fuxian Zhang / Rui Su / Xiaowu Li / Wenyuan Chen / Qingxiu Chen / Tao Yang / Jiawei Wang / Hongrong Liu / Qin Fang / Lingpeng Cheng /  要旨: Most double-stranded RNA (dsRNA) viruses transcribe RNA plus strands within a common innermost capsid shell. This process requires coordinated efforts by RNA-dependent RNA polymerase (RdRp) together ...Most double-stranded RNA (dsRNA) viruses transcribe RNA plus strands within a common innermost capsid shell. This process requires coordinated efforts by RNA-dependent RNA polymerase (RdRp) together with other capsid proteins and genomic RNA. Here we report the near-atomic resolution structure of the RdRp protein VP2 in complex with its cofactor protein VP4 and genomic RNA within an aquareovirus capsid using 200-kV cryoelectron microscopy and symmetry-mismatch reconstruction. The structure of these capsid proteins enabled us to observe the elaborate nonicosahedral structure within the double-layered icosahedral capsid. Our structure shows that the RdRp complex is anchored at the inner surface of the capsid shell and interacts with genomic dsRNA and four of the five asymmetrically arranged N termini of the capsid shell proteins under the fivefold axis, implying roles for these N termini in virus assembly. The binding site of the RNA end at VP2 is different from the RNA cap binding site identified in the crystal structure of orthoreovirus RdRp λ3, although the structures of VP2 and λ3 are almost identical. A loop, which was thought to separate the RNA template and transcript, interacts with an apical domain of the capsid shell protein, suggesting a mechanism for regulating RdRp replication and transcription. A conserved nucleoside triphosphate binding site was localized in our RdRp cofactor protein VP4 structure, and interactions between the VP4 and the genomic RNA were identified. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5zvt.cif.gz 5zvt.cif.gz | 1.9 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5zvt.ent.gz pdb5zvt.ent.gz | 1.6 MB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5zvt.json.gz 5zvt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/zv/5zvt https://data.pdbj.org/pub/pdb/validation_reports/zv/5zvt ftp://data.pdbj.org/pub/pdb/validation_reports/zv/5zvt ftp://data.pdbj.org/pub/pdb/validation_reports/zv/5zvt | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
| 2 |
|
| 3 | x 5
|
| 4 | x 6
|
| 5 | 
|
| 対称性 | 点対称性: (シェーンフリース記号 : I (正20面体型対称 : I (正20面体型対称 )) )) |
- 要素
要素
-タンパク質 , 5種, 25分子 lbfdhjnprtBDFHJLNPRTUVWXY
| #1: タンパク質 | 分子量: 29844.648 Da / 分子数: 10 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU63 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU63#3: タンパク質 | 分子量: 64362.086 Da / 分子数: 10 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU67 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU67#4: タンパク質 | 分子量: 44606.535 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU64 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU64#5: タンパク質 | | 分子量: 141512.156 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q9E3W0 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q9E3W0#6: タンパク質 | 分子量: 132203.312 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q9E3V8 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q9E3V8 |
|---|
-タンパク質・ペプチド / 非ポリマー , 2種, 20分子 ACEGIKMOQS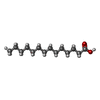

| #2: タンパク質・ペプチド | 分子量: 4302.686 Da / 分子数: 10 / 由来タイプ: 組換発現 / 由来: (組換発現)   Grass carp reovirus (ウイルス) / 発現宿主: Grass carp reovirus (ウイルス) / 発現宿主:   Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU67 Ctenopharyngodon idella (ソウギョ) / 参照: UniProt: Q8JU67#7: 化合物 | ChemComp-MYR /  ミリスチン酸 ミリスチン酸 |
|---|
-実験情報
-実験
| 実験 | 手法:  電子顕微鏡法 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法:  単粒子再構成法 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Grass carp reovirus / タイプ: VIRUS / Entity ID: #1-#6 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:   Grass carp reovirus (ウイルス) Grass carp reovirus (ウイルス) |
| 由来(組換発現) | 生物種:   Ctenopharyngodon idella (ソウギョ) Ctenopharyngodon idella (ソウギョ) |
| ウイルスについての詳細 | 中空か: NO / エンベロープを持つか: NO / 単離: STRAIN / タイプ: VIRION |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色 : NO / 凍結 : NO / 凍結 : YES : YES |
急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TECNAI ARCTICA |
| 電子銃 | 電子線源 : :  FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 200 kV / 照射モード: OTHER |
| 電子レンズ | モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | 電子線照射量: 25 e/Å2 フィルム・検出器のモデル: FEI FALCON II (4k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.13_2998: / 分類: 精密化 |
|---|---|
CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
3次元再構成 | 解像度: 3.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 41000 / 対称性のタイプ: POINT |
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj








