+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24497 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Yeast CTP Synthase (URA8) tetramer bound to ATP/UTP at neutral pH | |||||||||
 マップデータ マップデータ | Yeast CTP Synthase (Ura8) tetramer bound to ATP and UTP at neutral pH. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | glutaminase / amido-ligase / nucleotide metabolism / PROTEIN FIBRIL | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報CTP synthase (glutamine hydrolysing) / CTP synthase activity / cytoophidium / 'de novo' CTP biosynthetic process / pyrimidine nucleobase biosynthetic process / glutamine metabolic process / ATP binding / identical protein binding / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.8 Å | |||||||||
 データ登録者 データ登録者 | Hansen JM / Lynch EM | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2021 ジャーナル: Elife / 年: 2021タイトル: Cryo-EM structures of CTP synthase filaments reveal mechanism of pH-sensitive assembly during budding yeast starvation. 著者: Jesse M Hansen / Avital Horowitz / Eric M Lynch / Daniel P Farrell / Joel Quispe / Frank DiMaio / Justin M Kollman /  要旨: Many metabolic enzymes self-assemble into micron-scale filaments to organize and regulate metabolism. The appearance of these assemblies often coincides with large metabolic changes as in ...Many metabolic enzymes self-assemble into micron-scale filaments to organize and regulate metabolism. The appearance of these assemblies often coincides with large metabolic changes as in development, cancer, and stress. Yeast undergo cytoplasmic acidification upon starvation, triggering the assembly of many metabolic enzymes into filaments. However, it is unclear how these filaments assemble at the molecular level and what their role is in the yeast starvation response. CTP Synthase (CTPS) assembles into metabolic filaments across many species. Here, we characterize in vitro polymerization and investigate in vivo consequences of CTPS assembly in yeast. Cryo-EM structures reveal a pH-sensitive assembly mechanism and highly ordered filament bundles that stabilize an inactive state of the enzyme, features unique to yeast CTPS. Disruption of filaments in cells with non-assembly or pH-insensitive mutations decreases growth rate, reflecting the importance of regulated CTPS filament assembly in homeotstasis. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24497.map.gz emd_24497.map.gz | 4.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24497-v30.xml emd-24497-v30.xml emd-24497.xml emd-24497.xml | 12.9 KB 12.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_24497.png emd_24497.png | 161.9 KB | ||
| Filedesc metadata |  emd-24497.cif.gz emd-24497.cif.gz | 6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24497 http://ftp.pdbj.org/pub/emdb/structures/EMD-24497 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24497 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24497 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_24497_validation.pdf.gz emd_24497_validation.pdf.gz | 364.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_24497_full_validation.pdf.gz emd_24497_full_validation.pdf.gz | 363.9 KB | 表示 | |
| XML形式データ |  emd_24497_validation.xml.gz emd_24497_validation.xml.gz | 6.6 KB | 表示 | |
| CIF形式データ |  emd_24497_validation.cif.gz emd_24497_validation.cif.gz | 7.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24497 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24497 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24497 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24497 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7rkhMC  7rl0C  7rl5C  7rmcC  7rmfC  7rmkC  7rmoC  7rmvC  7rnlC  7rnrC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24497.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24497.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Yeast CTP Synthase (Ura8) tetramer bound to ATP and UTP at neutral pH. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.05 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Yeast CTP Synthase (URA8) tetramer bound to ATP/UTP at neutral pH
| 全体 | 名称: Yeast CTP Synthase (URA8) tetramer bound to ATP/UTP at neutral pH |
|---|---|
| 要素 |
|
-超分子 #1: Yeast CTP Synthase (URA8) tetramer bound to ATP/UTP at neutral pH
| 超分子 | 名称: Yeast CTP Synthase (URA8) tetramer bound to ATP/UTP at neutral pH タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 256 kDa/nm |
-分子 #1: CTP synthase
| 分子 | 名称: CTP synthase / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO / EC番号: CTP synthase (glutamine hydrolysing) |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 62.439168 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MKYVVVSGGV ISGIGKGVLA SSTGMLLKTL GLKVTSIKID PYMNIDAGTM SPLEHGECFV LDDGGETDLD LGNYERYLGI TLSRDHNIT TGKIYSHVIS RERRGDYLGK TVQIVPHLTN AIQDWIQRVS KIPVDDTGLE PDVCIIELGG TVGDIESAPF V EALRQFQF ...文字列: MKYVVVSGGV ISGIGKGVLA SSTGMLLKTL GLKVTSIKID PYMNIDAGTM SPLEHGECFV LDDGGETDLD LGNYERYLGI TLSRDHNIT TGKIYSHVIS RERRGDYLGK TVQIVPHLTN AIQDWIQRVS KIPVDDTGLE PDVCIIELGG TVGDIESAPF V EALRQFQF EVGRENFALI HVSLVPVIHG EQKTKPTQAA IKDLRSLGLI PDMIACRCSE ELNRSTIDKI AMFCHVGPEQ VV NVHDVNS TYHVPLLLLK QHMIDYLHSR LKLGEVPLTL EDKERGSQLL TNWENMTKNL DDSDDVVKIA LVGKYTNLKD SYL SVTKSL EHASMKCRRQ LEILWVEASN LEPETQEVDK NKFHDSWNKL SSADGILVPG GFGTRGIEGM ILAAKWARES GVPF LGVCL GLQVAAIEFA RNVIGRPNSS STEFLDETLL APEDQVVITM RLGLRPTIFQ PNSEWSNIRK LYGEVNEVHE RHRHR YEIN PKIVNDMESR GFIFVGKDET GQRCEIFELK GHPYYVGTQY HPEYTSKVLE PSRPFWGLVA AASGTLGEVI KDINL UniProtKB: CTP synthase |
-分子 #2: URIDINE 5'-TRIPHOSPHATE
| 分子 | 名称: URIDINE 5'-TRIPHOSPHATE / タイプ: ligand / ID: 2 / コピー数: 4 / 式: UTP |
|---|---|
| 分子量 | 理論値: 484.141 Da |
| Chemical component information | 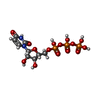 ChemComp-UTP: |
-分子 #3: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 3 / コピー数: 4 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-分子 #4: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 4 / コピー数: 8 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | モデル: C-flat / 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 90.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 5.5 µm / 最小 デフォーカス(公称値): 1.2 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: D2 (2回x2回 2面回転対称) 解像度のタイプ: BY AUTHOR / 解像度: 2.8 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: RELION / 詳細: FSCref0.5 (Phenix Density modification) / 使用した粒子像数: 76963 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 3.1) |
 ムービー
ムービー コントローラー
コントローラー





















