+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM map of the WT KdpFABC complex in the E2-P conformation, stabilised with the inhibitor orthovanadate | ||||||||||||||||||
 マップデータ マップデータ | Cryo-EM map of the WT KdpFABC complex, in the E2-P tight conformation, at 7.4 A resolution, sharpened at -195 A2. Data obtained in the presence of 2mM orthovanadate and 1mM KCl. | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード |  P-type ATPase / superfamily of K+ transporters (SKT) / potassium uptake system / P-type ATPase / superfamily of K+ transporters (SKT) / potassium uptake system /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | ||||||||||||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | ||||||||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 7.4 Å クライオ電子顕微鏡法 / 解像度: 7.4 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Hielkema L / Stock C / Silberberg JM / Corey RA / Wunnicke D / Stansfeld PJ / Haenelt I / Paulino C | ||||||||||||||||||
| 資金援助 |  英国, 5件 英国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2022 ジャーナル: Elife / 年: 2022タイトル: Inhibited KdpFABC transitions into an E1 off-cycle state. 著者: Jakob M Silberberg / Charlott Stock / Lisa Hielkema / Robin A Corey / Jan Rheinberger / Dorith Wunnicke / Victor R A Dubach / Phillip J Stansfeld / Inga Hänelt / Cristina Paulino /    要旨: KdpFABC is a high-affinity prokaryotic K uptake system that forms a functional chimera between a channel-like subunit (KdpA) and a P-type ATPase (KdpB). At high K levels, KdpFABC needs to be ...KdpFABC is a high-affinity prokaryotic K uptake system that forms a functional chimera between a channel-like subunit (KdpA) and a P-type ATPase (KdpB). At high K levels, KdpFABC needs to be inhibited to prevent excessive K accumulation to the point of toxicity. This is achieved by a phosphorylation of the serine residue in the TGES motif in the A domain of the pump subunit KdpB (KdpB). Here, we explore the structural basis of inhibition by KdpB phosphorylation by determining the conformational landscape of KdpFABC under inhibiting and non-inhibiting conditions. Under turnover conditions, we identified a new inhibited KdpFABC state that we termed E1P tight, which is not part of the canonical Post-Albers transport cycle of P-type ATPases. It likely represents the biochemically described stalled E1P state adopted by KdpFABC upon KdpB phosphorylation. The E1P tight state exhibits a compact fold of the three cytoplasmic domains and is likely adopted when the transition from high-energy E1P states to E2P states is unsuccessful. This study represents a structural characterization of a biologically relevant off-cycle state in the P-type ATPase family and supports the emerging discussion of P-type ATPase regulation by such states. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14347.map.gz emd_14347.map.gz | 49.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14347-v30.xml emd-14347-v30.xml emd-14347.xml emd-14347.xml | 22.7 KB 22.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
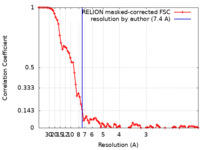
| FSC (解像度算出) |  emd_14347_fsc.xml emd_14347_fsc.xml | 8.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14347.png emd_14347.png | 58.5 KB | ||
| マスクデータ |  emd_14347_msk_1.map emd_14347_msk_1.map | 52.7 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-14347.cif.gz emd-14347.cif.gz | 6.6 KB | ||
| その他 |  emd_14347_half_map_1.map.gz emd_14347_half_map_1.map.gz emd_14347_half_map_2.map.gz emd_14347_half_map_2.map.gz | 40.9 MB 40.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14347 http://ftp.pdbj.org/pub/emdb/structures/EMD-14347 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14347 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14347 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14347.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14347.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM map of the WT KdpFABC complex, in the E2-P tight conformation, at 7.4 A resolution, sharpened at -195 A2. Data obtained in the presence of 2mM orthovanadate and 1mM KCl. | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.012 Å | ||||||||||||||||||||||||||||||||||||
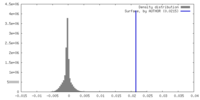
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14347_msk_1.map emd_14347_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
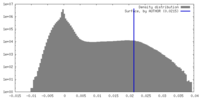
| 密度ヒストグラム |
-ハーフマップ: Half map 1 used during refinement and for...
| ファイル | emd_14347_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 used during refinement and for FSC gold-standard resolution calculation of the WT KdpFABC complex in the presence of orthovanadate. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
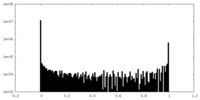
| 密度ヒストグラム |
-ハーフマップ: Half map 2 used during refinement and for...
| ファイル | emd_14347_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 used during refinement and for FSC gold-standard resolution calculation of the WT KdpFABC complex in the presence of orthovanadate. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
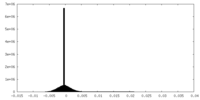
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : KdpFABC
| 全体 | 名称: KdpFABC |
|---|---|
| 要素 |
|
-超分子 #1: KdpFABC
| 超分子 | 名称: KdpFABC / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 157 KDa |
-分子 #1: Potassium-transporting ATPase potassium-binding subunit
| 分子 | 名称: Potassium-transporting ATPase potassium-binding subunit タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MAAQGFLLIA TFLLVLMVLA RPLGSGLARL INDIPLPGTT GVERVLFRAL GVSDREMNWK QYLCAILGL NMLGLAVLFF MLLGQHYLPL NPQQLPGLSW DLALNTAVSF VTNTNWQSYS G ETTLSYFS QMAGLTVQNF LSAASGIAVI FALIRAFTRQ SMSTLGNAWV ...文字列: MAAQGFLLIA TFLLVLMVLA RPLGSGLARL INDIPLPGTT GVERVLFRAL GVSDREMNWK QYLCAILGL NMLGLAVLFF MLLGQHYLPL NPQQLPGLSW DLALNTAVSF VTNTNWQSYS G ETTLSYFS QMAGLTVQNF LSAASGIAVI FALIRAFTRQ SMSTLGNAWV DLLRITLWVL VP VALLIAL FFIQQGALQN FLPYQAVNTV EGAQQLLPMG PVASQEAIKM LGTNGGGFFN ANS SHPFEN PTALTNFVQM LAIFLIPTAL CFAFGEVMGD RRQGRMLLWA MSVIFVICVG VVMW AEVQG NPHLLALGTD SSINMEGKES RFGVLVSSLF AVVTTAASCG AVIAMHDSFT ALGGM VPMW LMQIGEVVFG GVGSGLYGMM LFVLLAVFIA GLMIGRTPEY LGKKIDVREM KLTALA ILV TPTLVLMGAA LAMMTDAGRS AMLNPGPHGF SEVLYAVSSA ANNNGSAFAG LSANSPF WN CLLAFCMFVG RFGVIIPVMA IAGSLVSKKS QAASSGTLPT HGPLFVGLLI GTVLLVGA L TFIPALALGP VAEYLS |
-分子 #2: Potassium-transporting ATPase KdpC subunit
| 分子 | 名称: Potassium-transporting ATPase KdpC subunit / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSGLRPALST FIFLLLITGG VYPLLTTVLG QWWFPWQANG SLIREGDTVR GSALIGQNFT GNGYFHGRP SATAEMPYNP QASGGSNLAV SNPELDKLIA ARVAALRAAN PDASASVPVE L VTASASGL DNNITPQAAA WQIPRVAKAR NLSVEQLTQL IAKYSQQPLV ...文字列: MSGLRPALST FIFLLLITGG VYPLLTTVLG QWWFPWQANG SLIREGDTVR GSALIGQNFT GNGYFHGRP SATAEMPYNP QASGGSNLAV SNPELDKLIA ARVAALRAAN PDASASVPVE L VTASASGL DNNITPQAAA WQIPRVAKAR NLSVEQLTQL IAKYSQQPLV KYIGQPVVNI VE LNLALDK LDE |
-分子 #3: Potassium-transporting ATPase KdpF subunit
| 分子 | 名称: Potassium-transporting ATPase KdpF subunit / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSAGVITGVL LVFLLLGYLV YALINAE |
-分子 #4: Potassium-transporting ATPase ATP-binding subunit
| 分子 | 名称: Potassium-transporting ATPase ATP-binding subunit / タイプ: protein_or_peptide / ID: 4 / 光学異性体: LEVO / EC番号: P-type K+ transporter |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSRKQLALFE PTLVVQALKE AVKKLNPQAQ WRNPVMFIVW IGSLLTTCIS IAMASGAMPG NALFSAAIS GWLWITVLFA NFAEALAEGR SKAQANSLKG VKKTAFARKL REPKYGAAAD K VPADQLRK GDIVLVEAGD IIPCDGEVIE GGASVDESAI TGE(SEP) ...文字列: MSRKQLALFE PTLVVQALKE AVKKLNPQAQ WRNPVMFIVW IGSLLTTCIS IAMASGAMPG NALFSAAIS GWLWITVLFA NFAEALAEGR SKAQANSLKG VKKTAFARKL REPKYGAAAD K VPADQLRK GDIVLVEAGD IIPCDGEVIE GGASVDESAI TGE(SEP)APVIRE SGGDFASVTG GT RILSDWL VIECSVNPGE TFLDRMIAMV EGAQRRKTPN EIALTILLIA LTIVFLLATA TLW PFSAWG GNAVSVTVLV ALLVCLIPTT IGGLLSAIGV AGMSRMLGAN VIATSGRAVE AAGD VDVLL LDKTGTITLG NRQASEFIPA QGVDEKTLAD AAQLASLADE TPEGRSIVIL AKQRF NLRE RDVQSLHATF VPFTAQSRMS GINIDNRMIR KGSVDAIRRH VEANGGHFPT DVDQKV DQV ARQGATPLVV VEGSRVLGVI ALKDIVKGGI KERFAQLRKM GIKTVMITGD NRLTAAA IA AEAGVDDFLA EATPEAKLAL IRQYQAEGRL VAMTGDGTND APALAQADVA VAMNSGTQ A AKEAGNMVDL DSNPTKLIEV VHIGKQMLMT RGSLTTFSIA NDVAKYFAII PAAFAATYP QLNALNIMCL HSPDSAILSA VIFNALIIVF LIPLALKGVS YKPLTASAML RRNLWIYGLG GLLVPFIGI KVIDLLLTVC GLV |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4.0 mg/mL |
|---|---|
| 緩衝液 | pH: 8 詳細: 10 mM Tris-HCl pH 8, 10 mM MgCl2, 10 mM NaCl and 0.0125% DDM |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 20 sec. / 詳細: at 5 mA |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 293 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 最大 デフォーカス(補正後): 2.0 µm / 最小 デフォーカス(補正後): 0.5 µm / 倍率(補正後): 49407 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 49407 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 49407 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 温度 | 最低: 90.0 K / 最高: 105.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3838 pixel / デジタル化 - サイズ - 縦: 3710 pixel / デジタル化 - 画像ごとのフレーム数: 1-60 / 撮影したグリッド数: 2 / 実像数: 2487 / 平均露光時間: 9.0 sec. / 平均電子線量: 52.0 e/Å2 |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|
 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)